

高等学校化学学报 ›› 2021, Vol. 42 ›› Issue (11): 3277.doi: 10.7503/cjcu20210465
收稿日期:2021-07-01
出版日期:2021-11-10
发布日期:2021-09-10
通讯作者:
刘巧玲
E-mail:qlliu@hnu.edu.cn
基金资助:
LIU Xuejiao, YANG Fan, LIU Shuang, ZHANG Chunjuan, LIU Qiaoling( )
)
Received:2021-07-01
Online:2021-11-10
Published:2021-09-10
Contact:
LIU Qiaoling
E-mail:qlliu@hnu.edu.cn
Supported by:摘要:
膜蛋白在细胞生命活动中发挥着重要作用, 研究并调控细胞膜蛋白的结构和功能有助于阐明生命活动的基本规律, 为新型药物研发和高效疾病诊治提供研究基础. 核酸适体是一类特殊的寡核苷酸序列, 因具有特异性识别靶标的能力而被广泛用于生物传感领域. 将核酸适体与DNA纳米技术相结合, 利用DNA分子可程序化设计、 可功能化修饰等优势, 发展核酸适体靶向的膜蛋白识别与功能调控方法可为研究膜蛋白相互作用提供有力工具. 本文介绍了基于核酸适体靶向识别的DNA纳米技术在膜蛋白识别及细胞功能调控中的研究进展, 并对核酸适体靶向的膜蛋白识别及功能调控领域面临的挑战进行了分析, 对其应用前景进行了展望.
中图分类号:
TrendMD:
刘学娇, 杨帆, 刘爽, 张春娟, 刘巧玲. 核酸适体靶向的膜蛋白识别与功能调控研究进展. 高等学校化学学报, 2021, 42(11): 3277.
LIU Xuejiao, YANG Fan, LIU Shuang, ZHANG Chunjuan, LIU Qiaoling. Progress in Aptamer-targeted Membrane Protein Recognition and Functional Regulation. Chem. J. Chinese Universities, 2021, 42(11): 3277.
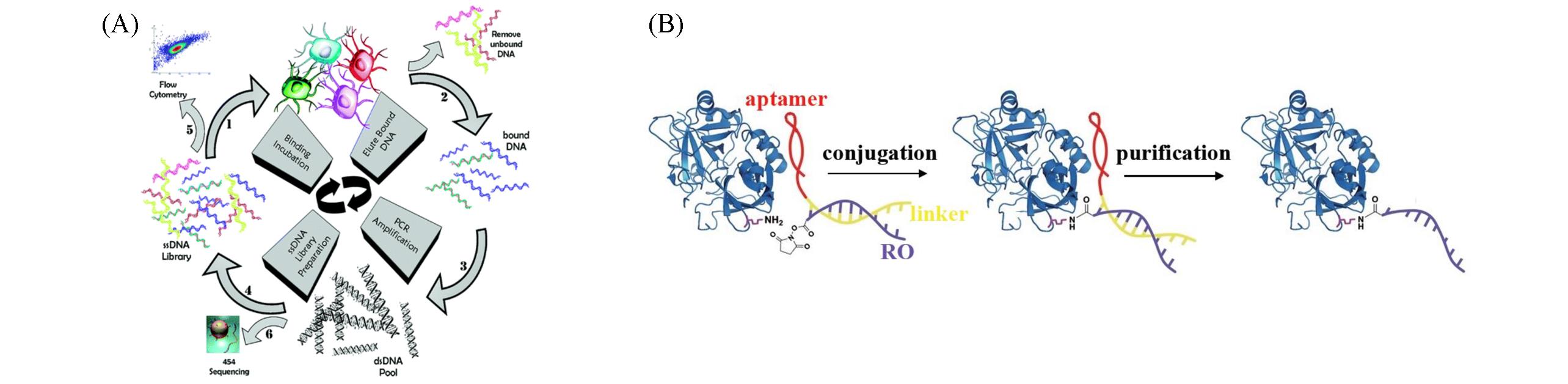
Fig.1 Scheme of aptamer screening utilizing cell?SELEX(A)[16] and membrane protein recognition and functional modification mediated by aptamer(B)[24](A) Copyright 2011, American Chemical Society; (B) Copyright 2017, Wiley?VCH.
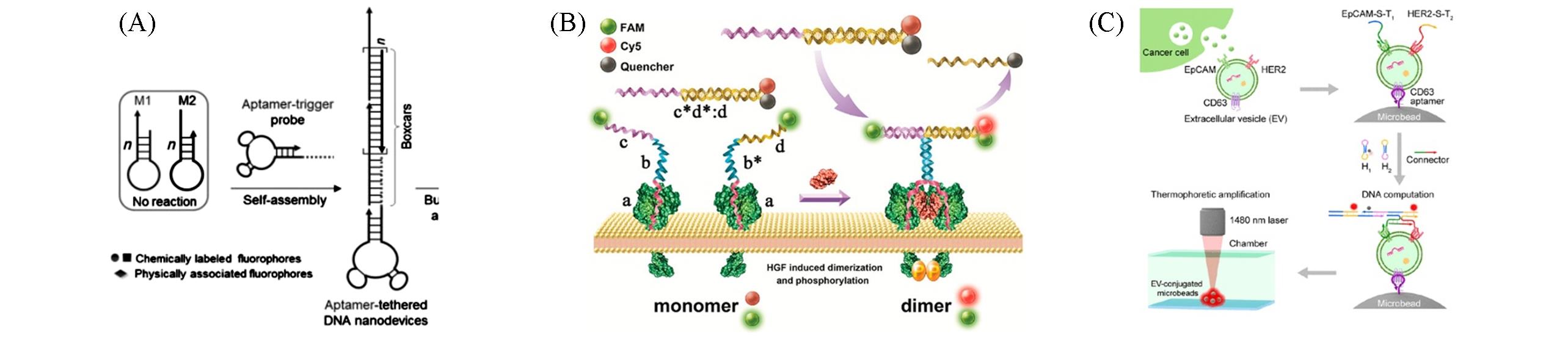
Fig.2 HCR reaction based on aptamer targeting used for membrane protein recognition and signal amplification(A)[36], DNA strand displacement reaction based on aptamer targeting used for membrane protein recognition and signal amplification(B)[39] and DNA logical computation based on aptamer targeting used for membrane protein precise detection and signal amplification(C)[42](A) Copyright 2013, Wiley?VCH; (B) Copyright 2018, American Chemical Society; (C) Copyright 2021, American Chemical Society.
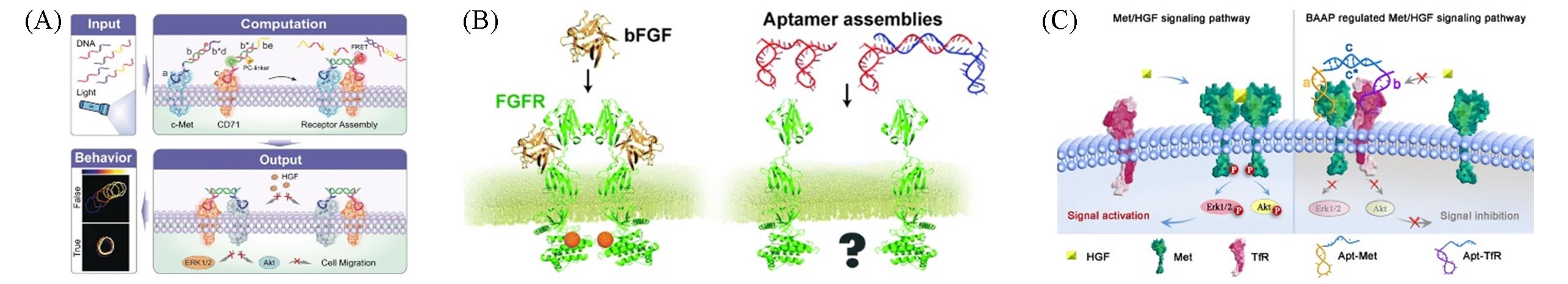
Fig.3 Analysis and regulation of membrane protein based on aptamer targeting(A)[56], regulation of dimerization of membrane receptor proteins based on aptamer targeting(B)[62] and regulation of cell proliferation and migration based on aptamer targeting(C)[64](A) Copyright 2019, Wiley?VCH; (B) Copyright 2019, the Royal Society of Chemistry; (C) Copyright 2019, American Chemical Society.
| 1 | Wang W. J., Qiao Y. H., Li Z. J., Trends Pharmacol.Sci., 2018, 39(4), 367―386 |
| 2 | Yang Y., Song H. P., He D., Zhang S., Dai S. Z., Xie X., Lin S. X., Hao Z. Y., Zheng H. T., Chen P. R., Nat. Protoc., 2017, 12(10), 2147―2168 |
| 3 | Wang J., Cheng B., Li J., Zhang Z. Y., Hong W. Y., Chen X., Chen P. R., Angew Chem. Int. Ed., 2015, 54(18), 5364―5368 |
| 4 | Li J., Yu J. T., Zhao J. Y., Wang J., Zheng S. Q., Lin S. X., Chen L., Yang M. Y., Jia S., Zhang X. Y., Chen P. R., Nat. Chem., 2014, 6(4), 352―361 |
| 5 | Spencer D., Wandless T., Schreiber S., Crabtree G., Science, 1993, 262(5136), 1019―1024 |
| 6 | Miyamoto T., DeRose R., Suarez A., Ueno T., Chen M., Sun T. P., Wolfgang M. J., Mukherjee C., Meyers D., Inoue T., Nat. Chem. Biol., 2012, 8(5), 465―470 |
| 7 | Zhang Y., Lai B. S., Juhas M., Molecules, 2019, 24(5), 941 |
| 8 | Ellington A. D., Szostak J. W., Nature, 1990, 346(6287), 818―822 |
| 9 | Tuerk C., Gold L., Science, 1990, 249(4968), 505―510 |
| 10 | Dunn M. R., Jimenez R. M., Chaput J. C., Nat. Rev. Chem., 2017, 1(10), 0076 |
| 11 | Zhu G. Z., Chen X. Y., Adv. Drug. Deliv. Rev., 2018, 134, 65―78 |
| 12 | Wilson D. S., Szostak J. W., Annu. Rev. Biochem., 1999, 68, 611―647 |
| 13 | Nutiu R., Li Y. F., J. Am. Chem. Soc., 2003, 125(16), 4771―4778 |
| 14 | Nutiu R., Li Y. F., Chemistry, 2004, 10(8), 1868―1876 |
| 15 | Meng H. M., Liu H., Kuai H. L., Peng R. Z., Mo L. T., Zhang X. B., Chem. Soc. Rev., 2016, 45(9), 2583―2602 |
| 16 | Bayrac A. T., Sefah K., Parekh P., Bayrac C., Gulbakan B., Oktem H. V., Tan W. H., ACS Chem. Neurosci., 2011, 2(3), 175―181 |
| 17 | Xu J. H., Teng I. T., Zhang L. Q., Delgado S., Champanhac C., Cansiz S., Wu C. C., Shan H., Tan W. H., PLoS One, 2015, 10(5), e0125863 |
| 18 | Wu X. Q., Liu H. L., Han D. M., Peng B., Zhang H., Zhang L., Li J. L., Liu J., Cui C., Fang S. B., Li M., Ye M., Tan W., J. Am. Chem. Soc., 2019, 141(27), 10760―10769 |
| 19 | Jia W. T., Ren C. P., Wang L., Zhu B., Jia W., Gao M. H., Zeng F., Zeng L., Xia X. M., Zhang X. B., Fu T., Li S. S., Du C., Jiang X. J., Chen Y. X., Tan W. H., Zhao Z. L., Liu W. D., Oncotarget, 2016, 7(34), 55328―55342 |
| 20 | Shangguang D. H., Cao Z. H., Meng L., Mallikaratchy P., Sefah K., Wang H., Li Y., Tan W. H., J. Proteome Res., 2008, 7(5), 2133―2139 |
| 21 | Shangguan D. H., Tang Z. W., Mallikaratchy P., Xiao Z. Y., Tan W. H., ChemBioChem, 2007, 8(6), 603―606 |
| 22 | O’Donoghue M. B., Shi X. L., Fang X. H., Tan W. H., Anal. Bioanal. Chem., 2012, 402(10), 3205―3209 |
| 23 | Lee H. J., Canny M. D., Erkenez A. D., Krilleke D., Ng Y. S., Shima D., Pardi A., Jucker F., Proc. Natl. Acad. Sci. USA, 2005, 102(52), 18902―18907 |
| 24 | Cui C., Zhang H., Wang R. W., Cansiz S., Pan X. S., Wang S., Hou W. J., Li L., Chen M. W., Liu Y., Chen X. G., Liu Q. L., Tan W. H., Angew Chem. Int. Ed., 2017, 56(39), 12116―12119 |
| 25 | Yang J. W., Wang C. Y., Luo L., Guo L., Xie J. W., Chinese J. Anal. Chem., 2020, 48(11), 1439―1447(杨捷威, 王晨钰, 罗黎, 郭磊, 谢剑炜. 分析化学, 2020, 48(11), 1439―1447) |
| 26 | Liu J., Cui M. R., Niu L., Zhou H., Zhang S. S., Chem.⁃Eur. J., 2016, 22(50), 18001―18008 |
| 27 | Yu T. X., Zhang H., Huang Z. L., Luo Z. H., Huang N. S., Ding S. J., Feng W. L., Electroanalysis, 2017, 29(3), 828―834 |
| 28 | Khoshfetrat S. M., Mehrgardi M. A., Bioelectrochemistry, 2017, 114, 24―32 |
| 29 | Miao X. M., Li Z. B., Zhu A. H., Feng Z. Z., Tian J., Peng X., Biosens. Bioelectron., 2016, 83, 39―44 |
| 30 | Mironov G. G., Bouzekri A., Watson J., Loboda O., Ornatsky O., Berezovski M. V., Anal. Bioanal. Chem., 2018, 410(13), 3047―3051 |
| 31 | Gai P. P., Ji Y. S., Wang W. J., Song R. B., Zhu C., Chen Y., Zhang J. R., Zhu J. J., Nano Energy, 2016, 19, 541―549 |
| 32 | Ke Y. G., Castro C., Choi J. H., Annu. Rev. Biomed. Eng., 2018, 20, 375―401 |
| 33 | Bi S., Yue S. Z., Zhang S. S., Chem. Soc. Rev., 2017, 46(14), 4281―4298 |
| 34 | Wang L. P., Li W., Sun J., Zhang S. Y., Yang S., Li J. Y., Li J., Yang H. H., Anal. Chem., 2018, 90(24), 14433―14438 |
| 35 | Yang T. T., Xu L. L., Liu S. C., Shen Y. F., Huang L. Z., Zhang L. T., Ding S. J., Cheng W., Microchim. Acta, 2019, 186(7), 439 |
| 36 | Zhu G. Z., Zhang S. F., Song E. Q., Zheng J., Hu R., Fang X. H., Tan W. H., Angew. Chem. Int. Ed., 2013, 52(21), 5490―5496 |
| 37 | Zhang D. Y., Winfree E., J. Am. Chem. Soc., 2009, 131(47), 17303―17314 |
| 38 | Wei X. J., Li M. M., Hu P., Yang B., Sensor Actuat. B: Chem., 2017, 241, 422―429 |
| 39 | Liang H., Chen S., Li P. P., Wang L. P., Li J. J., Li J., Yang H. H., Tan W. H., J. Am. Chem. Soc., 2018, 140(12), 4186―4190 |
| 40 | Yang S., Li J. Y., Cui Y. J., Teng Y., Chin. J. Biotech., 2021, 37(4), 1120―1130(杨姗, 李金玉, 崔玉军, 滕越. 生物工程学报, 2021, 37(4), 1120―1130) |
| 41 | Zhang J. H., Qiu Z. Y., Fan J. H., He F., Kang W. Y., Yang S. H., Wang H. H., Huang J., Nie Z., Angew. Chem. Int. Ed., 2021, 60(12), 6733―6743 |
| 42 | Li Y. K., Deng J. Q., Han Z. W., Liu C., Tian F., Xu R., Han D., Zhang S. H., Sun J. S., J. Am. Chem. Soc., 2021, 143(3), 1290―1295 |
| 43 | Sako Y., Minoguchi S., Yanagida T., Nat. Cell Biol., 2000, 2(3), 168―172 |
| 44 | Ueki R., Atsuta S., Yeki A., Sando S., J. Am. Chem. Soc., 2017, 139(19), 6554―6557 |
| 45 | Li J. Y., Wang L. P., Tian J. M., Zhou Z. L., Li J., Yang H. H., Chem. Soc. Rev., 2020, 49, 1545―1568 |
| 46 | Li J. Y., Chen C., Li J., Yang H. H., Chem. J. Chinese Universities, 2020, 41(5), 892―900(李婧影, 陈琛, 李娟, 杨黄浩. 高等学校化学学报, 2020, 41(5), 892―900) |
| 47 | Liu J. B., Wang L. H., Zuo X. L., Prog. Chem., 2019, 31(8), 1067―1074(刘江波, 王丽华, 左小磊. 化学进展, 2019, 31(8), 1067―1074) |
| 48 | Chen Y., Munteanu Dr. A. C., Huang Dr. Y. F., Phillips Dr. J., Zhu Z., Mavros M., Tan W. H., Chem. Eur. J., 2009, 15(21), 5327―5336 |
| 49 | Prescher J. A., Bertozzi C. R., Nat. Chem. Biol., 2005, 1(1), 13―21 |
| 50 | Chen X. G., Qiu L. P., Cai R., Cui C., Li L., Jiang J. H., Tan W. H., ACS Appl. Mater. Interfaces, 2020, 12(34), 37845―37850 |
| 51 | Ambrosetti E., Bernardinelli G., Hoffecker L., Hartmanis L., Kiriako G., Marco A. D., Sandberg R., Högberg B., Teixeira A. I., Nat. Nanotechnol., 2021, 16(1), 85―95 |
| 52 | Li M., Yu Y., J. Cell Sci., 2021, 134(4), jcs249318 |
| 53 | Hartman N. C., Groves J. T., Curr. Opin. Cell Biol., 2011, 23(4), 370―376 |
| 54 | McNamara J. O., Kolonias D., Pastor F., Mittler R. S., Chen L. P., Giangrande P. H., Sullenger B., Gilboa E., J. Clin. Invest., 2008, 118(1), 376―386 |
| 55 | Li H., Wang M., Shi T. H., Yang S.H., Zhang J. H., Wang H. H., Nie Z., Angew. Chem. Int. Ed., 2018, 57(32), 10226―10230 |
| 56 | Chen S., Xu Z. F., Yang W., Lin X. H., Li J. Y., Li J., Yang H. H., Angew. Chem. Int. Ed., 2019, 58(50), 18186―18190 |
| 57 | Snider J., Stagljar I., Cold Spring Harb. Protoc., 2016, 2016(1), doi: 10.1101/pdb.top077560 |
| 58 | Ma W. Y., Liu S. B., Chen P., Chem. J. Chinese Universities, 2020, 41(12), 2658―2666(马维绎, 刘士博, 陈鹏. 高等学校化学学报, 2020, 41(12), 2658―2666) |
| 59 | Fan J. H., Wang H. H., Xie S. Y., Wang M., Nie Z., ChemBioChem, 2020, 21(3), 282―293 |
| 60 | Ueki R., Ueki A., Kanda N., Sando S., Angew Chem. Int. Ed., 2016, 55(2), 579―582 |
| 61 | Ueki R., Uchida S., Kanda N., Yamada N., Ueki A., Akiyama M., Toh K., Cabral H., Sando S., Sci. Adv., 2020, 6(14), eaay2801 |
| 62 | Ueki R., Atsuta S., Ueki A., Hoshiyama J., Li J. Y., Hayashi Y., Sando S., Chem. Commun., 2019, 55(18), 2672―2675 |
| 63 | Trusolino L., Bertotti A., Comoglio P. M., Nat. Rev. Mol., Cell Biol., 2010, 11(12), 834―848 |
| 64 | Wang L. P., Liang H., Sun J., Liu Y. C., Li J. Y., Li J. Y., Li J., Yang H. H., J. Am. Chem. Soc., 2019, 141(32), 12673―12681 |
| 65 | Chen S., Li J. Y., Liang H., Lin H. X., Li J., Yang H. H., Chem. Eur. J., 2018, 24(60), 15988―15992 |
| 66 | Wang M., He F., Li H., Yang S. H., Zhang J. H., Ghosh P., Wang H. H., Nie Z., Nano Lett., 2019, 1(4), 2603―2613 |
| 67 | Ramaswamy V., Monsalve A., Sautina L., Segal M. S., Dobson J., Allen J. B., Nucleic Acid Ther., 2015, 25(5), 227―234 |
| 68 | Baig M. M. F.A., Zhang Q. W., Younis M. R., Xia X. H., Nano Lett., 2019, 19(10), 7503―7513 |
| [1] | 王隆杰, 范鸿川, 秦渝, 曹秋娥, 郑立炎. 金属有机框架材料在分离分析领域的研究进展[J]. 高等学校化学学报, 2021, 42(4): 1167. |
| [2] | 刘珂, 靳宇, 梁建功, 吴园. 化学修饰提高核酸适体结合亲和力的研究进展[J]. 高等学校化学学报, 2021, 42(11): 3477. |
| [3] | 张晓荣, 陈岚岚, 胡善文. 基于分子识别的细菌检测研究进展[J]. 高等学校化学学报, 2021, 42(11): 3468. |
| [4] | 彭海月, 汪婷, 李国瑞, 黄静. 黑色素的合成及小分子对其功能的调控[J]. 高等学校化学学报, 2021, 42(11): 3357. |
| [5] | 吉采灵, 程兴, 谈洁, 袁荃. 功能化核酸适体的筛选及分子识别应用[J]. 高等学校化学学报, 2021, 42(11): 3457. |
| [6] | 解忱, 陈娜, 杨雁冰, 袁荃. 核酸适体功能化的二维材料场效应晶体管传感器研究进展[J]. 高等学校化学学报, 2021, 42(11): 3406. |
| [7] | 赵卓, 王雪强. 核酸适体偶联药物的生物偶联构建技术与应用[J]. 高等学校化学学报, 2021, 42(11): 3367. |
| [8] | 刘园, 邓瑾琦, 赵帅, 田飞, 李轶, 孙佳姝, 刘超. 基于分子识别的免疫层析技术用于新冠肺炎感染的快速诊断[J]. 高等学校化学学报, 2021, 42(11): 3390. |
| [9] | 林宁钦, 姚克, 陈祥军. 晶状体蛋白识别互作与白内障的研究进展[J]. 高等学校化学学报, 2021, 42(11): 3379. |
| [10] | 黄玲, 庄梓健, 李翔, 石沐玲, 刘高强. 基于核酸适体的外泌体分子识别研究进展[J]. 高等学校化学学报, 2021, 42(11): 3493. |
| [11] | 严磊, 毛秀海, 左小磊. 框架核酸辅助的仿生膜构建[J]. 高等学校化学学报, 2020, 41(7): 1415. |
| [12] | 黄云帅, 杨霓, 吴泽宏, 吴思. 利用光响应钌配合物的动态配位键调控表面功能[J]. 高等学校化学学报, 2020, 41(6): 1174. |
| [13] | 彭与煜,王煜,于鑫垚,曾巨澜,肖忠良,曹忠. 基于单(6-巯基-6-去氧)-β-环糊精修饰金电极对L-半胱氨酸的快速灵敏检测[J]. 高等学校化学学报, 2020, 41(2): 268. |
| [14] | 董倩, 李兆倩, 彭天欢, 陈卓, 谭蔚泓. 核酸适体在癌症诊疗中的研究进展[J]. 高等学校化学学报, 2020, 41(12): 2648. |
| [15] | 马玉聪, 樊保民, 郝华, 吕金玉, 冯云皓, 杨彪. 十八胺基分子组装体在碳钢表面的作用机理与模拟[J]. 高等学校化学学报, 2019, 40(1): 96. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||