

高等学校化学学报 ›› 2021, Vol. 42 ›› Issue (11): 3477.doi: 10.7503/cjcu20210292
收稿日期:2021-04-28
出版日期:2021-11-10
发布日期:2021-06-01
通讯作者:
吴园
E-mail:yuanwu@mail.hzau.edu.cn
基金资助:
LIU Ke, JIN Yu, LIANG Jiangong, WU Yuan( )
)
Received:2021-04-28
Online:2021-11-10
Published:2021-06-01
Contact:
WU Yuan
E-mail:yuanwu@mail.hzau.edu.cn
Supported by:摘要:
核酸适体(Aptamer)是通过体外筛选得到的短单链DNA或RNA寡核苷酸, 具有与抗体相当或更优异的特异性及亲和力, 且具有靶标范围广、 易制备和灵活可控修饰、 免疫原性低、 批次差异性小以及易于运输保存等优势, 为食品、 环境和生物医学等领域提供了全新的分子识别工具, 获得了研究者的广泛关注. 但是目前其商业应用的数量仍有限. 为了增强核酸适体的应用性能, 研究者对核酸适体进行了大量的改性研究. 本文系统总结了核酸适体筛选前、 后采用非共价或共价方式对其进行化学修饰, 以增加核酸适体与靶标的结合亲和力的相关研究进展, 并对未来发展前景进行了展望.
中图分类号:
TrendMD:
刘珂, 靳宇, 梁建功, 吴园. 化学修饰提高核酸适体结合亲和力的研究进展. 高等学校化学学报, 2021, 42(11): 3477.
LIU Ke, JIN Yu, LIANG Jiangong, WU Yuan. Research Progress on Improving the Binding Affinity of Aptamers through Chemical Modification. Chem. J. Chinese Universities, 2021, 42(11): 3477.
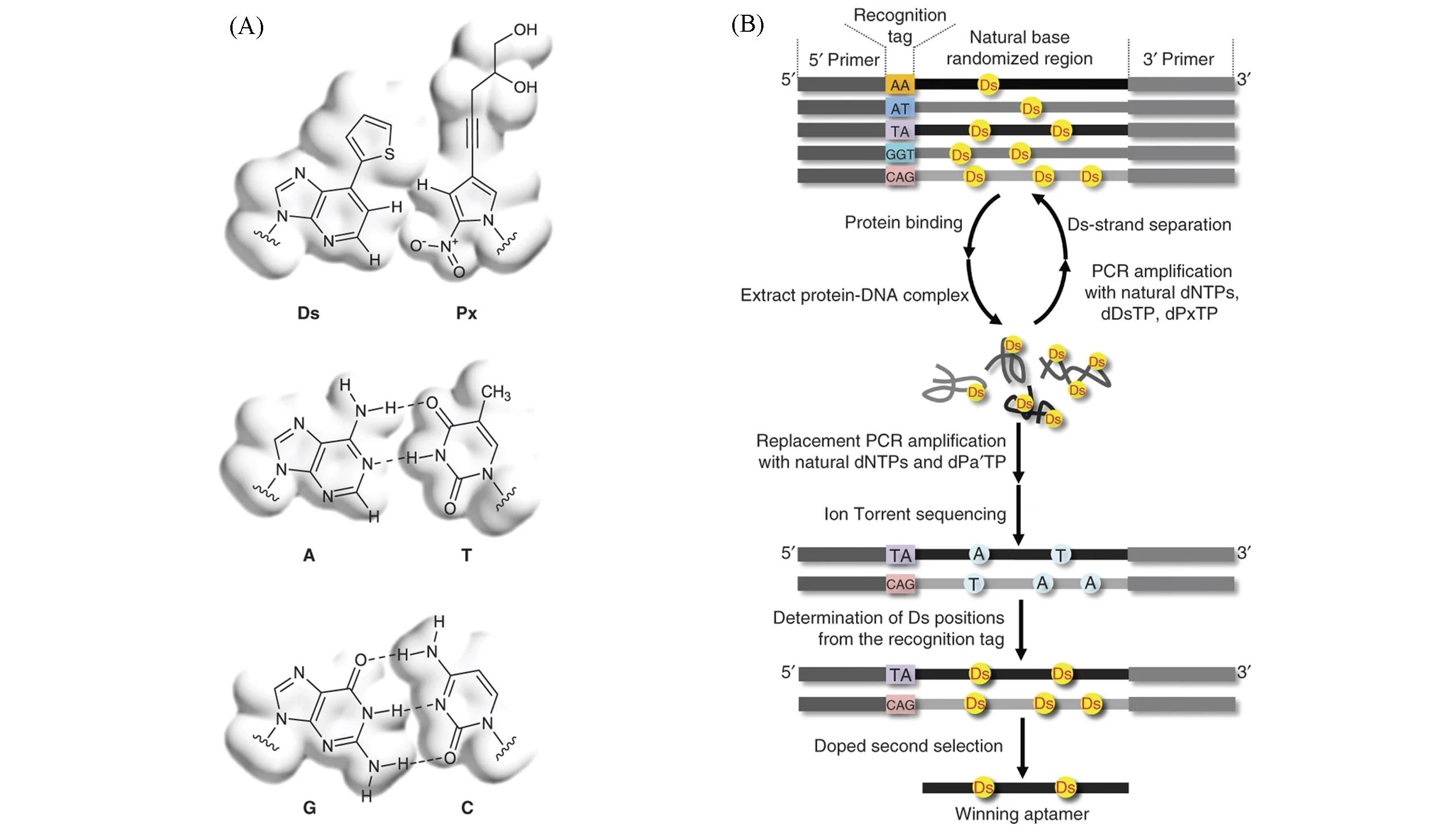
Fig.4 DNA aptamer selection using libraries containing hydrophobic Ds bases[46](A) Chemical structures of the indicated base pairs; (B) scheme of the SELEX procedure using DNA libraries with five different bases. Copyright 2013, Nature Publishing Group.
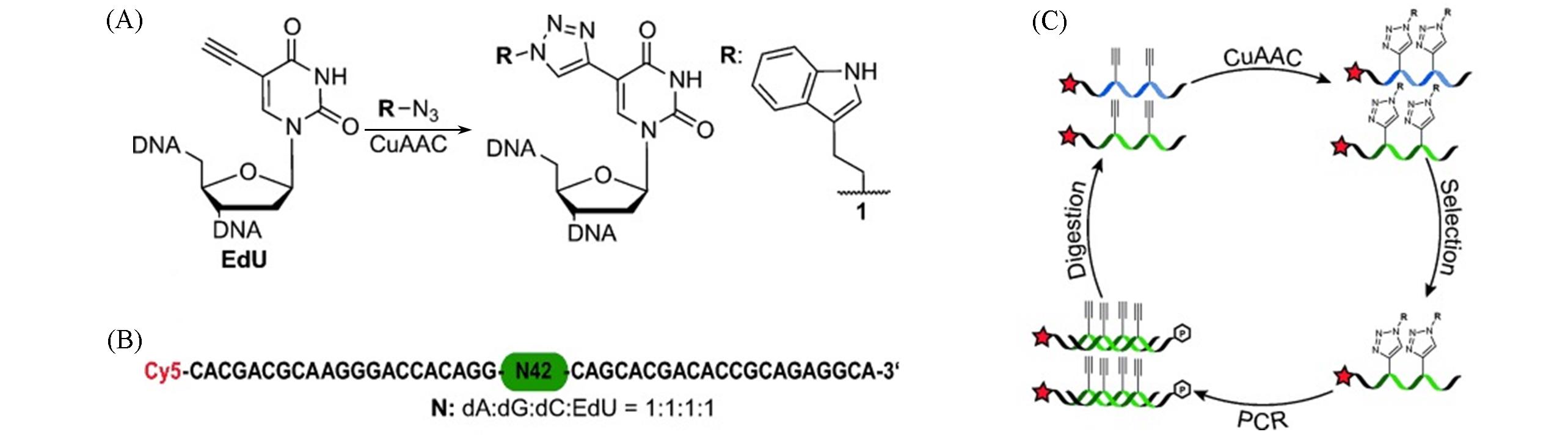
Fig.9 CuAAC functionalization of EdU?containing DNA molecules with azides(A), schematic representation of the library design(B) and schematic representation of the Click?SELEX process(C)[66]Copyright 2015, Wiley?VCH.
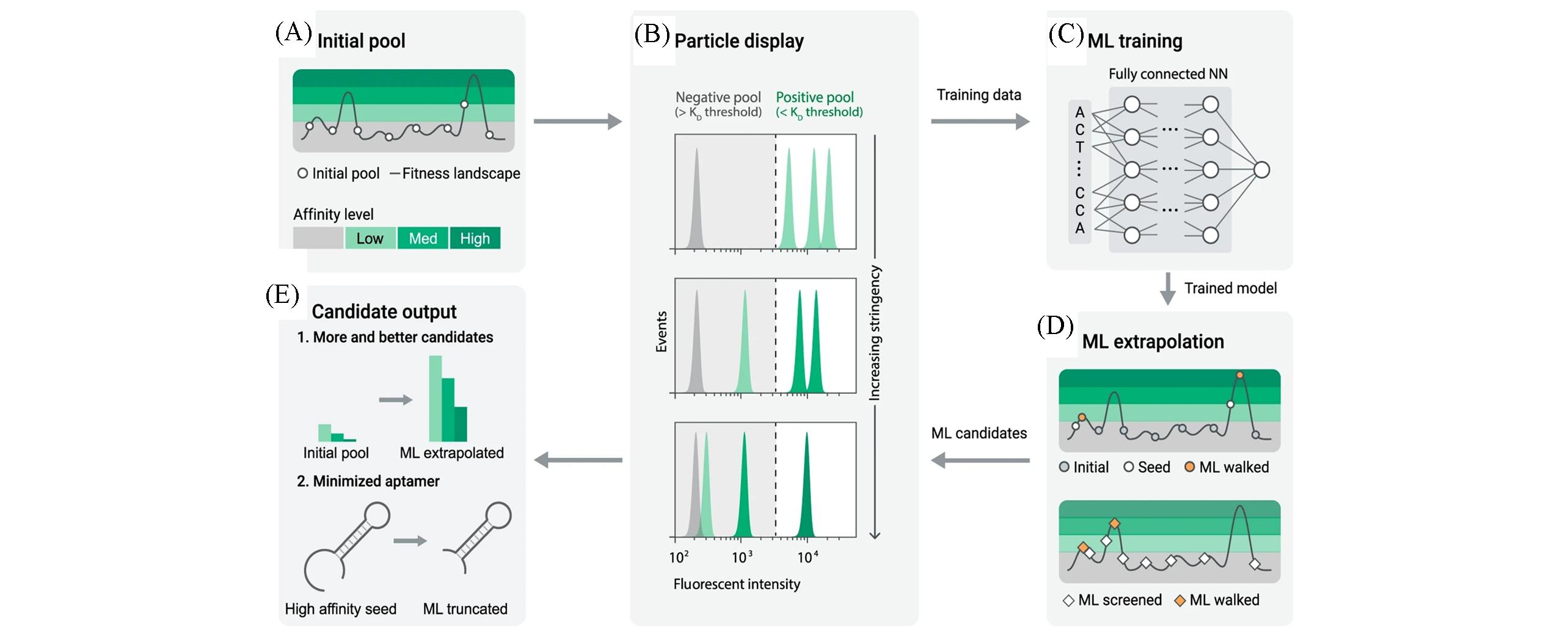
Fig.10 MLPD overview[81](A) Initial pool of MLPD?based SELEXA; (B) particle display; (C) to train and validate a neural network ML model; (D) the ML model extrapolates new sequences on the fitness landscape; (E) MLPD yields more candidates at each affinity level compared to the initial library, and enables sequence truncation without reduction in affinity. Copyright 2021, Nature Publishing Group.
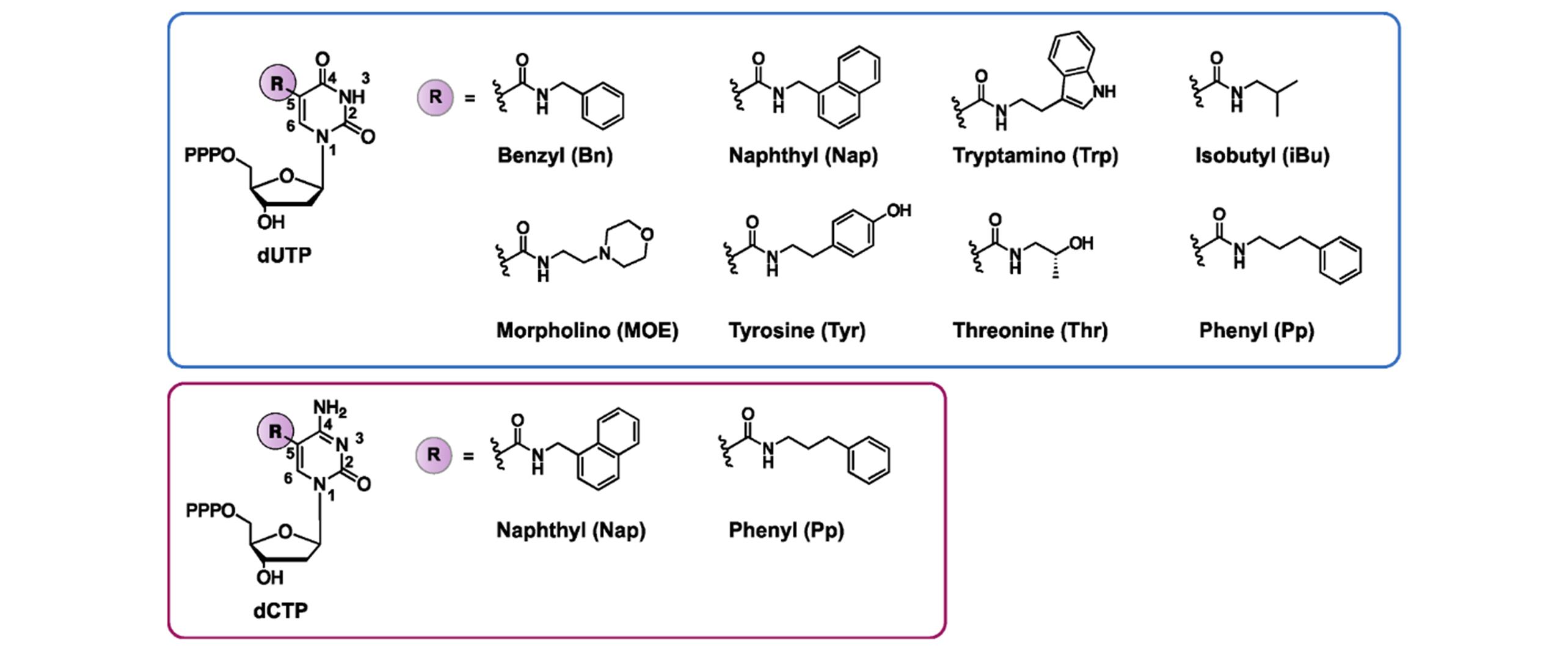
Fig.12 Overview of nucleobase modifications introduced at the C5 position of dUTP(deoxyuridines triphosphate) or dCTP (deoxycytidine triphosphate) for the synthesis of so?called SOMAmers[15]Copyright 2020, International Journal of Molecular Sciences.
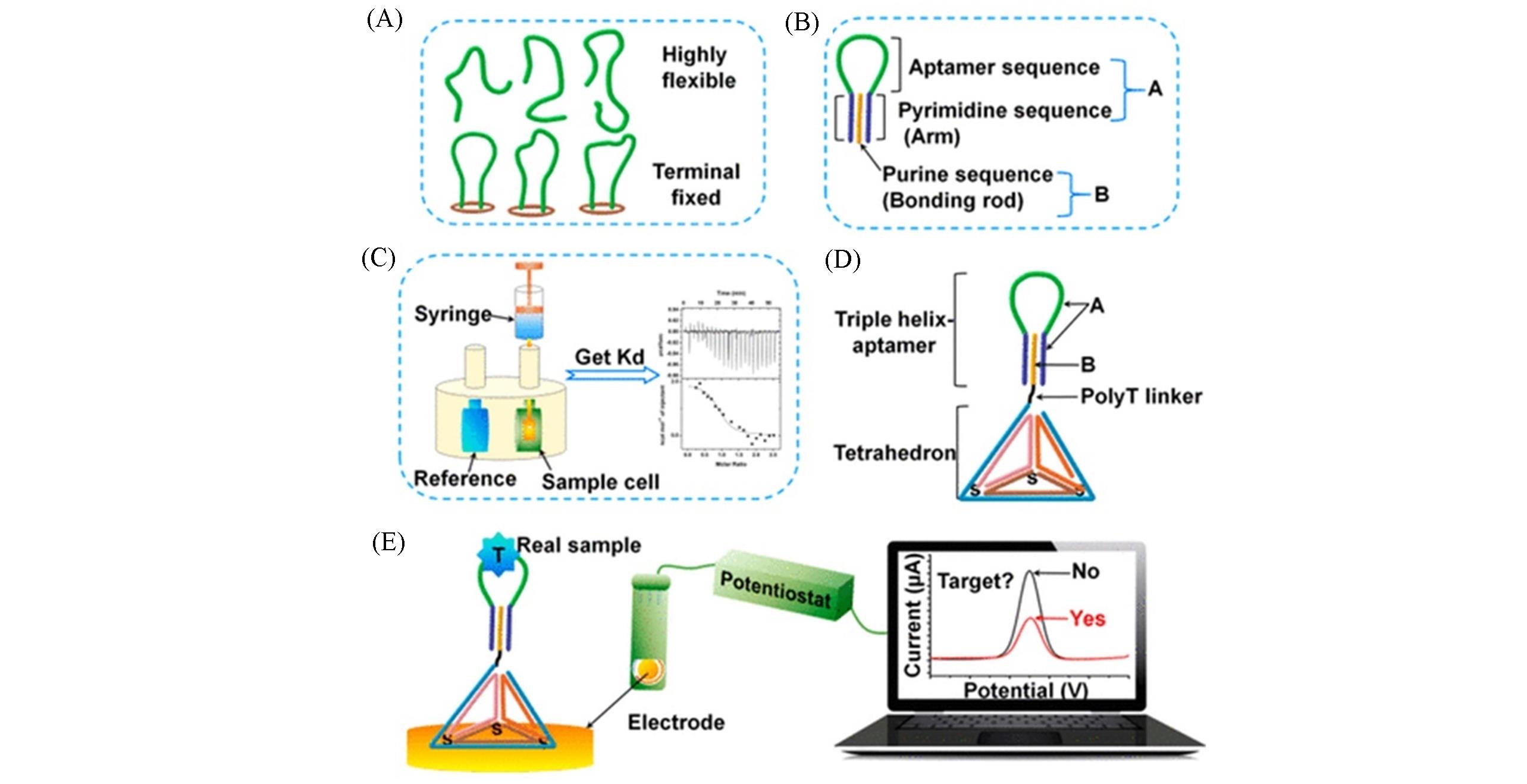
Fig.13 Terminal fixation restricting the flexibility of the original aptamer(A), schematic presentation of terminal fixation(B), scheme of the ITC(C), scheme of the tetrahedron?assisted triple helix?aptamer nanostructure(D) and schematic illustration of the developed electrochemical aptasensor(E)[99]Copyright 2019, American Chemical Society.
| 1 | Ellington A. D., Szostak J. W., Nature,1990, 346(6287), 818—822 |
| 2 | Tuerk C., Gold L., Science,1990, 249(4968), 505—510 |
| 3 | Strehlitz B., Reinemann C., Linkorn S., Stoltenburg R., Bioanal. Rev.,2012, 4(1), 1—30 |
| 4 | Tan S. Y., Acquah C., Sidhu A., Ongkudon C. M., Yon L. S., Danquah M. K., Crit. Rev. Anal. Chem.,2016, 46(6), 521—537 |
| 5 | Hermann T., Patel D. J., Science,2000, 287(5454), 820—825 |
| 6 | Vivekananda J., Kiel J. L., Lab. Invest.,2006, 86(6), 610—618 |
| 7 | Xu H., Mao X., Zeng Q. X., Wang S. F., Kawde A. N., Liu G. D., Anal. Chem.,2009, 81(2), 669—675 |
| 8 | Pilehvar S., Reinemann C., Bottari F., Vanderleyden E., van Vlierberghe S., Blust R., Strehlitz B., De Wael K., Sens. Actuators B,2017, 240, 1024—1035 |
| 9 | Canoura J., Yu H., Alkhamis O., Roncancio D., Farhana R., Xiao Y., J. Am. Chem. Soc., 2020, 143(2), 805—816 |
| 10 | Li J. J., Xu M., Huang H. P., Zhou J. J., Abdel⁃Halim E. S., Zhang J. R., Zhu J. J., Talanta,2011, 85(4), 2113—2120 |
| 11 | Dougherty C. A., Cai W. B., Hong H., Curr. Top. Med. Chem.,2015, 15(12), 1138—1152 |
| 12 | Banerjee J., Nilsen⁃Hamilton M., J. Mol. Med.,2013, 91(12), 1333—1342 |
| 13 | Dunn M. R., Jimenez R. M., Chaput J. C., Nat. Rev. Chem.,2017, 1(10), 0076 |
| 14 | Li L., Xu S., Yan H., Li X., Yazd H. S., Li X., Huang T., Cui C., Jiang J., Tan W., Angew. Chem. Int. Ed.,2020, 60(5), 2221—2231 |
| 15 | Elskens J. P., Elskens J. M., Madder A., Int. J. Mol. Sci.,2020, 21(12), 4522 |
| 16 | Shen R., Tan J., Yuan Q., ACS Appl. Bio. Mater.,2020, 3(5), 2816—2826 |
| 17 | Chen A. L., Yang S. M., Biosens. Bioelectron.,2015, 71, 230—242 |
| 18 | Rajesh K., Rana K. V., Suri C. R., Bionanoscience,2013, 3(2), 137—144 |
| 19 | Hoogenboom H. R., Nat. Biotechnol.,2005, 23(9), 1105—1116 |
| 20 | Wang X. Q., Peng M., Li C. X., Zhang Y., Zhang M., Tang Y., Liu M. D., Xie B. R., Zhang X. Z., Nano Lett.,2018, 18(11), 6804—6811 |
| 21 | Baker B. R., Lai R. Y., Wood M. S., Doctor E. H., Heeger A. J., Plaxco K. W., J. Am. Chem. Soc.,2006, 128(10), 3138—3139 |
| 22 | Bates P. J., Reyes⁃Reyes E. M., Malik M. T., Murphy E. M., O’Toole M. G., Trent J. O., Biochim. Biophys. Acta Gen. Subj.,2017, 1861(5), 1414—1428 |
| 23 | Zou X. R., Wu J., Gu J. Q., Shen L., Mao L. X., Front. Microbiol.,2019, 10, 20 |
| 24 | Wang L. J., Wang R. H., Wei H., Li Y. B., World J. Microbiol. Biotechnol.,2018, 34(10), 11 |
| 25 | Cerchia L., de Franciscis V., Trends Biotechnol.,2010, 28(10), 517—525 |
| 26 | Meek K. N., Rangel A. E., Heemstra J. M., Methods,2016, 106, 29—36 |
| 27 | Lei Y., Qiao Z., Tang J., He X., Shi H., Ye X., Yan L., He D., Wang K., Theranostics,2018, 8(15), 4062—4071 |
| 28 | Li K., Deng J., Jin H., Yang X., Fan X., Li L., Zhao Y., Guan Z., Wu Y., Zhang L., Yang Z., Org. Biomol. Chem.,2017, 15(5), 1174—1182 |
| 29 | Thiviyanathan V., Gorenstein D. G., Prot. Clin. Appl.,2012, 6(11/12), 563—573 |
| 30 | Liu H. C., Ponniah G., Zhang H. M., Nowak C., Neill A., Gonzalez-Lopez N., Patel R., Cheng G. L., Kita A. Z., Andrien B., mAbs,2014, 6(5), 1145—1154 |
| 31 | Gomez E. F., Venkatraman V., Grote J. G., Steckl A. J., Adv. Mater.,2015, 27(46), 7552—7562 |
| 32 | Zhirnov V., Zadegan R. M., Sandhu G. S., Church G. M. Hughes W. L., Nat. Mater.,2016, 15(4), 366—370 |
| 33 | Meng H. M., Liu H., Kuai H., Peng R., Mo L., Zhang X. B., Chem. Soc. Rev.,2016, 45(9), 2583—2602 |
| 34 | Kim Y. S., Raston N. H., Gu M. B., Biosens. Bioelectron.,2016, 76, 2—19 |
| 35 | Abbaspour A., Norouz⁃Sarvestani F., Noori A., Soltani N., Biosens. Bioelectron.,2015, 68, 149—155 |
| 36 | Hianik T., Ostatna V., Sonlajtnerova M., Grman, I., Bioelectrochemistry,2007, 70(1), 127—133 |
| 37 | Huang L. L., Yang X. J., Qi C., Niu X. F., Zhao C. L., Zhao X. H., Shangguan D. H., Yang Y. H., Anal. Chim. Acta,2013, 787, 203—210 |
| 38 | Nakatsuka N., Abendroth J. M., Yang K. A., Andrews A. M., ACS Appl. Mater. Interfaces,2021,13(8), 9425—9435 |
| 39 | Chen T., Hongdilokkul N., Liu Z., Thirunavukarasu D., Romesberg F.E., Curr. Opin. Chem. Biol., 2016, 34, 80—87 |
| 40 | Kimoto M., Hikida Y., Hirao I., Isr. J. Chem., 2013, 53(6/7), 450—468 |
| 41 | Sigel A., Sigel H., Sigel R. K. O., Interplay Between Metal Ions and Nucleic Acids, Springer, Netherlands, 2012, 280—320 |
| 42 | Benner S. A., Karalkar N. B., Hoshika S., Laos R., Shaw R. W., Matsuura M., Fajardo D., Moussatche P., Cold Spring Harb. Perspect. Biol.,2016, 8(11), 26 |
| 43 | Rich A.; Ed.: Kasha M., Pullman B., Horizons in Biochemistry, Academic Press, New York, 1962, 103—126 |
| 44 | Switzer C., Moroney S. E., Benner S. A., J. Am. Chem. Soc., 1989, 111(21), 8322—8323 |
| 45 | Piccirilli J. A., Krauch T., Moroney S. E., Benner S. A., Nature, 1990, 343(6253), 33—37 |
| 46 | Kimoto M., Yamashige R., Matsunaga K., Yokoyama S., Hirao I., Nat. Biotechnol.,2013, 31(5), 453—457 |
| 47 | Zhang L., Yang Z., Sefah K., Bradley K. M., Hoshika S., Kim M. J., Kim H. J., Zhu G., Jimenez E., Cansiz S., Teng I. T., Champanhac C., McLendon C., Liu C., Zhang W., Gerloff D. L., Huang Z., Tan W., Benner S. A., J. Am. Chem. Soc., 2015, 137(21), 6734—6737 |
| 48 | Georgiadis M. M., Singh I., Kellett W. F., Hoshika S., Benner S. A., Richards N. G., J. Am. Chem. Soc., 2015, 137(21), 6947—6955 |
| 49 | Wang X., Hoshika S., Peterson R. J., Kim M. J., Benner S. A., Kahn J. D., ACS Synth. Biol., 2017, 6(5), 782—792 |
| 50 | Benner S. A., Karalkar N. B., Hoshika S., Laos R., Shaw R. W., Matsuura M., Fajardo D., Moussatche P., Cold Spring Harb. Perspect. Biol., 2016, 8(11), a023770 |
| 51 | Yang Z., Sismour A. M., Sheng P., Puskar N. L., Benner S. A., Nucleic Acids Res., 2007, 35(13), 4238—4249 |
| 52 | Yang Z., Chen F., Chamberlin S. G., Benner S. A., Angew. Chem. Int. Ed. Engl., 2010, 49(1), 177—180 |
| 53 | Yang Z., Chen F., Alvarado J. B., Benner S. A., J. Am. Chem. Soc., 2011, 133(38), 15105—15112 |
| 54 | Shangguan D., Li Y., Tang Z., Cao Z. C., Chen H. W., Mallikaratchy P., Sefah K., Yang C. J., Tan W., Proc. Natl. Acad. Sci. USA,2006, 103(32), 11838—11843 |
| 55 | Sefah K., Yang Z., Bradley K. M., Hoshika S., Jimenez E., Zhang L., Zhu G., Shanker S., Yu F., Turek D., Tan W., Benner S. A., Proc. Natl. Acad. Sci. USA, 2014, 111(4), 1449—1454 |
| 56 | Zhang L., Yang Z., Le Trinh T., Teng I. T., Wang S., Bradley K. M., Hoshika S., Wu Q., Cansiz S., Rowold D. J., McLendon C., Kim M. S., Wu Y., Cui C., Liu Y., Hou W., Stewart K., Wan S., Liu C., Benner S. A., Tan W., Angew. Chem. Int. Ed.,2016, 55(40), 12372—12375 |
| 57 | Biondi E., Lane J. D., Das D., Dasgupta S., Piccirilli J. A., Hoshika S., Bradley K. M., Krantz B. A., Benner S. A., Nucleic Acids Res.,2016, 44(20), 9565—9577 |
| 58 | Yang Z., Chen F., Chamberlin S. G., Benner S. A., Angew. Chem. Int. Ed. Engl., 2010, 49(1), 177—180 |
| 59 | Feng M., Ho M., FEBS Lett., 2014, 588(2), 377—382 |
| 60 | Capurro M., Wanless I. R., Sherman M., Deboer G., Shi W., Miyoshi E., Filmus J., Gastroenterology, 2003, 125(1), 89—97 |
| 61 | Tan J., Zhao M., Wang J., Li Z., Liang L., Zhang L., Yuan Q., Tan W., Angew. Chem. Int. Ed.,2019, 58(6), 1621—1625 |
| 62 | Mangani S., Orioli P. L., Scozzafava A., Messori L., Carloni P., Biometals,1994, 7(2), 104—108 |
| 63 | Terrón A., Fiol J. J., García⁃Raso A., Barceló⁃Oliver M., Moreno V., Coord. Chem. Rev.,2007, 251(15/16), 1973—1986 |
| 64 | Guo F., Li Q., Zhou C., Org. Biomol. Chem.,2017, 15(45), 9552—9565 |
| 65 | Sakthivel K., Barbas C. F., Angew. Chem. Int. Ed., 1998, 37(20), 2872—2875 |
| 66 | Tolle F., Brandle G. M., Matzner D., Mayer G., Angew. Chem. Int. Ed.,2015, 54(37), 10971—10974 |
| 67 | Davies D. R., Gelinas A. D., Zhang C., Rohloff J. C., Carter J. D., O'Connell D., Waugh S. M., Wolk S. K., Mayfield W. S., Burgin A. B., Edwards T. E., Stewart L. J., Gold L., Janjic N., Jarvis T. C., Proc. Natl. Acad. Sci. USA,2012, 109(49), 19971—19976 |
| 68 | Gawande B. N., Rohloff J. C., Carter J. D., von Carlowitz I., Zhang C., Schneider D. J., Janjic N., Proc. Natl. Acad. Sci. USA,2017, 114(11), 2898—2903 |
| 69 | Wang L., Liang H., Sun J., Liu Y., Li J., Yang H., J. Am. Chem. Soc.,2019,141(32), 12673—12681 |
| 70 | Lee I., Berdis A. J., Biochim. Biophys. Acta Proteins Proteom., 2010, 1804(5), 1064—1080 |
| 71 | Pinheiro V. B., Holliger P., Trends Biotechnol., 2014, 32(6), 321—328 |
| 72 | Laos R., Thomson J. M., Benner S. A., Front. Microbiol., 2014, 5, 1—14 |
| 73 | Staiger N., Marx A., Chembiochem, 2010, 11(14), 1963—1966 |
| 74 | Schneider G., Nat. Rev. Drug Discov., 2018, 17(2), 97—113 |
| 75 | Liu G., Zeng H., Mueller J., Carter B., Wang Z., Schilz J., Horny G., Birnbaum M. E., Ewert S., Gifford D. K., Bioinformatics, 2020, 36(7), 2126—2133 |
| 76 | Cuperus J. T., Groves B., Kuchina A., Rosenberg A. B., Jojic N., Fields S., Seelig G., Genome Res., 2017, 27(12), 2015—2024 |
| 77 | Hall B., Micheletti J. M., Satya P., Ogle K., Pollard J., Ellington A. D., Curr. Protoc. Nucleic Acid Chem., 2009, 39, 9.2.1—9.2.28 |
| 78 | Sabeti P. C., Unrau P. J., Bartel D. P., Chem. Biol., 1997, 4(10), 767—774 |
| 79 | Knight C. G., Platt M., Rowe W., Wedge D. C., Khan F., Day P. J., McShea A., Knowles J., Kell D. B., Nucleic Acids Res., 2009, 37(1), e6 |
| 80 | Chushak Y., Stone M. O., Nucleic Acids Res., 2009, 37(12), e87 |
| 81 | Bashir A., Yang Q., Wang J., Hoyer S., Chou W., McLean C. Davis G., Gong Q., Armstrong Z., Jang J., Kang H., Pawlosky A., Scott A., Dahl G. E., Berndl M., Dimon M., Ferguson B. S., Nat. Commun., 2021, 12(1), 2366 |
| 82 | Gao S. X., Zheng X., Jiao B. H., Wang L. H., Anal. Bioanal. Chem.,2016, 408(17), 4567—4573 |
| 83 | Rothlisberger P., Hollenstein M., Adv. Drug Deliv. Rev.,2018, 134, 3—21 |
| 84 | Gupta S., Hirota M., Waugh S. M., Murakami I., Suzuki T., Muraguchi M., Shibamori M., Ishikawa Y., Jarvis T. C., Carter J. D., Zhang C., Gawande B., Vrkljan M., Janjic N., Schneider D. J., J. Biol. Chem.,2014, 289(12), 8706—8719 |
| 85 | Karlsen K. K., Wengel J., Nucleic Acid Ther.,2012, 22(6), 366—370 |
| 86 | Kuwahara M.; Eds.: Erdmann V. A., Markiewicz W. T., Barciszewski J., Chemical Biology of Nucleic Acids: Fundamentals and Clinical Applications, Springer Press, Berlin, 2014, 243—270 |
| 87 | Lapa S. A., Chudinov A. V., Timofeev E. N., Mol. Biotechnol., 2016, 58(2), 79—92 |
| 88 | Yamamoto T., Nakatani M., Narukawa K., Obika S., Future Med. Chem.,2011, 3(3), 339—365 |
| 89 | Borbone N., Bucci M., Oliviero G., Morelli E., Amato J., D’Atri V., D'Errico S., Vellecco V., Cirino G., Piccialli G., Fattorusso C., Varra M., Mayol L., Persico M., Scuotto M., J. Med. Chem.,2012, 55(23), 10716—10728 |
| 90 | Matsunaga K. I., Kimoto M., Hirao I., J. Am. Chem. Soc.,2017, 139(1), 324—334 |
| 91 | Tam R. C., Wu⁃Pong S., Pai B., Lim C., Chan A., Thomas D. F., Milovanovic T., Bard J., Middleton P. J., Antisense Nucleic Acid Drug Dev.,1999, 9(3), 289—300 |
| 92 | Lee K. Y., Kang H., Ryu S. H., Lee D. S., Lee J. H., Kim S., J. Biomed. Biotechnol.,2010, 168306 |
| 93 | Mallikaratchy P. R., Ruggiero A., Gardner J. R., Kuryavyi V., Maguire W. F., Heaney M. L., McDevitt M. R., Patel D. J., Scheinberg D. A., Nucleic Acids Res.,2011, 39(6), 2458—2469 |
| 94 | Lin Y., Padmapriya A., Morden K. M., Jayasena S. D., Proc. Natl. Acad. Sci. USA,1995, 92(24), 11044—11048 |
| 95 | Gold L., Ayers D., Bertino J., Bock C., Bock A., Brody E. N., Carter J., Dalby A. B., Eaton B. E., Fitzwater T., Flather D., Forbes A., Foreman T., Fowler C., Gawande B., Goss M., Gunn M., Gupta S., Halladay D., Heil J., Heilig J., Hicke B., Husar G., Janjic J., Jarvis T., Jennings S., Katilius E., Keeney T. R., Kim N., Koch T. H., Kraemer S., Kroiss L., Le N., Levine D., Lindsey W., Lollo B., Mayfield W., Mehan M., Mehler R., Nelson S. K., Nelson M., Nieuwlandt D., Nikrad M., Ochsner U., Ostroff R. M., Otis M., Parker T., Pietrasiewicz S., Resnicow D. I., Rohloff J., Sanders G., Sattin S., Schneider D., Singer B., Stanton M., Sterkel A., Stewart A., Stratford S., Vaught J. D., Vrkljan M., Walker J. J., Watrobka M., Waugh S., Weiss A., Wilcox S. K., Wolfson A., Wolk S. K., Zhang C., Zichi D., PLoS One,2010, 5(12), 17 |
| 96 | Gelinas A. D., Davies D. R., Edwards T. E., Rohloff J. C., Carter J. D., Zhang C., Gupta S., Ishikawa Y., Hirota M., Nakaishi Y., Jarvis T. C., Janjic N., J. Biol. Chem.,2014, 289(12), 8720—8734 |
| 97 | AlShamaileh H., Veedu R. N., ChemBioChem,2017, 18(16), 1565—1567 |
| 98 | Gold L., Walker J. J., Wilcox S. K., Williams S., New Biotechnol.,2012, 29(5), 543—549 |
| 99 | Zhao L., Qi X., Yan X., Huang Y., Liang X., Zhang L., Wang S., Tan W., J. Am. Chem. Soc.,2019, 141(44), 17493—17497 |
| 100 | Lao Y. H., Phua K. K. L., Leong K. W., ACS Nano,2015, 9(3), 2235—2254 |
| 101 | Kong H. Y., Byun J., Biomol. Ther.,2013, 21(6), 423—434 |
| 102 | Wang R. E., Wu H., Niu Y., Cai J., Curr. Med. Chem.,2011, 18(27), 4126—4138 |
| 103 | Yamamoto R., Kumar P. K. R., Genes Cells,2000, 5(5), 389—396 |
| 104 | Lee E. H., Lim H. J., Lee S. D., Son A., ACS Appl. Mater. Inter.,2017, 9(17), 14889—14898 |
| 105 | Gao S., Hu B., Zheng X., Cao Y., Liu D., Sun M., Jiao B., Wang L., Biosens. Bioelectron.,2016, 79, 938—944 |
| 106 | Park J. W., Tatavarty R., Kim D. W., Jung H. T., Gu M. B., Chem. Commun.,2012, 48(15), 2071—2073 |
| 107 | Zheng X., Hu B., Gao S. X., Liu D. J., Sun M. J., Jiao B. H., Wang L. H., Toxicon,2015, 101, 41—47 |
| 108 | Alhadrami H. A., Chinnappan R., Eissa S., Rahamn A. A., Zourob M., Anal. Biochem.,2017, 525, 78—84 |
| 109 | Jia M., Sha J., Li Z., Wang W., Zhang H., Food Chem.,2020, 317, 126459 |
| 110 | Jo M., Ahn J. Y., Lee J., Lee S., Hong S. W., Yoo J. W., Kang J., Dua P., Lee D. K., Hong S., Kim S., Oligonucleotides,2011, 21(2), 85—91 |
| 111 | Van Dongen M. A., Dougherty C. A., Banaszak Holl M. M., Biomacromolecules,2014, 15(9), 3215—3234 |
| 112 | Kim J., Hu J., Bezerra A. B., Holtan M. D., Brooks J. C., Easley C. J., Anal. Chem.,2015, 87(19), 9576—9579 |
| 113 | Jiang Y., Pan X., Chang J., Niu W., Hou W., Kuai H., Zhao Z., Liu J., Wang M., Tan W., J. Am. Chem. Soc.,2018, 140(22), 6780—6784 |
| 114 | Xue C., Zhang S., Yu X., Hu S., Lu Y., Wu Z. S., Angew. Chem. Int. Ed.,2020, 59(40), 17540—17547 |
| 115 | Zhang S., Chen C., Xue C., Chang D., Xu H., Salena B. J., Li Y., Wu Z. S., Angew. Chem. Int. Ed.,2020, 59(34), 14584—14592 |
| 116 | Liu Y. L., Zhang H. M., Du Y. H., Zhu Z., Zhang M. X., Lv Z. H., Wu L. L., Yang Y. Y., Li A., Yang L., Song Y. L., Wang S. L., Yang C. Y., Small,2020, 16(20), 8 |
| 117 | Mallikaratchy P., Tang Z., Kwame S., Meng L., Shangguan D., Tan W., Mol. Cell. Proteomics,2007, 6(12), 2230—2238 |
| 118 | Wu X., Zhao Z., Bai H., Fu T., Yang C., Hu X., Liu Q., Champanhac C., Teng I. T., Ye M., Tan W., Theranostics,2015, 5(9), 985—994 |
| 119 | Kuai H., Zhao Z., Mo L., Liu H., Hu X., Fu T., Zhang X., Tan W., J. Am. Chem. Soc.,2017, 139(27), 9128—9131 |
| 120 | Wu Y., Zhang L., Cui C., Cansiz S., Liang H., Wu C., Teng I. T., Chen W., Liu Y., Hou W., Zhang X., Tan W., J. Am. Chem. Soc.,2018, 140(1), 2—5 |
| 121 | Ding C., Zhang C., Cheng S., Xian Y., Adv. Funct. Mater.,2020, 30(16), 1909781 |
| 122 | Sheng W. A., Chen T., Tan W. H., Fan Z. H., ACS Nano,2013, 7(8), 7067—7076 |
| 123 | Chen Y., Tyagi D., Lyu M., Carrier A. J., Nganou C., Youden B., Wang W., Cui S., Servos M., Oakes K., He S., Zhang X., Anal. Chem.,2019, 91(6), 4017—4022 |
| 124 | Ahmed M. G., Abate M. F., Song Y., Zhu Z., Yan F., Xu Y., Wang X., Li Q., Yang C., Angew. Chem. Int. Ed.,2017, 56(36), 10681—10685 |
| [1] | 崔韶丽, 张维佳, 邵学广, 蔡文生. 自由能计算揭示苏氨酸对抗冻蛋白与冰晶结合能力的影响[J]. 高等学校化学学报, 2022, 43(3): 20210838. |
| [2] | 解忱, 陈娜, 杨雁冰, 袁荃. 核酸适体功能化的二维材料场效应晶体管传感器研究进展[J]. 高等学校化学学报, 2021, 42(11): 3406. |
| [3] | 赵卓, 王雪强. 核酸适体偶联药物的生物偶联构建技术与应用[J]. 高等学校化学学报, 2021, 42(11): 3367. |
| [4] | 刘学娇, 杨帆, 刘爽, 张春娟, 刘巧玲. 核酸适体靶向的膜蛋白识别与功能调控研究进展[J]. 高等学校化学学报, 2021, 42(11): 3277. |
| [5] | 张晓荣, 陈岚岚, 胡善文. 基于分子识别的细菌检测研究进展[J]. 高等学校化学学报, 2021, 42(11): 3468. |
| [6] | 吉采灵, 程兴, 谈洁, 袁荃. 功能化核酸适体的筛选及分子识别应用[J]. 高等学校化学学报, 2021, 42(11): 3457. |
| [7] | 黄玲, 庄梓健, 李翔, 石沐玲, 刘高强. 基于核酸适体的外泌体分子识别研究进展[J]. 高等学校化学学报, 2021, 42(11): 3493. |
| [8] | 李容庆,刘佳璐,范若辰,白鹏阳,张丽影,权春善. 磷酰化组氨酸特异性抗体的制备与应用[J]. 高等学校化学学报, 2020, 41(7): 1552. |
| [9] | 董倩, 李兆倩, 彭天欢, 陈卓, 谭蔚泓. 核酸适体在癌症诊疗中的研究进展[J]. 高等学校化学学报, 2020, 41(12): 2648. |
| [10] | 马永钧, 丁静, 金芝梅, 铁珍珍, 周敏. 修饰铂阳极上氯离子对4种有机醇电氧化反应的阻化作用[J]. 高等学校化学学报, 2015, 36(5): 864. |
| [11] | 黎春怡, 黄卓烈, 王春晓. 壳寡糖化学修饰对云芝漆酶催化活性和酶学性质的影响[J]. 高等学校化学学报, 2015, 36(4): 704. |
| [12] | 刘中成, 赵丽健, 刘利鹏, 张艳芬, 王南南, 陈瑶, 王向欢. 基于胶体金检测核酸适配子与蛋白相互作用的新方法[J]. 高等学校化学学报, 2015, 36(4): 638. |
| [13] | 赵秋伶, 刘玲玲, 杨丽娜. 基于核酸适体检测ATP的酶联分析新方法[J]. 高等学校化学学报, 2014, 35(6): 1161. |
| [14] | 李海云, 蒋育澄, 胡满成, 李淑妮, 翟全国. 氯过氧化物酶活性中心结构域中Mn2+与酶催化行为的关系[J]. 高等学校化学学报, 2013, 34(4): 875. |
| [15] | 赵春玲, 华梅, 赵晓慧, 黄亮亮, 冯亚娟, 牛司朋, 符雪文, 袁聪, 杨云慧. 非标记型血小板衍生生长因子核酸适体传感器[J]. 高等学校化学学报, 2013, 34(1): 61. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||