

高等学校化学学报 ›› 2023, Vol. 44 ›› Issue (3): 20220335.doi: 10.7503/cjcu20220335
收稿日期:2022-05-13
出版日期:2023-03-10
发布日期:2023-03-14
通讯作者:
田沺
E-mail:ttian@whu.edu.cn
基金资助:
ZHANG Kaisong, WANG Shaoru, ZHANG Yutong, TIAN Tian( )
)
Received:2022-05-13
Online:2023-03-10
Published:2023-03-14
Contact:
TIAN Tian
E-mail:ttian@whu.edu.cn
Supported by:摘要:
核酸是生物体的遗传物质, 在生命体系中发挥着重要作用. 除了构成核酸的经典碱基之外, 核酸中还存在天然修饰的碱基, 这被称为核酸的表观遗传修饰. 核酸的表观遗传修饰在基因表达过程中具有重要的调控作用, 对生物体遗传和生命生长过程影响很大, 并且核酸表观遗传与疾病密切相关. 超分子化学是研究分子间键的化学, 而许多生物分子都需要通过超分子化学作用来发挥其生物功能, 可以说生物体内天然存在着大量的超分子化学过程. 本文综合评述了基于超分子化学的核酸表观遗传修饰研究的一些代表性工作.
中图分类号:
TrendMD:
张凯嵩, 王少儒, 张雨桐, 田沺. 基于超分子化学的核酸表观遗传修饰研究. 高等学校化学学报, 2023, 44(3): 20220335.
ZHANG Kaisong, WANG Shaoru, ZHANG Yutong, TIAN Tian. Study of Epigenetic Modifications of Nucleic Acids Based on Supramolecular Chemistry. Chem. J. Chinese Universities, 2023, 44(3): 20220335.
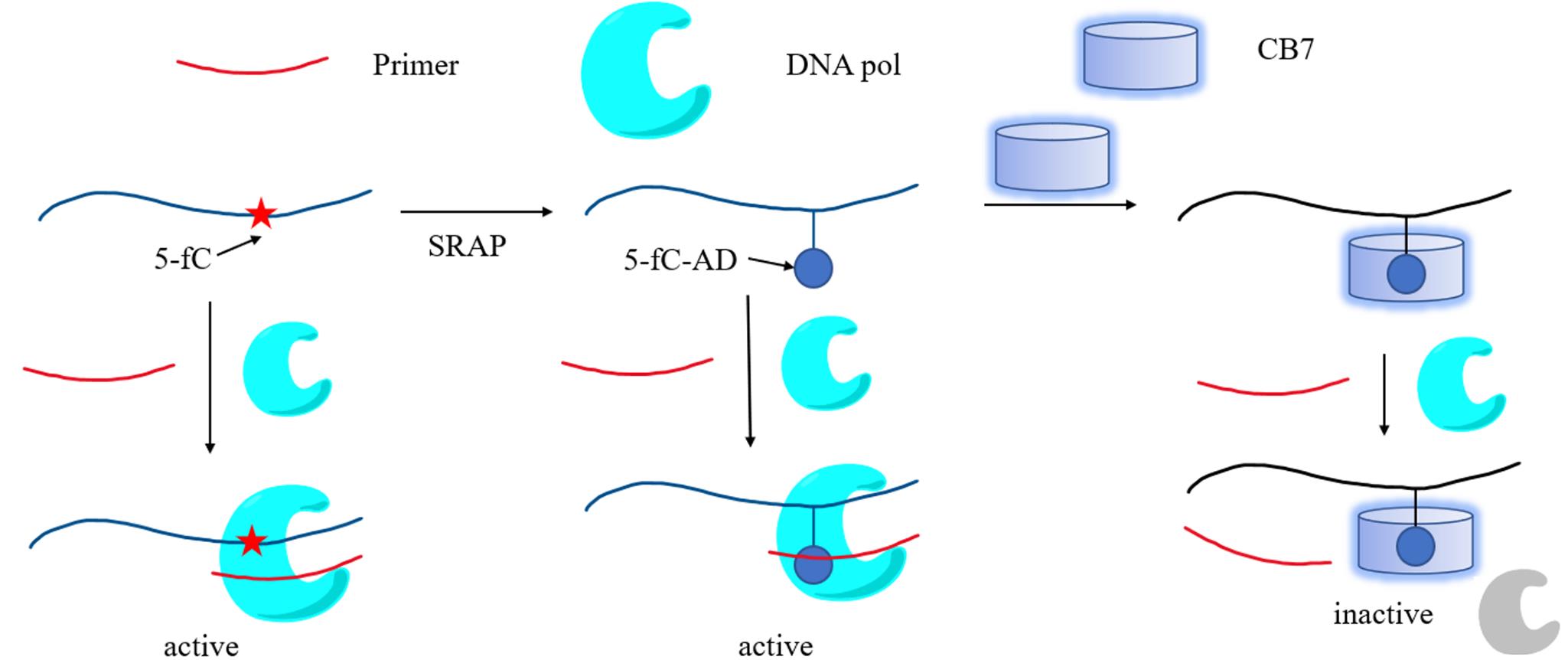
Fig.3 Schematic illustration of CB7⁃driven host⁃guest chemistry for intervention of 5‑formylcytosine⁃targeted PCR[18]Copyright 2017, American Chemical Society.
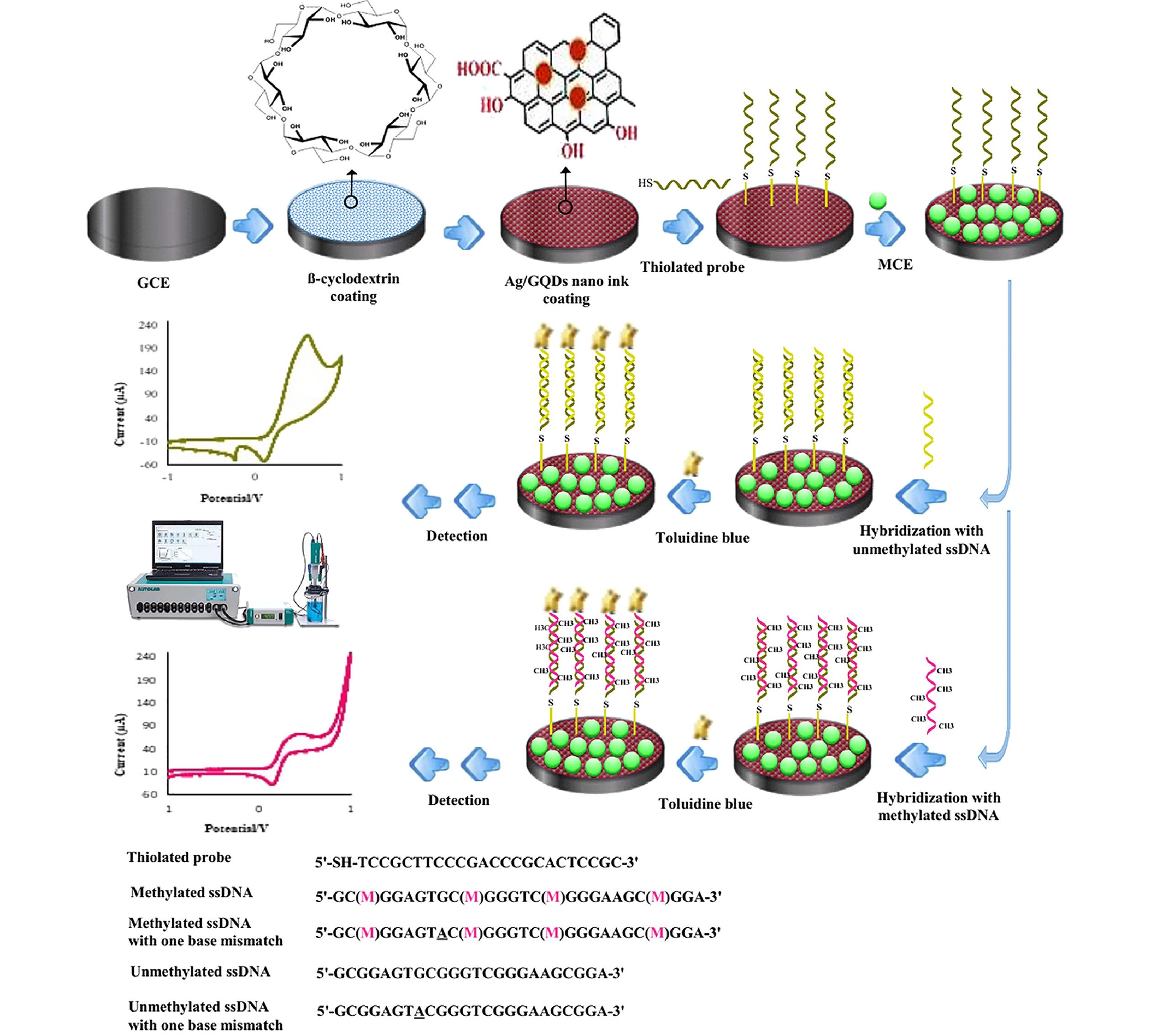
Fig.13 Schematic illustration of reliable recognition of DNA methylation using bioanalysis of hybridization on the surface of Ag/GQD nanocomposite[49]Copyright 2021, John Wiley & Sons Ltd.
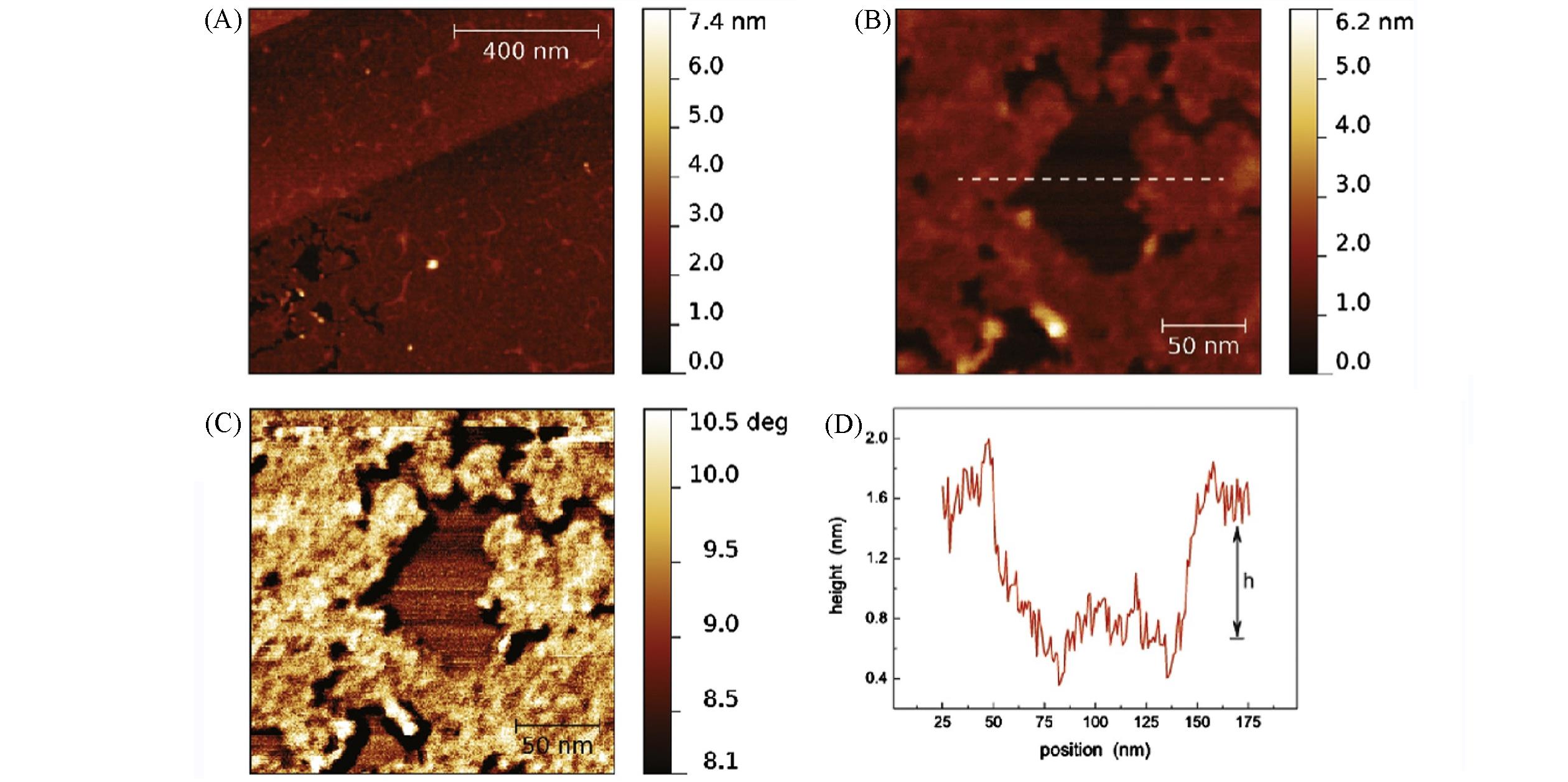
Fig.14 AFM characterization of (caC)2⁃Ca superstructures self⁃assembled on HOPG[50](A) Topography of a 1 μm×1 μm area; (B) closer view of the topography showing discontinuities in the monolayer which reveal the HOPG substrate; (C) corresponding phase imaging evidencing that the layer and exposed substrate are constitu⁃ted by different materials; (D) profile extracted in correspondence of the line shown in the inset from which the thickness of the layer is evaluated as (0.8±0.1) nm, compatible with a single-molecule layer.Copyright 2017, Elsevier B. V.
| 1 | Cantara W. A., Crain P. F., Rozenski J., McCloskey J. A., Harris K. A., Zhang X. N., Vendeix F. A. P., Fabris D., Agris P. F., Nucleic Acids Res., 2011, 39, D195—D201 |
| 2 | Herdewijn P., Modified Nucleosides: In Biochemistry, Biotechnology and Medicine, John Wiley & Sons, Weinheim, 2008 |
| 3 | Chen Y. Q., Hong T. T., Wang S. R., Mo J., Tian T., Zhou X., Chem. Soc. Rev., 2017, 46(10), 2844—2872 |
| 4 | Jaenisch R., Bird A., Nat. Genet., 2003, 33, 245—254 |
| 5 | Dai Y., Yuan B. F., Feng Y. Q., RSC Chem. Biol., 2021, 2(4), 1096—1114 |
| 6 | Sood A. J., Viner C., Hoffman M. M., J. Cheminform., 2019, 11, 30 |
| 7 | Heyn H., Esteller M., Cell, 2015, 161(4), 710—713 |
| 8 | Kallen R. G., Simon M., Marmur J., J. Mol. Biol., 1962, 5, 248—250 |
| 9 | Pfaffeneder T., Spada F., Wagner M., Brandmayr C., Laube S. K., Eisen D., Truss M., Steinbacher J., Hackner B., Kotljarova O., Schuermann D., Michalakis S., Kosmatchev O., Schiesser S., Steigenberger B., Raddaoui N., Kashiwazaki G., Muller U., Spruijt C. G., Vermeulen M., Leonhardt H., Schar P., Muller M., Carell T., Nat. Chem. Biol., 2014, 10(7), 574—581 |
| 10 | Musheev M. U., Baumgartner A., Krebs L., Niehrs C., Nat. Chem. Biol., 2020, 16(6), 630—634 |
| 11 | Portela A., Esteller M., Nat. Biotechnol., 2010, 28(10), 1057—1568 |
| 12 | Goelz S. E., Vogelstein B., Hamilton S. R., Feinberg A. P., Science, 1985, 228(4696), 187—190 |
| 13 | Lehn J. M., Angew. Chem. Int. Ed. Engl., 1988, 27(1), 89—112 |
| 14 | Lehn J. M., Science, 1993, 260(5115), 1762—1763 |
| 15 | Zhou J., Li J., Du X. W., Xu B., Biomaterials, 2017, 129, 1—27 |
| 16 | Aldaye F. A., Sleiman H. F., Pure and Applied Chemistry, 2009, 81(12), 2157—2181 |
| 17 | McLaughlin C. K., Hamblin G. D., Sleiman H. F., Chem. Soc. Rev., 2011, 40(12), 5647—5656 |
| 18 | Wang S. R., Song Y. Y., Wei L., Liu C. X., Fu B. S., Wang J. Q., Yang X. R., Liu Y. N., Liu S. M., Tian T., Zhou X., J. Am. Chem. Soc., 2017, 139(46), 16903—16912 |
| 19 | Wagner M., Steinbacher J., KrausT. F. J., Michalakis S., Hackner B., Pfaffeneder T., Perera A., Muller M., Giese A., Kretzschmar H. A., Carell T., Angew. Chem. Int. Ed. Engl., 2015, 54(42), 12511—12514 |
| 20 | Bachman M., Uribe⁃Lewis S., Yang X. P., Burgess H. E., Iurlaro M., Reik W., Murrell A., Balasubramanian S., Nat. Chem. Biol., 2015, 11(8), 555—557 |
| 21 | Pfaffeneder T., Hackner B., Truss M., Munzel M., Muller M., Deiml C. A., Hagemeier C., Carell T., Angew. Chem. Int. Ed. Engl., 2011, 50(31), 7008—7012 |
| 22 | Song C. X., He C., Trends Biochem. Sci., 2013, 38(10), 480—484 |
| 23 | Kellinger M. W., Song C. X., Chong J., Lu X. Y., He C., Wang D., Nat. Struct. Mol. Biol., 2012, 19(8), 831—833 |
| 24 | Isaacs L., Acc. Chem. Res., 2014, 47(7), 2052—2062 |
| 25 | Murray J., Kim K., Ogoshi T., Yao W., Gibb B. C., Chem. Soc. Rev., 2017, 46(9), 2479—2496 |
| 26 | Liu S. M., Ruspic C., Mukhopadhyay P., Chakrabarti S., Zavalij P. Y., Isaacs L., J. Am. Chem. Soc., 2005, 127(45), 15959—15967 |
| 27 | Barrow S. J., Kasera S., Rowland M. J., del Barrio J., Scherman O. A., Chem. Rev., 2015, 115(22), 12320—12406 |
| 28 | Tonga G. Y., Jeong Y., Duncan B., Mizuhara T., Mout R., Das R., Kim S. T., Yeh Y. C., Yan B., Hou S., Rotello V. M., Nat. Chem., 2015, 7(7), 597—603 |
| 29 | Li Q. L., Sun Y., Sun Y. L., Wen J. J., Zhou Y., Bing Q. M., Isaacs L. D., Jin Y. H., Gao H., Yang Y. W., Chem. Mater., 2014, 26(22), 6418—6431 |
| 30 | Shetty D., Khedkar J. K., Park K. M., Kim K., Chem. Soc. Rev., 2015, 44(23), 8747—8761 |
| 31 | Cao L. P., Sekutor M., Zavalij P. Y., Mlinaric⁃Majerski K., Glaser R., Isaacs L., Angew. Chem. Int. Ed. Engl., 2014, 53(4), 988—993 |
| 32 | Liu K., Liu Y. L., Yao Y. X., Yuan H. X., Wang S., Wang Z. Q.,Zhang X., Angew. Chem. Int. Ed. Engl., 2013, 52(32), 8285—8289 |
| 33 | Lee D. W., Park K. M., Banerjee M., Ha S. H., Lee T., Suh K., Paul S., Jung H., Kim J., Selvapalam N., Ryu S. H., Kim K., Nat. Chem., 2011, 3(2), 154—159 |
| 34 | Bhasikuttan A. C., Mohanty J., Nau W. M., Pal H., Angew. Chem. Int. Ed. Engl., 2007, 46(22), 4120—4122 |
| 35 | Wang S. R., Wang J. Q., Fu B. S., Chen K., Xiong W., Wei L., Qing G. Y., Tian T., Zhou X., J. Am. Chem. Soc., 2018, 140(46), 15842—15849 |
| 36 | Ji S. F., Fu I., Naldiga S., Shao H. Z., Basu A. K., Broyde S., Tretyakova N. Y., Nucleic Acids Res., 2018, 46(13), 6455—6469 |
| 37 | Li F. C., Zhang Y. Q., Bai J., Greenberg M. M., Xi Z., Zhou C. Z., J. Am. Chem. Soc., 2017, 139(31), 10617—10620 |
| 38 | Zeng T., Liu L., Li T., Li Y. R., Gao J., Zhao Y. L., Wu H. C., Chem. Sci., 2015, 6(10), 5628—5634 |
| 39 | Esteller M., Oncogene, 2002, 21(35), 5427—5440 |
| 40 | Branco M. R., Ficz G., Reik W., Nat. Rev. Genet., 2012, 13(1), 7—13 |
| 41 | Clarke J., Wu H. C., Jayasinghe L., Patel A., Reid S., Bayley H., Nat. Nanotechnol., 2009, 4(4), 265—270 |
| 42 | Liu L., Li Y. R., Li T., Xie J. I., Chen C. F., Liu Q. S., Zhang S. W., Wu H. C., Anal. Chem., 2016, 88(2), 1073—1077 |
| 43 | Hsu G. W., Ober M., Carell T., Beese L. S., Nature, 2004, 431(7005), 217—221 |
| 44 | Loft S., Danielsen P., Lohr M., Jantzen K., Hemmingsen J. G., Roursgaard M., Karotki D. G., Moller P., Arch. Biochem. Biophys., 2012, 518(2), 142—150 |
| 45 | Gao D. M., Chen J. H., Fang S., Ma T., Qiu X. H., Ma J. G., Gu Q. F., Cheng P., Matter, 2021, 4(3), 1001—1016 |
| 46 | Wu T. P., Wang T., Seetin M. G., Lai Y. Q., Zhu S. J., Lin K. X., Liu Y. F., Byrum S. D., Mackintosh S. G., Zhong M., Tackett A., Wang G. L., Hon L. S., Fang G., Swenberg J. A., Xiao A. Z., Nature, 2016, 532(7599), 329—333 |
| 47 | Xiao C. L., Zhu S., He M. H., Chen D., Zhang Q., Chen Y., Yu G. L., Liu J. B., Xie S. Q., Luo F., Liang Z., Wang D. P., Bo X. C., Gu X. F., Wang K.,Yan G. R., Mol. Cell, 2018, 71(2), 306—318 |
| 48 | Yang H. M., Ren J., Zhao M., Chen C., Wang F., Chen Z. L., Bioelectrochemistry, 2022, 146, 108111 |
| 49 | Adampourezare M., Saadati A., Hasanzadeh M., Dehghan G., Feizi M. H., J. Mol. Recognit., 2022, 35(2), e2945 |
| 50 | Irrera S., Ruiz⁃Hernandez S. E., Reggente M., Passeri D., Natali M., Gala F., Zollo G., Rossi M., Portalone G., Applied Surface Science, 2017, 407, 297—306 |
| [1] | 孙昕, 高明媚, 张泽, 王海燕, 于涵洋. 催化RNA切割反应的苏糖核酸酶的表征及在切割microRNA中的应用[J]. 高等学校化学学报, 2023, 44(3): 20220246. |
| [2] | 陈佳璐, 黄硕. 纳米孔测序技术在核酸修饰检测中的应用[J]. 高等学校化学学报, 2023, 44(3): 20220333. |
| [3] | 方鑫, 赵瑞奇, 莫婧, 王雅芬, 翁小成. 检测核酸表观遗传修饰的测序方法[J]. 高等学校化学学报, 2023, 44(3): 20220342. |
| [4] | 宋璐, 张舒阳, 王丽华, 左小磊, 李敏. 框架核酸高通量检测芯片[J]. 高等学校化学学报, 2023, 44(2): 20220563. |
| [5] | 王君旸, 刘争, 张茜, 孙春燕, 李红霞. DNA银纳米簇在功能核酸荧光生物传感器中的应用[J]. 高等学校化学学报, 2022, 43(6): 20220010. |
| [6] | 赵恒智, 余方志, 李翔菲, 李乐乐. 基于DNA与上转换纳米颗粒相结合的生物传感与成像研究进展[J]. 高等学校化学学报, 2022, 43(12): 20220626. |
| [7] | 赵雪琪, 赵越, 薛静, 白敏, 陈锋, 孙颖, 宋大千, 赵永席. 单细胞核酸编码扩增成像分析[J]. 高等学校化学学报, 2022, 43(12): 20220572. |
| [8] | 刘珂, 靳宇, 梁建功, 吴园. 化学修饰提高核酸适体结合亲和力的研究进展[J]. 高等学校化学学报, 2021, 42(11): 3477. |
| [9] | 张晓荣, 陈岚岚, 胡善文. 基于分子识别的细菌检测研究进展[J]. 高等学校化学学报, 2021, 42(11): 3468. |
| [10] | 吉采灵, 程兴, 谈洁, 袁荃. 功能化核酸适体的筛选及分子识别应用[J]. 高等学校化学学报, 2021, 42(11): 3457. |
| [11] | 黄玲, 庄梓健, 李翔, 石沐玲, 刘高强. 基于核酸适体的外泌体分子识别研究进展[J]. 高等学校化学学报, 2021, 42(11): 3493. |
| [12] | 胡灵, 殷垚, 柯国梁, 张晓兵. 基于DNA纳米结构的细胞间相互作用的调控[J]. 高等学校化学学报, 2021, 42(11): 3284. |
| [13] | 解忱, 陈娜, 杨雁冰, 袁荃. 核酸适体功能化的二维材料场效应晶体管传感器研究进展[J]. 高等学校化学学报, 2021, 42(11): 3406. |
| [14] | 赵卓, 王雪强. 核酸适体偶联药物的生物偶联构建技术与应用[J]. 高等学校化学学报, 2021, 42(11): 3367. |
| [15] | 刘学娇, 杨帆, 刘爽, 张春娟, 刘巧玲. 核酸适体靶向的膜蛋白识别与功能调控研究进展[J]. 高等学校化学学报, 2021, 42(11): 3277. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||