

高等学校化学学报 ›› 2023, Vol. 44 ›› Issue (2): 20220500.doi: 10.7503/cjcu20220500
沈琦1, 陈海瑶1, 高登辉1, 赵熹1( ), 那日松2, 刘佳2, 黄旭日1
), 那日松2, 刘佳2, 黄旭日1
收稿日期:2022-07-25
出版日期:2023-02-10
发布日期:2022-10-04
通讯作者:
赵熹
E-mail:zhaoxi@jlu.edu.cn
基金资助:
SHEN Qi1, CHEN Haiyao1, GAO Denghui1, ZHAO Xi1( ), NA Risong2, LIU Jia2, HUANG Xuri1
), NA Risong2, LIU Jia2, HUANG Xuri1
Received:2022-07-25
Online:2023-02-10
Published:2022-10-04
Contact:
ZHAO Xi
E-mail:zhaoxi@jlu.edu.cn
Supported by:摘要:
通过分子动力学模拟、 伞形采样模拟、 结合自由能计算和分子对接等方法, 研究了法卡林二醇在γ-氨基丁酸A型(GABAA)受体上结合作用的模式和对GABAA受体动态属性的影响, 确定了3个有效结合位点均对此受体产生拮抗作用, 为后续研究聚乙炔醇类化合物对GABAA受体作用及相应药物开发提供了理论依据.
中图分类号:
TrendMD:
沈琦, 陈海瑶, 高登辉, 赵熹, 那日松, 刘佳, 黄旭日. 天然产物法卡林二醇与人类GABAA受体相互作用的机制. 高等学校化学学报, 2023, 44(2): 20220500.
SHEN Qi, CHEN Haiyao, GAO Denghui, ZHAO Xi, NA Risong, LIU Jia, HUANG Xuri. Interaction Mechanism of the Natural Product Falcarindiol and Human GABAA Receptor. Chem. J. Chinese Universities, 2023, 44(2): 20220500.
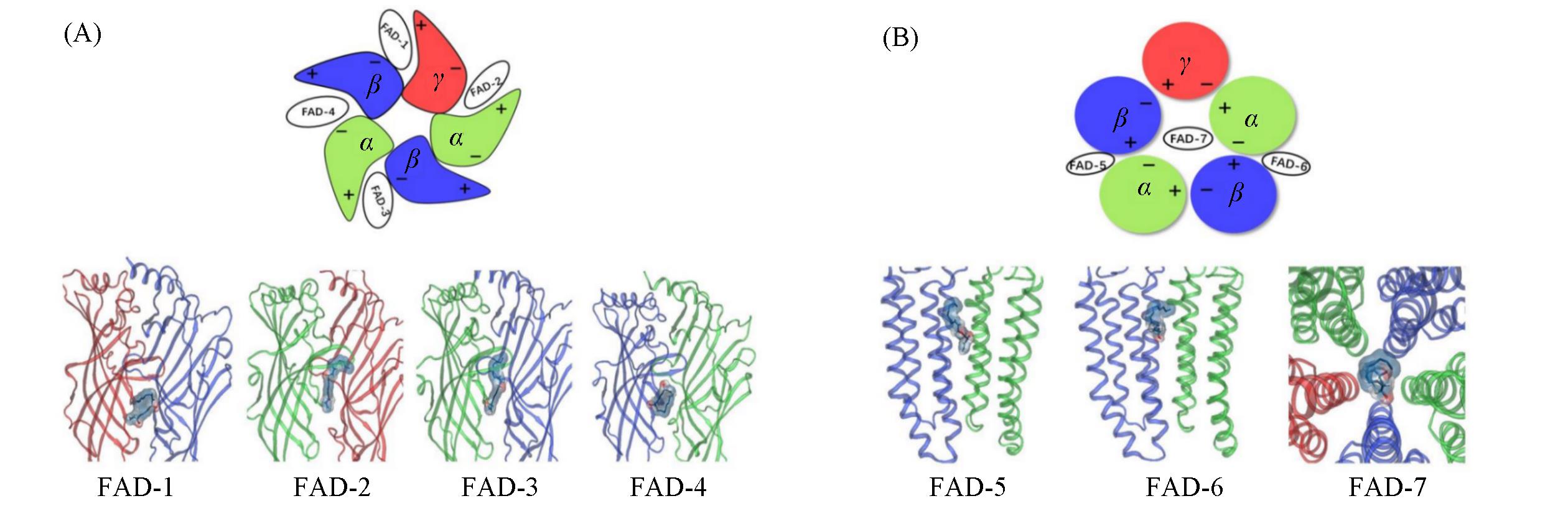
Fig.1 Seven sites of falcarindiol binding to GABAA receptors(A) The four sites of the extracellular structural domain FAD-1—FAD-4; (B) three sites in the transmembrane structural domain FAD-5—FAD-7.
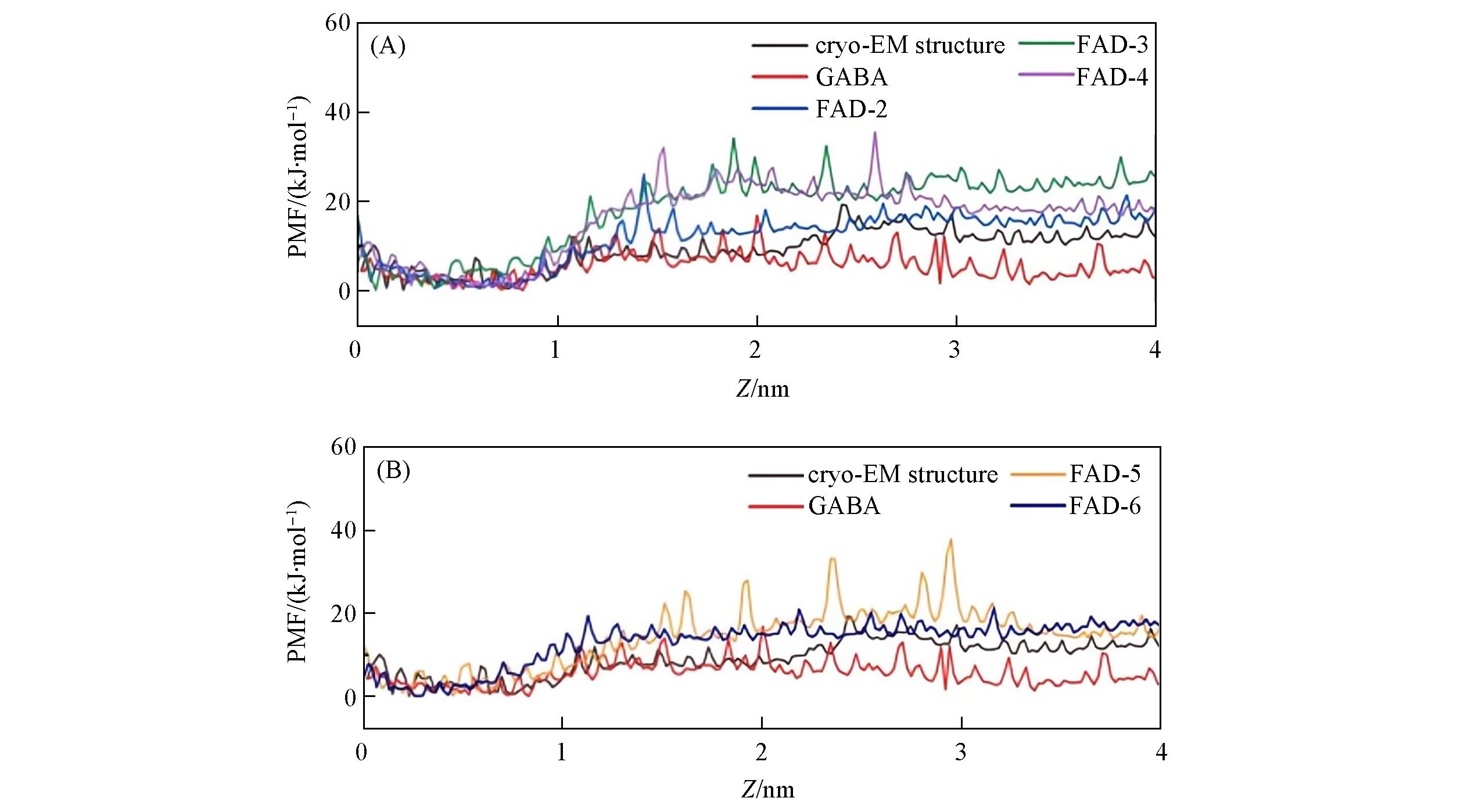
Fig.4 Calculated PMF of chloride ions through GABAA receptor helical channels of FAD⁃2—FAD⁃4 GABAA protein and GABA⁃only molecular complexes(A) and FAD⁃5—FAD⁃6 GABAA protein and GABA⁃only molecular complexes(B)cryo⁃EM structure: Cryo⁃electron microscopy structure of GABAA.
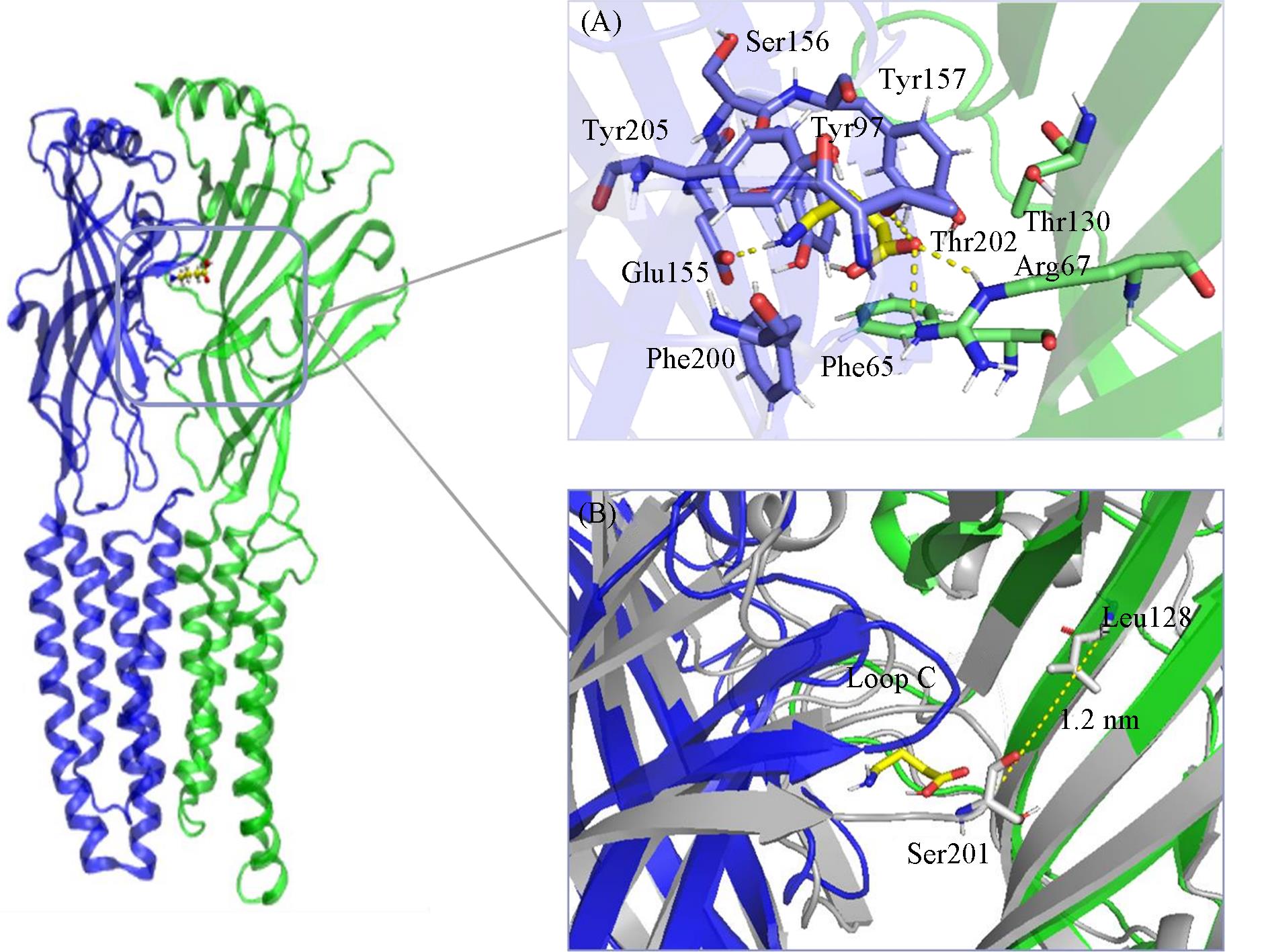
Fig.5 Interaction of GABA and surrounding amino acids at site 2(A) Interaction of GABA and surrounding amino acids at site 2; (B) The distance between the residue Ser201 Ca atom on the β-subunit loop C and the α-subunit Leu128 Ca atom is 1.2 nm. Subunits containing only GABA molecules are in gray, subunits containing falcarindiol molecules are in color.
| Site | GABA | FAD⁃2 | FAD⁃3 | FAD⁃4 | FAD⁃5 | FAD⁃6 | FAD⁃7 |
|---|---|---|---|---|---|---|---|
| 1 | 30 ns | 10 ns | 5 ns | 80 ns | 20 ns | 50 ns | 5 ns |
| 2 | 200 ns | 30 ns | 15 ns | 105 ns | 50 ns | 100 ns | 8 ns |
Table 1 GABA and FAD-2—FAD-6 GABA molecular residence time
| Site | GABA | FAD⁃2 | FAD⁃3 | FAD⁃4 | FAD⁃5 | FAD⁃6 | FAD⁃7 |
|---|---|---|---|---|---|---|---|
| 1 | 30 ns | 10 ns | 5 ns | 80 ns | 20 ns | 50 ns | 5 ns |
| 2 | 200 ns | 30 ns | 15 ns | 105 ns | 50 ns | 100 ns | 8 ns |
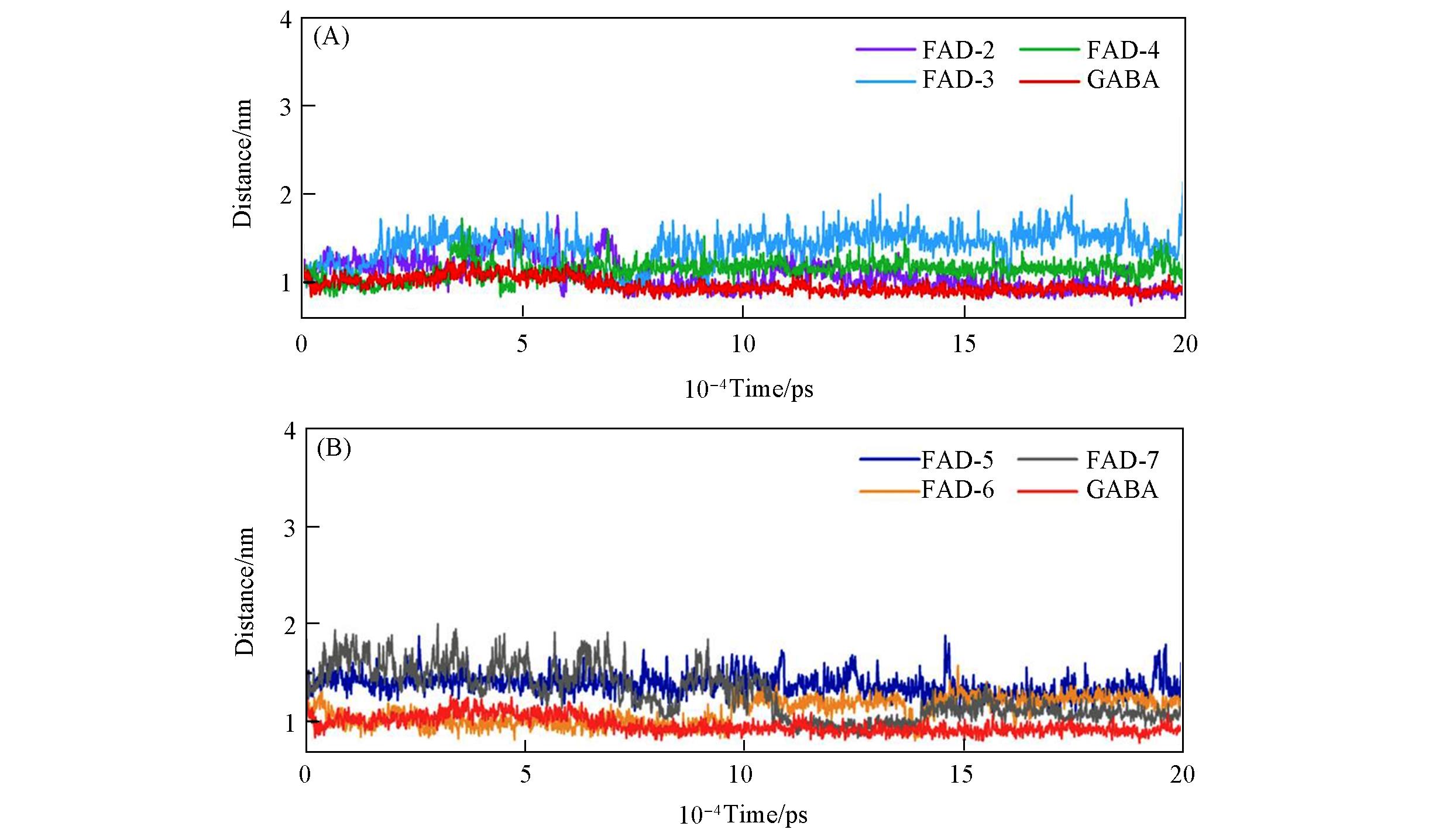
Fig.6 Distance between the CA atom of residue Ser201 on the β2 subunit Loop C and the CA atom of residue Leu128 on the α1 subunit at site 2 of the GABA molecule over time(A) FAD-2—FAD-4 and GABA; (B) FAD-5—FAD-7 and GABA.
| Species | ∆Eele/ (kJ·mol-1) | ∆Evdw/ (kJ·mol-1) | ∆GPB/ (kJ·mol-1) | ∆GSA/ (kJ·mol-1) | ∆Gpolar/ (kJ·mol-1) | ∆Gnonpolar/ (kJ·mol-1) | T∆S/ (kJ·mol-1) | ∆Gbind/ (kJ·mol-1) |
|---|---|---|---|---|---|---|---|---|
| FAD⁃1(γ2+/β2-) | -118.378 | -99.604 | 173.117 | -20.974 | 54.739 | -120.579 | 51.534 | -14.305 |
| FAD⁃2(α1+/γ2-) | -101.399 | -153.113 | 168.678 | -22.192 | 67.279 | -174.176 | 27.221 | -80.806 |
| FAD⁃3(α1+/β2-) | -120.052 | -125.934 | 197.071 | -21.564 | 77.019 | -147.499 | 16.983 | -53.497 |
| FAD⁃4(β2+/α1-) | -159.712 | -101.604 | 223.961 | -20.456 | 64.250 | -122.060 | 12.631 | -45.179 |
| FAD⁃5(β2+/α1-) | -64.283 | -167.406 | 115.817 | -22.903 | 51.534 | -190.309 | 19.761 | -119.014 |
| FAD⁃6(β2+/α1-) | -31.275 | -150.114 | 95.374 | -23.242 | 64.099 | -173.356 | 9.033 | -100.224 |
| FAD⁃7(Pore) | -31.966 | -160.561 | 81.220 | -22.782 | 49.254 | -183.340 | 12.602 | -121.487 |
Table 2 Free energy of falcarindiol binding at FAD-1—FAD-7 sites on the GABAA receptor*
| Species | ∆Eele/ (kJ·mol-1) | ∆Evdw/ (kJ·mol-1) | ∆GPB/ (kJ·mol-1) | ∆GSA/ (kJ·mol-1) | ∆Gpolar/ (kJ·mol-1) | ∆Gnonpolar/ (kJ·mol-1) | T∆S/ (kJ·mol-1) | ∆Gbind/ (kJ·mol-1) |
|---|---|---|---|---|---|---|---|---|
| FAD⁃1(γ2+/β2-) | -118.378 | -99.604 | 173.117 | -20.974 | 54.739 | -120.579 | 51.534 | -14.305 |
| FAD⁃2(α1+/γ2-) | -101.399 | -153.113 | 168.678 | -22.192 | 67.279 | -174.176 | 27.221 | -80.806 |
| FAD⁃3(α1+/β2-) | -120.052 | -125.934 | 197.071 | -21.564 | 77.019 | -147.499 | 16.983 | -53.497 |
| FAD⁃4(β2+/α1-) | -159.712 | -101.604 | 223.961 | -20.456 | 64.250 | -122.060 | 12.631 | -45.179 |
| FAD⁃5(β2+/α1-) | -64.283 | -167.406 | 115.817 | -22.903 | 51.534 | -190.309 | 19.761 | -119.014 |
| FAD⁃6(β2+/α1-) | -31.275 | -150.114 | 95.374 | -23.242 | 64.099 | -173.356 | 9.033 | -100.224 |
| FAD⁃7(Pore) | -31.966 | -160.561 | 81.220 | -22.782 | 49.254 | -183.340 | 12.602 | -121.487 |
| 1 | Hsu Y. T., Chang Y. G., Chern Y., Roy. Soc. Open Biol., 2018, 8(12), 180165 |
| 2 | O’Gorman Tuura R. L., Baumann C. R., Baumann⁃Vogel H., Parkinsonism Relat. D, 2018, 54—60 |
| 3 | Dutar P., Villette V., Curr. Alzheimer Res., 2017, 14(1), 30—39 |
| 4 | Garret M., Du Z., Chazalon M., Cho Y. H., Baufreton J., CNS Neurosci. Ther., 2018,292—300 |
| 5 | Takács V. T., Cserép C., Schlingloff D., Pósfai B., Szőnyi A., Sos K. E., Környei Z., Dénes Á., Gulyás A. I., Freund T. F., Nyiri G., Nat. Commun., 2018, 9(1), 2848 |
| 6 | Olsen R. W., Sieghart W., Neuropharmacology, 2009, 56(1), 141—148 |
| 7 | Scott S., Aricescu A. R., Curr. Opin. Struc. Biol., 2019, 54, 189—197 |
| 8 | Miller P. S., Aricescu A. R., Nature, 2014, 512(7514), 270—275 |
| 9 | Masiulis S., Desai R., Uchański T., Uchański T., Martin I. S., Laverty D., Karia D., Malinauskas T., Zivanov J., Pardon E., Kotecha A., Steyaert J., Miller K. W., Aricescu A. R., Nature, 2019, 565(7740), 454—459 |
| 10 | Adamiker D., Hoger H., Fuchs K., Ebert V., Tretter V., Jechlinger M., Sieghart W., Neurochem. Int., 1999, 34(5), 379—385 |
| 11 | Sieghart W., Adv. Pharmacol., 2015, 72, 53—96 |
| 12 | Jansen M., Nature, 2019, 565(7740), 436—438 |
| 13 | Zhu S., Noviello C. M., Teng J., Walsh Richard M. Jr., Kim J., Hibbs R., Nature, 2018, 559(7712), 67—72 |
| 14 | Luscher B., Fuchs T., Kilpatrick C. L., Neuron, 2011, 70(3), 385—409 |
| 15 | Lee M. R., Dukan E., Milne I., J. Roy. Coll. Phys. Edinb., 2020, 50(1), 80—86 |
| 16 | Minto R. E., Blacklock B. J., Prog. Lipid Res., 2008, 47(4), 233—306 |
| 17 | Leung W., Zheng H., Huen M., Law S., Xue H., Prog. Neuro⁃Psychoph., 2003, 27(5), 775—779 |
| 18 | Halbsguth C., Meissner O., Hberlein H., Planta Med., 2003, 69(4), 305—309 |
| 19 | Zaugg J., Baburin I., Strommer B., Kim H., Hering S., J. Nat. Prod., 2010, 73(2), 185—191 |
| 20 | Leidenheimer B., Neuropharmacology, 1998, 383—390 |
| 21 | Alali F. Q., El⁃Elimat T., Li C., Qandil A., Alkofahi A., Tawaha K., Burgess J. P., Nakanishi Y., Kroll D. J., Navarro H. A., J. Nat. Prod., 2005, 68(2), 173—178 |
| 22 | Uwai K., Ohashi K., Takaya Y., Ohta T., Tadano T., Kisara K., Shibusawa K., Sakakibara R., Oshima Y., J. Med. Chem., 2000, 43(23), 4508—4515 |
| 23 | Kessler A., Sahin⁃Nadeem H., Lummis S., Weigel I., Villmann C., Mol. Nutr. Food Res., 2014, 58(4), 851—862 |
| 24 | Zhao X. Y., Wang Y., Li Y., Chen X. Q., Yang H. H., Yue J. M., Hu G. Y., Neurosci. Lett., 2003, 337(1), 33—36 |
| 25 | Eder C., Schupp P., Proksch P., Wray V., Steube K., Müller C. E., Frobenius W., Herderich M., Soest R. W., J. Nat. Prod., 1998, 61(2), 301—305 |
| 26 | Jin H. R., Zhao J., Zhang Z., Liao Y., Wang C. Z., Huang W. H., Li S. P., He T. C., Yuan C. S., Du W., Cell Death Dis., 2012, 3(8), e376 |
| 27 | Kobaek⁃Larsen M., Notabi M. K., El⁃Houri R. B., Christensen L. P., Al⁃Najami I., Fretté X., Baatrup G., Nutrients, 2019, 11(9), 2223 |
| 28 | Frisch M. J., Trucks G. W., Schlegel J., Scuseria G. E., Robb M. A., Cheeseman J. R., Schlegel H. B., Scalmani G., Barone V., Mennucci B., Petersson G. A., Nakatsuji H., Caricato M., Li X., Hratchian H. P., Izmaylov A. F., Bloino J., Zheng G., Sonnenberg J. L., Hada M., Ehara M., Toyota K., Fukuda R., Hasegawa J., Ishida M., Nakajima T., Honda Y., Kitao O., Nakai H., Vreven T., Montgomery J. A. Jr., Peralta J. E., Ogliaro F., Bearpark M., Heyd J. J., Brothers E., Kudin K. N., Staroverov V. N., Kobayashi R., Normand J., Raghavachari K., Rendell A., Burant J. C., Iyengar S. S., Tomasi J., Cossi M., Rega N., Millam N. J., Klene M., Knox J. E., Cross J. B., Bakken V., Adamo C., Jaramillo J., Gomperts R., Stratmann R. E., Yazyev O., Austin A. J., Cammi R., Pomelli C., Ochterski J. W., Martin R. L., Morokuma K., Zakrzewski V. G., Voth G. A., Salvador P., Dannenberg J. J., Dapprich S., Daniels A. D., Farkas Ö., Foresman J. B., Ortiz J. V., Cioslowski J., Fox D. J., Gaussian 09, Revision A.1, Gaussian Inc., Wallingford CT, 2009 |
| 29 | Kozakov D., Grove L. E., Hall D. R., Bohnuud T., Mottarella S., Luo L., Xia B., Beglov D., Vajda S., Nat. Protoc., 2015, 10(5), 733—755 |
| 30 | Trott O., Olson A. J., Trott O., Olson A. J., J. Comput. Chem., 2009, 31(2), 455—461 |
| 31 | Olsson M. H. M., Søndergaard C. R., Rostkowski M., Jensen J. H., J. Chem. Theory. Comput., 2011, 7(2), 525—537 |
| 32 | Schmidt T. H., Kandt C., J. Chem. Inf. Model., 2012, 52(10), 2657—2669 |
| 33 | Schmid N., Eichenberger A. P., Choutko A., Riniker S., Winger M., Mark A. E., Gunsteren W. F. V., Eur. Biophys. J., 2011, 40(7), 843—856 |
| 34 | Hess B., Bekker H., Berendsen H. J., Fraaije J. G., J. Comput. Chem., 1997, 18(12), 1463—1472 |
| 35 | Darden T., York D., Pedersen L., J. Chem. Phys., 1993, 98(12), 10089—10092 |
| 36 | Kutzner C., Páll S., Fechner M., Esztermann A., Groot B., Grubmüller H., J. Comput. Chem., 2019, 40(27), 2418—2431 |
| 37 | Humphrey W., Dalke A., Schulten K., J. Mol. Graphics, 1996, 14(1), 33—38 |
| 38 | Delano W. L., Proteins., 2002, 30, 442—454 |
| 39 | Alpeshkumar K. M., J. Chem. Theory. Comput., 2011, 7(12), 4026—4037 |
| 40 | Haefely W. E., Eur. Arch. Psy. N., 1989, 238(5/6), 294—301 |
| 41 | Wei W., J. Neurosci., 2004, 24(38), 8379—8382 |
| 42 | Li G. D., Chiara D. C., Cohen J. B., J. Biol. Chem., 2010, 285(12), 8615—8620 |
| 43 | Maldifassi M. C., Baur R., Sigel E., Neuropharmacology, 2016, 105, 207—214 |
| 44 | Ticku M. K., Olsen R. W., Brain Res. Bull., 1980, 5, 213—216 |
| 45 | Mortensen M., Patel B., Smart T., Front. Cell. Neurosci., 2012, 6, 1 |
| 46 | Valdés⁃Tresanco M. S., Valdés⁃Tresanco M. E., Valiente P. A., Moreno E., J. Chem. Theory. Comput., 2021, 17(10), 6281—6291 |
| 47 | Elgarf A. A., Siebert D. C. B., Steudle F., Draxler A., Li G., Huang S., Cook J. M., Ernst M., Scholze P., ACS Chem. Biol., 2018, 13(8), 2033—2039 |
| 48 | Baumann S. W., Baur R., Sigel E., J. Neurosci., 2003, 23(35), 11158—11166 |
| 49 | Grant B. J., Rodrigues A. P., Elsawy K. M., McCammon J. A., Caves L. S. D., Bioinformatics, 2006, 22(21), 2695—2696 |
| [1] | 李吉辰, 蔡珊珊, 彭巨擘, 李宏飞, 段晓征. 电场下离子型聚合物复合囊泡结构变化的分子动力学模拟[J]. 高等学校化学学报, 2023, 44(2): 20220553. |
| [2] | 高志伟, 李军委, 史赛, 付强, 贾钧儒, 安海龙. 基于分子动力学模拟的TRPM8通道门控特性分析[J]. 高等学校化学学报, 2022, 43(6): 20220080. |
| [3] | 胡波, 朱昊辰. 双层氧化石墨烯纳米体系中受限水的介电常数[J]. 高等学校化学学报, 2022, 43(2): 20210614. |
| [4] | 雷晓彤, 金怡卿, 孟烜宇. 基于分子模拟方法预测PIP2在双孔钾通道TREK-1上结合位点的研究[J]. 高等学校化学学报, 2021, 42(8): 2550. |
| [5] | 李聪聪, 刘明皓, 韩佳睿, 朱镜璇, 韩葳葳, 李婉南. 基于分子动力学模拟的VmoLac非特异性底物催化活性的理论研究[J]. 高等学校化学学报, 2021, 42(8): 2518. |
| [6] | 曾永辉, 言天英. 质子水合结构的振动态密度分析[J]. 高等学校化学学报, 2021, 42(6): 1855. |
| [7] | 刘爱清, 徐文生, 徐晓雷, 陈继忠, 安立佳. 高分子/棒状纳米粒子复合物的分子动力学模拟[J]. 高等学校化学学报, 2021, 42(3): 875. |
| [8] | 齐人睿, 李明昊, 常浩, 付学奇, 高波, 韩葳葳, 韩璐, 李婉南. 基于拉伸分子动力学模拟的黄嘌呤氧化酶抑制剂解离途径的理论研究[J]. 高等学校化学学报, 2021, 42(3): 758. |
| [9] | 瞿思颖, 徐沁. 凝血因子Xa的S4口袋部分关键残基对利伐沙班结合的不同作用机制[J]. 高等学校化学学报, 2019, 40(9): 1918. |
| [10] | 马玉聪, 樊保民, 王满曼, 杨彪, 郝华, 孙辉, 张慧娟. 曲唑酮的两步法制备及对碳钢的缓蚀机理[J]. 高等学校化学学报, 2019, 40(8): 1706. |
| [11] | 孙浩帆, 张凌怡, PATRICKNorman, 张维冰. 二芳基乙烯衍生物与DNA结合的分子动力学研究[J]. 高等学校化学学报, 2019, 40(6): 1229. |
| [12] | 张璋, 王栋, 王晓雷, 徐岩. 华根霉脂肪酶有机相酯合成活性的重塑[J]. 高等学校化学学报, 2019, 40(4): 747. |
| [13] | 马兰, 容婧婧, 朱有亮, 黄以能, 孙昭艳. 软胶体粒子形成束晶的动力学模拟[J]. 高等学校化学学报, 2019, 40(1): 195. |
| [14] | 朱镜璇, 于正飞, 刘野, 詹冬玲, 韩佳睿, 田晓翩, 韩葳葳. 基于分子动力学模拟提高嗜热磷酸三酯酶样内酯酶非特异性底物活力的理论研究[J]. 高等学校化学学报, 2019, 40(1): 138. |
| [15] | 吴红枚, 李惠婷, 李永成, 王宏青, 王孟. 基于基团贡献法和分子动力学预测聚间苯二甲酰对苯二胺的玻璃化转变温度[J]. 高等学校化学学报, 2019, 40(1): 180. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||