

高等学校化学学报 ›› 2021, Vol. 42 ›› Issue (11): 3445.doi: 10.7503/cjcu20210450
收稿日期:2021-06-30
出版日期:2021-11-10
发布日期:2021-11-10
通讯作者:
郑磊
E-mail:maoyu@hfut.edu.cn;lei.zheng@aliyun.com
作者简介:毛 瑜, 女, 博士, 副研究员, 主要从事功能核酸方面的研究. E-mail: 基金资助:Received:2021-06-30
Online:2021-11-10
Published:2021-11-10
Contact:
ZHENG Lei
E-mail:maoyu@hfut.edu.cn;lei.zheng@aliyun.com
Supported by:摘要:
脱氧核酶是通过体外筛选技术得到的具有催化功能的单链寡核苷酸分子. 随着体外筛选技术的发展, 越来越多的脱氧核酶被筛选出来. 其中, 靶向细菌的具有RNA切割作用的脱氧核酶(RNA-cleaving DNAzyme, RCD)同时拥有分子识别和催化RNA裂解的功能, 且具有设计灵活、 易于制备和修饰、 成本低廉等优势, 在致病菌检测领域获得了广泛的关注和应用, 为致病菌的早期发现和预防提供了全新的分子工具. 本文系统总结了RCD在致病菌检测中的研究和应用, 并对其面临的问题和未来发展前景进行了展望.
中图分类号:
TrendMD:
毛瑜, 瞿昊, 郑磊. RNA切割型脱氧核酶在致病菌检测中的研究进展. 高等学校化学学报, 2021, 42(11): 3445.
MAO Yu, QU Hao, ZHENG Lei. Research Progress on RNA⁃cleaving DNAzyme for the Detection of Pathogenic Bacteria. Chem. J. Chinese Universities, 2021, 42(11): 3445.
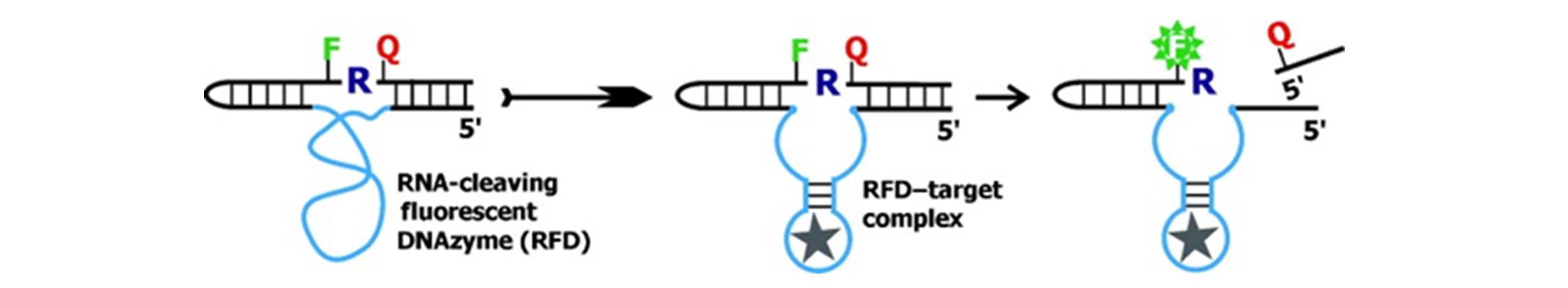
Fig.3 Conceptual design of fluorescent DNAzymes fluorescing upon contact with the CEM produced by living bacterial cells[38]F=fluorescein?dT, Q=dabcyl?dT, R=adenosine ribonucleotide. Copyright 2011, Wiley?VCH.
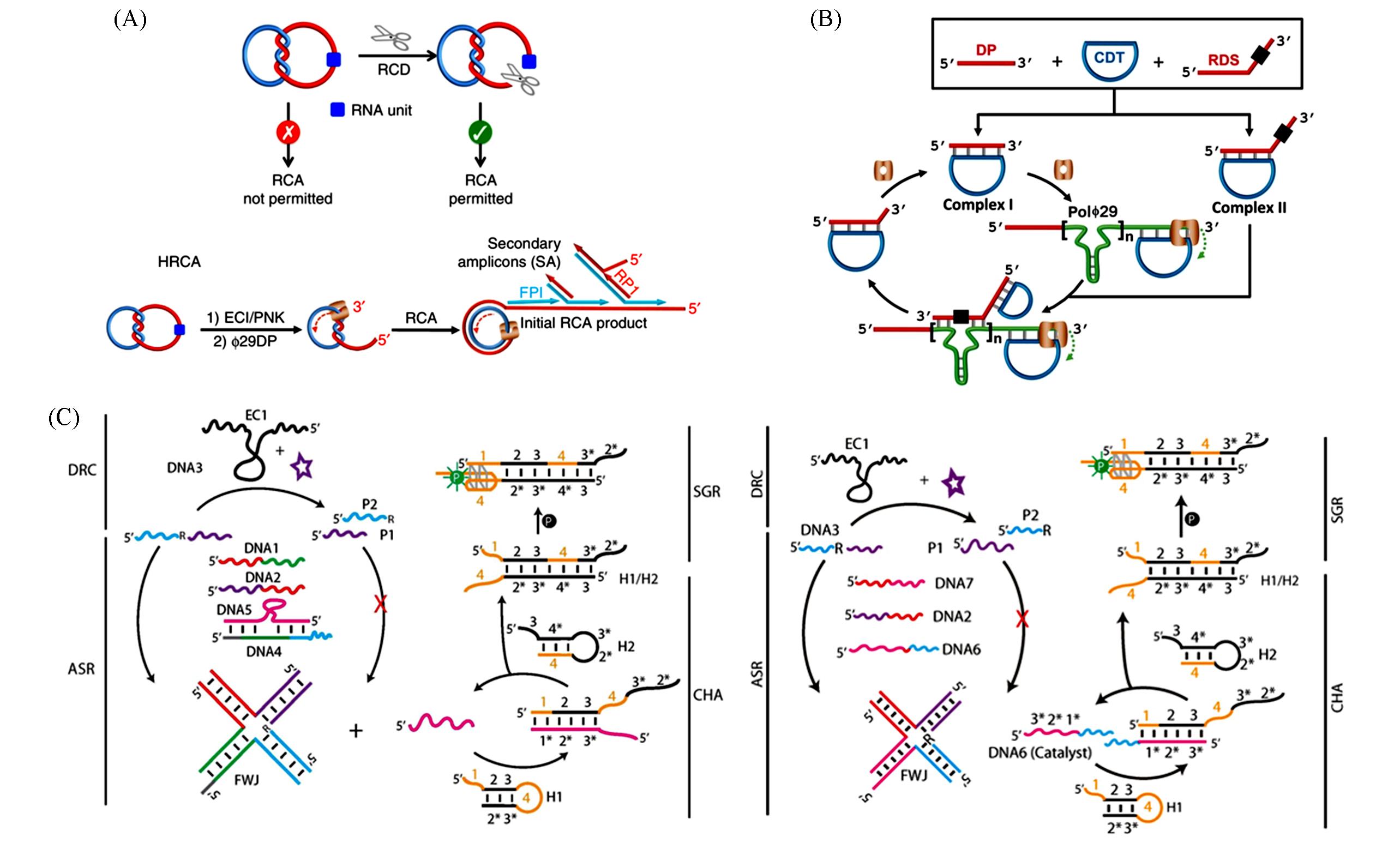
Fig.6 DNAzyme sensors coupled with isothermal amplification strategies for bacteria detection(A) Schematic illustration of a DNA catenane biosensor[68], Copyright 2016, Springer Nature; (B) schematic illustration of the DNAzyme feedback amplification[69], Copyright 2017, Wiley?VCH; (C) schematic illustration of an All?DNA biosensing system[70], Copyright 2020, Wiley?VCH.
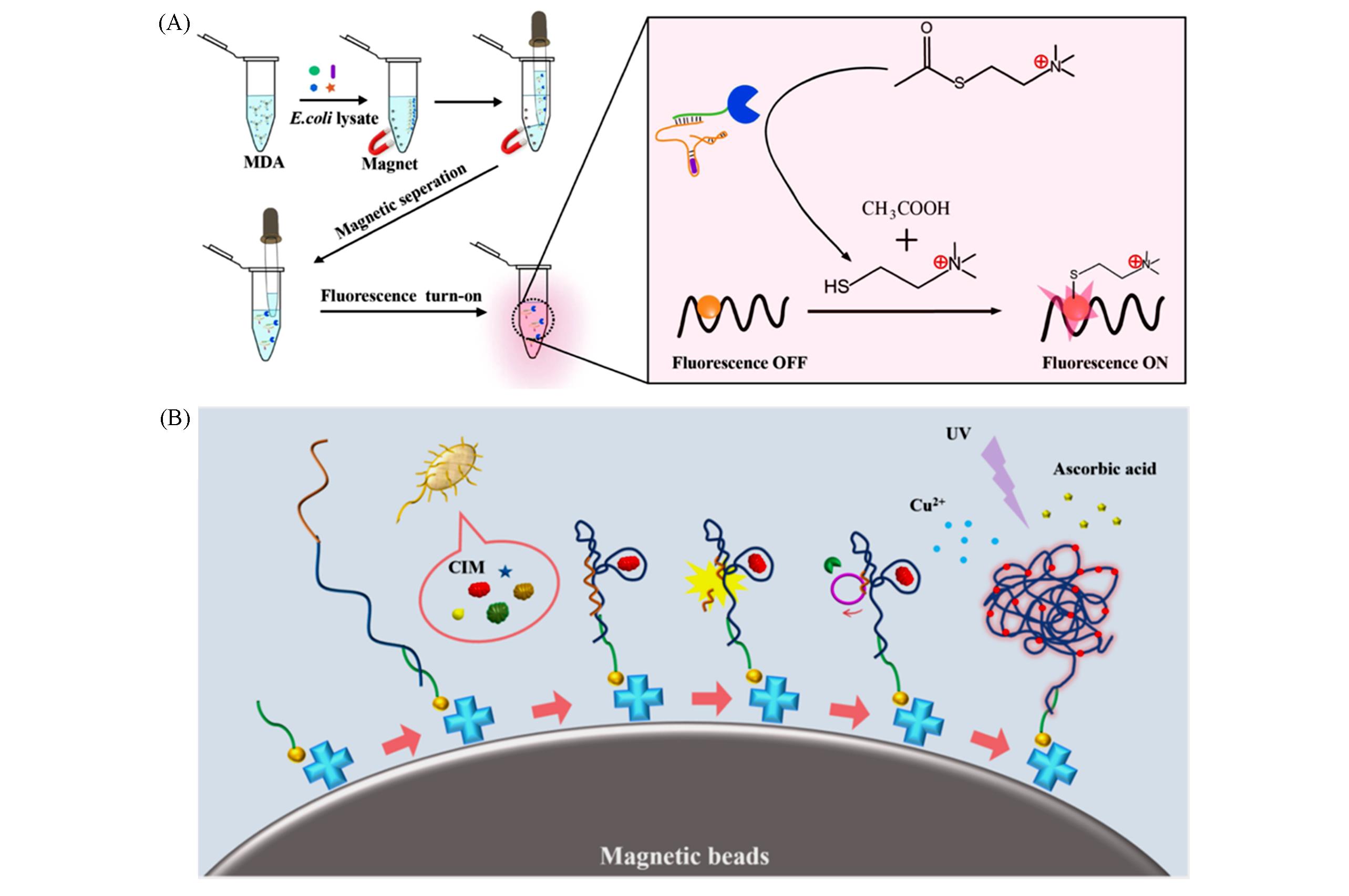
Fig.7 DNAzyme?based fluorescent sensors for bacteria detection(A) Schematic representation of DNA?templated fluorescent silver nanoclusters?based sensing system for E. coli detection[71], Copyright 2018, Elsevier; (B) magnetic DNAzyme?copper nanoclusters fluorescent biosensor for the detection of E. coli[72], Copyright 2020, Elsevier.
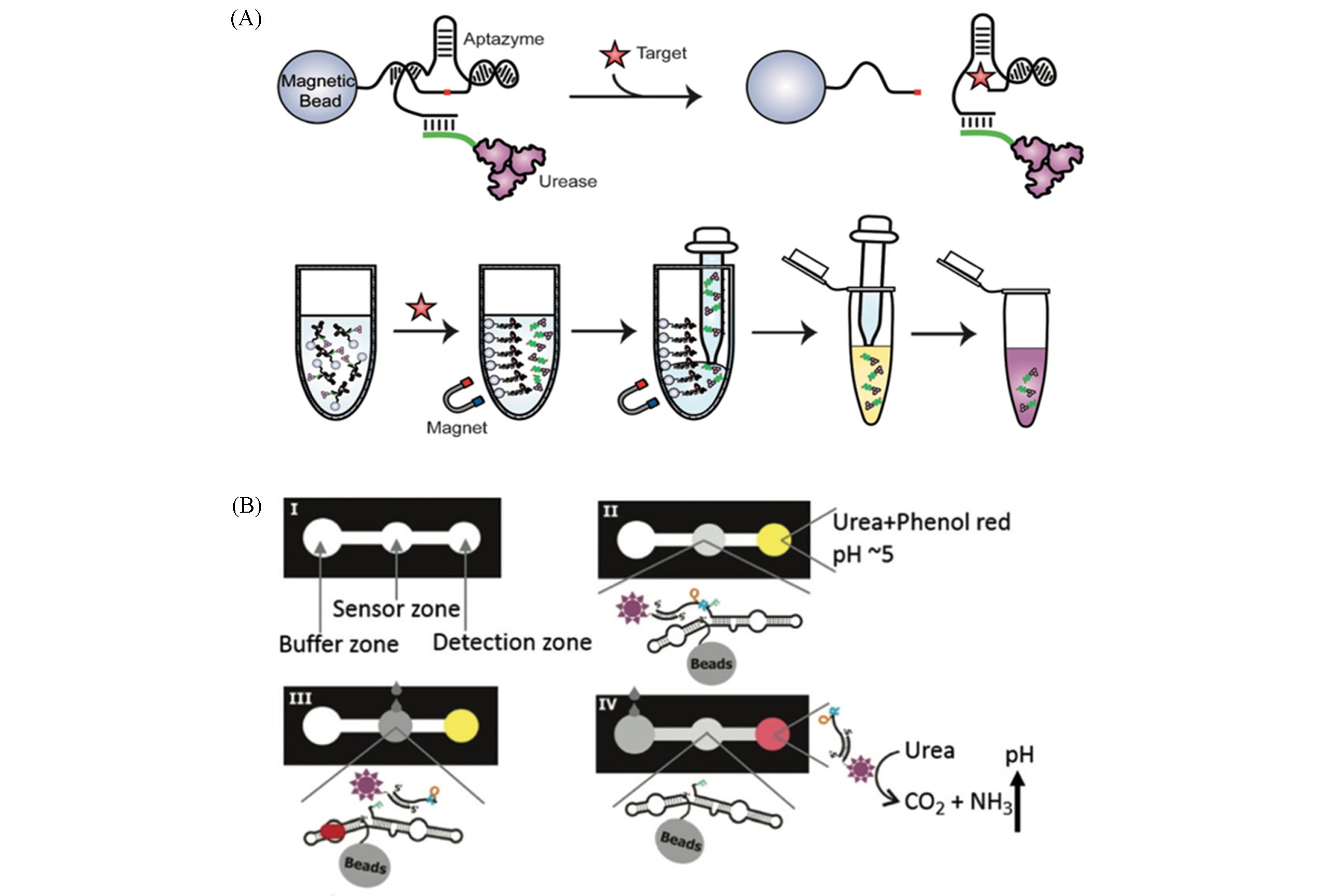
Fig.8 Schematic diagram of the litmus test for bacteria detection(A) Schematic diagram of DNAzyme?based colorimetric sensor for the detection of E. coli[73], Copyright 2014, Wiley?VCH;(B) schematic diagram of paper?based colorimetric sensor for H. pylori detection[41], Copyright 2019, Wiley?VCH.
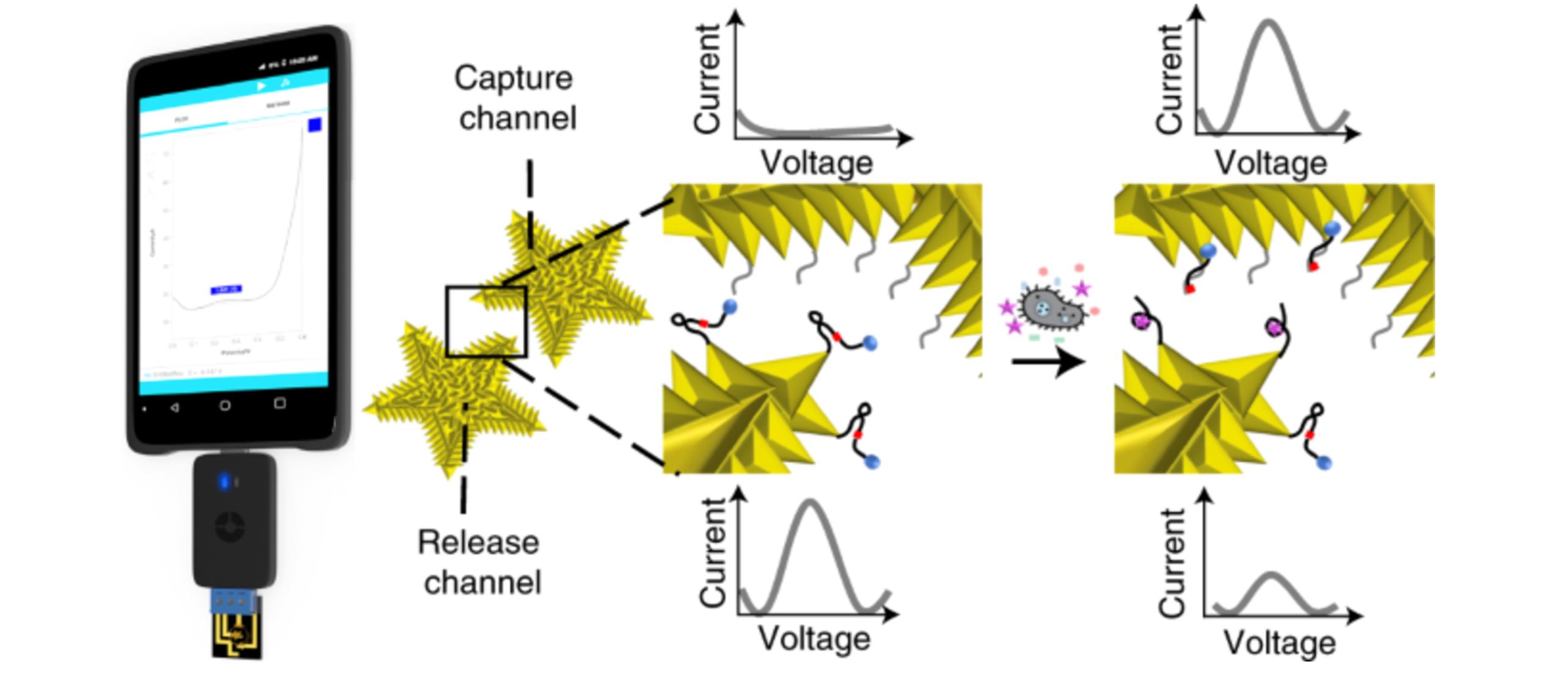
Fig.10 Illustration of DNAzymes integrated with electrical readout for rapid and culture?free bacterial detection using a handheld platform[78]Copyright 2021, Springer Nature.
| 1 | Wilcock A., Pun M., Khanona J., Aung M., Trends Food Sci. Tech., 2004, 15, 56—66 |
| 2 | Jain S., Costa Melo T. G., Dolabella S. S., Liu J., TrAC Trend. Anal. Chem., 2019, 121, 115695 |
| 3 | Liu Y., Zhou H., Hu Z., Yu G., Yang D., Zhao J., Biosens Bioelectron, 2017, 94, 131—140 |
| 4 | Tait E., Perry J. D., Stanforth S. P., Dean J. R., TrAC Trend. Anal. Chem., 2014, 53, 117—125 |
| 5 | Bhardwaj N., Bhardwaj S. K., Nayak M. K., Mehta J., Kim K. H., Deep A., TrAC Trend. Anal. Chem., 2017, 97, 120—135 |
| 6 | Richter L., Janczuk⁃Richter M., Niedziolka⁃Jonsson J., Paczesny J., Holyst R., Drug Discov. Today, 2018, 23, 448—455 |
| 7 | Guk K., Keem J. O., Hwang S. G., Kim H., Kang T., Lim E., Jung J., Biosens. Bioelectron., 2017, 95, 67—71 |
| 8 | Wang L., Shen X., Wang T., Chen P., Qi N., Yin B., Ye B., Biosens. Bioelectron., 2020, 165, 112364 |
| 9 | Peng L., Zhou J., Yin L., Man S., Ma L., Anal. Chim. Acta, 2020, 1125, 162—168 |
| 10 | Wang Y., Ke Y., Liu W., Sun Y., Ding X., ACS Sens., 2020, 5, 1427—1435 |
| 11 | Sun X., Wang Y., Zhang L., Liu S., Zhang M., Wang J., Ning B., Peng Y., He J., Hu Y., Gao Z., Anal. Chem., 2020, 92, 3032—3041 |
| 12 | Shen J., Zhou X., Shan Y., Yue H., Huang R., Hu J., Xing D., Nat. Commun., 2020, 11, 267 |
| 13 | Liu H., Wang J., Zeng H., Liu X., Jiang W., Wang Y., Ouyang W., Tang X., Food Chem., 2021, 334, 127608 |
| 14 | Sheng A., Wang P., Yang J., Tang L., Chen F., Zhang J., Anal. Chem., 2021, 93, 4676—4681 |
| 15 | Zhang T., Zhou W., Lin X., Khan M. R., Deng S., Zhou M., He G., Wu C., Deng R., He Q., Biosens. Bioelectron., 2021, 176, 112906 |
| 16 | Li F., Ye Q., Chen M., Zhou B., Zhang J., Pang R., Xue L., Wang J., Zeng H., Wu S., Zhang Y., Ding Y., Wu Q., Biosens. Bioelectron., 2021, 179, 113073 |
| 17 | Song F., Wei Y., Wang P., Ge X., Li C., Wang A., Yang Z., Wan Y., Li J., Biosens. Bioelectron., 2021, 185, 113262 |
| 18 | Wu H., Chen Y., Yang Q, Peng C., Wang X., Zhang M., Qian S., Xu J., Wu J., Biosens. Bioelectron., 2021, 188, 113352 |
| 19 | Li Y., Future Microbiol., 2011, 6, 973—976 |
| 20 | Riu J., Giussani B., TrAC Trend. Anal. Chem., 2020, 126, 115863 |
| 21 | Mobed A., Baradaran B., de la Guardia M., Agazadeh M., Hasanzadeh M., Rezaee M. A., Mosafer J., Mokhtarzadeh A., Hamblin M. R., TrAC Trend. Anal. Chem., 2019, 113, 157—171 |
| 22 | Breaker R. R., Joyce G. F., Chem. Biol., 1994, 1, 223—229 |
| 23 | Gopinath S. C., Anal. Bioanal. Chem., 2007, 387, 171—182 |
| 24 | Liu H., Yu X., Chen Y., Zhang J., Wu B., Zheng L., Haruehanroengra P., Wang R., Li S., Lin J., Li J., Sheng J., Huang Z., Ma J., Gan J., Nat. Commun., 2017, 8, 2006 |
| 25 | Schlosser K., Gu J., Sule L., Li Y., Nucleic Acids Res., 2008, 36, 1472—1481 |
| 26 | Sreedhara A., Li Y., Breaker R. R., J. Am. Chem. Soc., 2004, 126, 3454—3460 |
| 27 | Semlow D. R., Silverman S. K., J. Mol. Evol., 2005, 61, 207—215 |
| 28 | Camden A. J., Walsh S. M., Suk S. H., Silverman S. K., Biochemistry, 2016, 55, 2671—2676 |
| 29 | Silverman S. K., Org. Biomol. Chem., 2004, 2, 2701—2706 |
| 30 | Baum D. A., Silverman S. K., Cell. Mol. Life Sci., 2008, 65, 2156—2174 |
| 31 | Silverman S. K., Trends Biochem. Sci., 2016, 41, 595—609 |
| 32 | Saran R., Chen Q., Liu J., J. Mol. Evol., 2015, 81, 235—244 |
| 33 | Zhou W., Saran R., Huang P. J., Ding J., Liu J., ChemBioChem, 2017, 18, 518—522 |
| 34 | Kasprowicz A., Stokowa⁃Soltys K., Wrzesinski J., Jezowska⁃Bojczuk M., Ciesiolka J., Dalton Trans., 2015, 44, 8138—8149 |
| 35 | Nelson K. E., Bruesehoff P. J., Lu Y., J. Mol. Evol., 2005, 61, 216—225 |
| 36 | Moon W. J., Liu J., ChemBioChem, 2020, 21, 401—407 |
| 37 | Shen Y., Chiuman W., Brennan J. D., Li Y., ChemBioChem, 2006, 7, 1343—1348 |
| 38 | Ali M. M., Aguirre S. D., Lazim H., Li Y., Angew. Chem. Int. Ed. Eng.,2011, 50, 3751—3754 |
| 39 | Shen Z., Wu Z., Chang D., Zhang W., Tram K., Lee C., Kim P., Salena B. J., Li Y., Angew. Chem. Int. Ed. Eng.,2016, 55, 2431—2434 |
| 40 | Ali M. M., Slepenkin A., Peterson E., Zhao W., ChemBioChem, 2019, 20, 906—910 |
| 41 | Ali M. M., Wolfe M., Tram K., Gu J., Filipe C. D. M., Li Y., Brennan J. D., Angew. Chem. Int. Ed. Eng.,2019, 58, 9907—9911 |
| 42 | Rothenbroker M., McConnell E. M., Gu J., Urbanus M. L., Samani S. E., Ensminger A. W., Filipe C. D. M., Li Y., Angew. Chem. Int. Ed. Eng.,2021, 60, 4782—4788 |
| 43 | Gu L., Yan W., Wu H., Fan S., Ren W., Wang S., Lyu M., Liu J., Anal. Chem., 2019, 91, 7887—7893 |
| 44 | He S., Qu L., Shen Z., Tan Y., Zeng M., Liu F., Jiang Y., Li Y., Anal. Chem., 2015, 87, 569—577 |
| 45 | Geng X., Zhang M., Wang X., Sun J., Zhao X., Zhang L., Wang X., Shen Z., Anal. Chim. Acta, 2020, 1123, 28—35 |
| 46 | Mei S. H., Liu Z., Brennan J. D., Li Y., J. Am. Chem. Soc., 2003, 125, 412—420 |
| 47 | Chiuman W., Li Y., J. Mol. Biol., 2006, 357, 748—754 |
| 48 | Chiuman W., Li Y., Chem. Biol., 2006, 13, 1061—1069 |
| 49 | Shen Y., Brennan J. D., Li Y., Biochem., 2005, 44, 12066—12076 |
| 50 | Kandadai S. A., Li Y., Nucleic Acids Res., 2005, 33, 7164—7175 |
| 51 | Ali M. M., Kandadai S. A., Li Y., Can. J. Chem., 2007, 85, 261—273 |
| 52 | Rupcich N., Chiuman W., Nutiu R., Mei S., Flora K. K., Li Y., Brennan J. D., J. Am. Chem. Soc., 2006, 128, 780—790 |
| 53 | Chiuman W., Li Y., PLoS One, 2007, 2, e1224 |
| 54 | Merrigan M., Venugopal A., Mallozzi M., Roxas B., Viswanathan V. K., Johnson S., Gerding D. N., Vedantam G., J. Bacteriol., 2010, 192, 4904—4911 |
| 55 | Zhang W., Feng Q., Chang D., Tram K., Li Y., Methods, 2016, 106, 66—75 |
| 56 | McConnell E. M., Cozma I., Mou Q., Brennan J. D., Lu Y., Li Y., Chem. Soc. Rev., 2021, 50(16), 8954—8994 |
| 57 | Morrison D., Rothenbroker M., Li Y., Small Methods, 2018, 2, 1700319 |
| 58 | Kang D. K., Ali M. M., Zhang K., Huang S. S., Peterson E., Digman M. A., Gratton E., Zhao W., Nat. Commun., 2014, 5, 5427 |
| 59 | Ali M. M., Brown C. L., Jahanshahi⁃Anbuhi S., Kannan B., Li Y., Filipe C. D. M., Brennan J. D., Sci. Rep., 2017, 7, 12335 |
| 60 | Liu M., Zhang Q., Kannan B., Botton G. A., Yang J., Soleymani L., Brennan J. D., Li Y., Angew. Chem. Int. Ed. Eng.,2018, 57, 12440—12443 |
| 61 | Carrasquilla C., Little J. R., Li Y., Brennan J. D., Chemistry, 2015, 21, 7369—7373 |
| 62 | Samani S. E., Chang D., McConnell E. M., Rothenbroker M., Filipe C. D. M., Li Y., ChemBioChem, 2020, 21, 632—637 |
| 63 | Yousefi H., Ali M. M., Su H. M., Filipe C. D. M., Didar T. F., ACS Nano, 2018, 12, 3287—3294 |
| 64 | Fire A., Xu S. Q., Proc. Natl. Acad. Sci. USA, 1995, 92, 4641—4645 |
| 65 | Wang F., Lu C. H., Willner I., Chem. Rev., 2014, 114, 2881—2941 |
| 66 | Mao Y., Liu M., Tram K., Gu J., Salena B. J., Jiang Y., Li Y., Chemistry, 2015, 21, 8069—8074 |
| 67 | Lv Y., Hu R., Zhu G., Zhang X., Mei L., Liu Q., Qiu L., Wu C., Tan W., Nat. Protoc., 2015, 10, 1508—1524 |
| 68 | Liu M., Zhang Q., Li Z., Gu J., Brennan J. D., Li Y., Nat. Commun., 2016, 7, 12074 |
| 69 | Liu M., Zhang Q., Chang D., Gu J., Brennan J. D., Li Y., Angew. Chem. Int. Ed. Eng.,2017, 56, 6142—6146 |
| 70 | Zhou Z., Brennan J. D., Li Y., Angew. Chem. Int. Ed. Eng.,2020, 59, 10401—10405 |
| 71 | Zheng L., Qi P., Zhang D., Sensor. Actuat. B: Chem., 2018, 276, 42—47 |
| 72 | Zhou Z., Zhang Y., Guo M., Huang K., Xu W., Biosens. Bioelectron., 2020, 167, 112475 |
| 73 | Tram K., Kanda P., Salena B. J., Huan S., Li Y., Angew. Chem. Int. Ed. Eng.,2014, 53, 12799—12802 |
| 74 | Tram K., Manochehry S., Feng Q., Chang D., Salena B. J., Li Y., J. Vis. Exp., 2016, 115, e54546 |
| 75 | Manochehry S., McConnell E. M., Tram K. Q., Macri J., Li Y., Front. Chem., 2018, 6, 332 |
| 76 | Sun Y., Chang Y., Zhang Q., Liu M., Micromachines, 2019, 10, 531 |
| 77 | Yu F., Li Y., Li M., Tang L., He J. J., Biosens. Bioelectron., 2017, 89, 880—885 |
| 78 | Pandey R., Chang D. R., Smieja M., Hoare T., Li Y. F., Soleymani L., Nat. Chem., 2021, doi:10.1038/s41557⁃021⁃00718⁃x |
| 79 | Cheglakov Z., Weizmann Y., Basnar B., Willner I., Org. Biomol. Chem., 2007, 5, 223—225 |
| 80 | Liu Z., Yao C., Wang Y., Yang C., Anal. Methods, 2018, 10, 848—854 |
| 81 | Gomez A., Miller N. S., Smolina I., Anal. Chem., 2014, 86, 11992—11998 |
| 82 | Cheng N., Li J. C., Liu D., Lin Y., Du D., Small, 2019, 15, e1901485 |
| 83 | Wu Y., Wu J., Jiao L., Xu W., Wang H., Wei X., Gu W., Ren G., Zhang N., Zhang Q., Huang L., Gu L., Zhu C., Anal. Chem., 2020, 92, 3373—3379 |
| 84 | Chen M., Zhou H., Liu X., Yuan T., Wang W., Zhao C., Zhao Y., Zhou F., Wang X., Xue Z., Yao T., Xiong C., Wu Y., Small, 2020, 16, e2002343 |
| 85 | Zhang R., Fan K., Yan X., Sci. China Life Sci., 2020, 63, 1183—1200 |
| 86 | Mao Y., Gao S., Yao L., Wang L., Qu H., Wu Y., Chen Y., Zheng L., J. Hazard. Mater., 2021, 408, 124898 |
| 87 | Wu W., Huang L., Wang E., Dong S., Chem. Sci., 2020, 11, 9741—9756 |
| 88 | Wang Y., Bi Y., Wang R., Wang L., Qu H., Zheng L., J. Agric. Food Chem., 2021, 69, 1398—1404 |
| 89 | Yao L., Gao S., Liu S., Bi Y., Wang R., Qu H., Wu Y., Mao Y., Zheng L., ACS Appl. Mater. Inter., 2020, 12, 6268—6275 |
| 90 | Wang R., Mao Y., Wang L., Qu H., Chen Y., Zheng L., Food Chem., 2021, 347, 128980 |
| 91 | Si Y., Li L., Wang N., Zheng J., Yang R., Li J., ACS Appl. Mater. Inter., 2019, 11, 7792—7799 |
| 92 | Zhong Z. T., Wang H. B., Zhang T., Li C. Q., Liu B., Zhao Y. D., Food Chem., 2021, 352, 129330 |
| 93 | Sun M., Liu S., Wei X., Wan S., Huang M., Song T., Lu Y., Weng X., Lin Z., Chen H., Song Y., Yang C., Angew. Chem. Int. Ed. Eng.,2021, 60, 10266—10272 |
| 94 | Song Y., Song J., Wei X., Huang M., Sun M., Zhu L., Lin B., Shen H., Zhu Z., Yang C., Anal. Chem., 2020, 92, 9895—9900 |
| 95 | Lin H., Zhang W., Jia S., Guan Z., Yang C. J., Zhu Z., Biomicrofluidics, 2014, 8, 041501 |
| 96 | Chen J., Liu X., Xu M., Li Z., Xu D., Biomicrofluidics, 2021, 15, 024107 |
| 97 | Lin C. S., Tsai Y. C., Hsu K. F., Lee G. B., Lab. Chip., 2021, 21, 725—734 |
| [1] | 刘晓磊, 陆永强, 游淇, 刘国辉, 姚伟, 胡日茗, 闫纪宪, 崔玉, 杨小凤, 孙国新, 蒋绪川. 基于3-羟基沙利度胺的比率型荧光探针对过氧化氢的检测[J]. 高等学校化学学报, 2022, 43(6): 20220070. |
| [2] | 鲁聪, 李振华, 刘金露, 华佳, 李光华, 施展, 冯守华. 一种新的镧系金属有机骨架材料的合成、 结构及荧光检测性质[J]. 高等学校化学学报, 2022, 43(6): 20220037. |
| [3] | 陈嘉敏, 曲孝章, 齐国华, 徐蔚青, 金永东, 徐抒平. SERS纳米探针对电刺激过程中细胞内产生活性氧的检测[J]. 高等学校化学学报, 2022, 43(6): 20220033. |
| [4] | 朱浩天, 金美秀, 唐文思, 苏芳, 李阳光. 过渡金属-联咪唑-Dawson型钨磷酸盐杂化化合物的酶固定化性能[J]. 高等学校化学学报, 2022, 43(11): 20220328. |
| [5] | 邵文惠, 胡欣, 尚静, 林峰, 金黎明, 权春善, 张艳梅, 李军. 高效广谱复合光催化抗菌剂Ag-AgVO3/BiVO4的设计合成及抗菌机制[J]. 高等学校化学学报, 2022, 43(10): 20220132. |
| [6] | 王玮, 邹秉辰, 侯捷, 周万里, 罗建平, 王康丽, 蒋凯. Li-Ga液态金属电池界面反应过程的原位检测[J]. 高等学校化学学报, 2022, 43(10): 20220261. |
| [7] | 李文, 乔珺一, 刘鑫垚, 刘云凌. 含萘基团的锆金属有机骨架材料对水中硝基芳烃爆炸物的荧光检测性能[J]. 高等学校化学学报, 2022, 43(1): 20210654. |
| [8] | 朱兆田, 李圣凯, 宋明慧, 蔡芯琪, 宋志灵, 陈龙, 陈卓. 多功能金属石墨纳米囊的生物医学应用进展[J]. 高等学校化学学报, 2021, 42(9): 2701. |
| [9] | 赵慧君, 吴通, 孙玥, 段炼, 马嫣宇. 基于香豆素的比率型荧光探针对溶液及气相中三氟化硼的检测[J]. 高等学校化学学报, 2021, 42(8): 2422. |
| [10] | 陈峰, 程娜, 赵健伟, 宋易恬, 孙燕燕, 娄鑫梨, 童夏燕. 纳米颗粒银层的电沉积机理及SERS效应[J]. 高等学校化学学报, 2021, 42(6): 1891. |
| [11] | 窦树珍, 王中舜, 吕男. 硅纳米结构对表面辅助激光解吸/电离质谱检测性能的提高[J]. 高等学校化学学报, 2021, 42(4): 1156. |
| [12] | 蔡瑞, 刘建波, 吴晓春. 贵金属基纳米酶的研究进展[J]. 高等学校化学学报, 2021, 42(4): 1188. |
| [13] | 郑海娇, 姜丽艳, 贾琼. 精氨酸功能化磁性纳米材料的制备及在磷酸化肽富集中的应用[J]. 高等学校化学学报, 2021, 42(3): 717. |
| [14] | 潘菁, 徐敏敏, 袁亚仙, 姚建林. 基于表面增强拉曼光谱快速检测纺织品禁用染料[J]. 高等学校化学学报, 2021, 42(12): 3716. |
| [15] | 张晓荣, 陈岚岚, 胡善文. 基于分子识别的细菌检测研究进展[J]. 高等学校化学学报, 2021, 42(11): 3468. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||
