

高等学校化学学报 ›› 2023, Vol. 44 ›› Issue (3): 20220362.doi: 10.7503/cjcu20220362
收稿日期:2022-05-21
出版日期:2023-03-10
发布日期:2023-03-14
通讯作者:
戴磊
E-mail:lei.dai@siat.ac.cn
基金资助:
HU Yucan, CAO Zhaohui, ZHENG Linggang, SHEN Juntao, ZHAO Wei, DAI Lei( )
)
Received:2022-05-21
Online:2023-03-10
Published:2023-03-14
Contact:
DAI Lei
E-mail:lei.dai@siat.ac.cn
Supported by:摘要:
微生物组工程是对复杂微生物群落进行改造, 在基因组、 代谢组及群落生态结构等多个层次上实现微生物组的精准调控. 成簇规律间隔短回文序列(CRISPR)及其相关蛋白(CRISPR-Cas)系统是近期发展迅速的高效基因编辑工具. 本文回顾了微生物组工程领域CRISPR-Cas系统的重要研究工作, 重点关注CRISPR-Cas系统在微生物组的基因编辑和生态调控方面的应用. 针对CRISPR-Cas系统在微生物组工程领域的应用挑战, 本文从外源DNA递送方式和基因表达调控元件两个方面总结了微生物组工程的关键辅助方法与发展趋势, 展望了微生物组工程领域所面临的挑战与机遇.
中图分类号:
TrendMD:
胡玉灿, 曹朝辉, 郑灵刚, 沈俊涛, 赵维, 戴磊. CRISPR⁃Cas基因编辑技术在微生物组工程中的应用. 高等学校化学学报, 2023, 44(3): 20220362.
HU Yucan, CAO Zhaohui, ZHENG Linggang, SHEN Juntao, ZHAO Wei, DAI Lei. Applications of CRISPR-Cas Technologies in Microbiome Engineering. Chem. J. Chinese Universities, 2023, 44(3): 20220362.
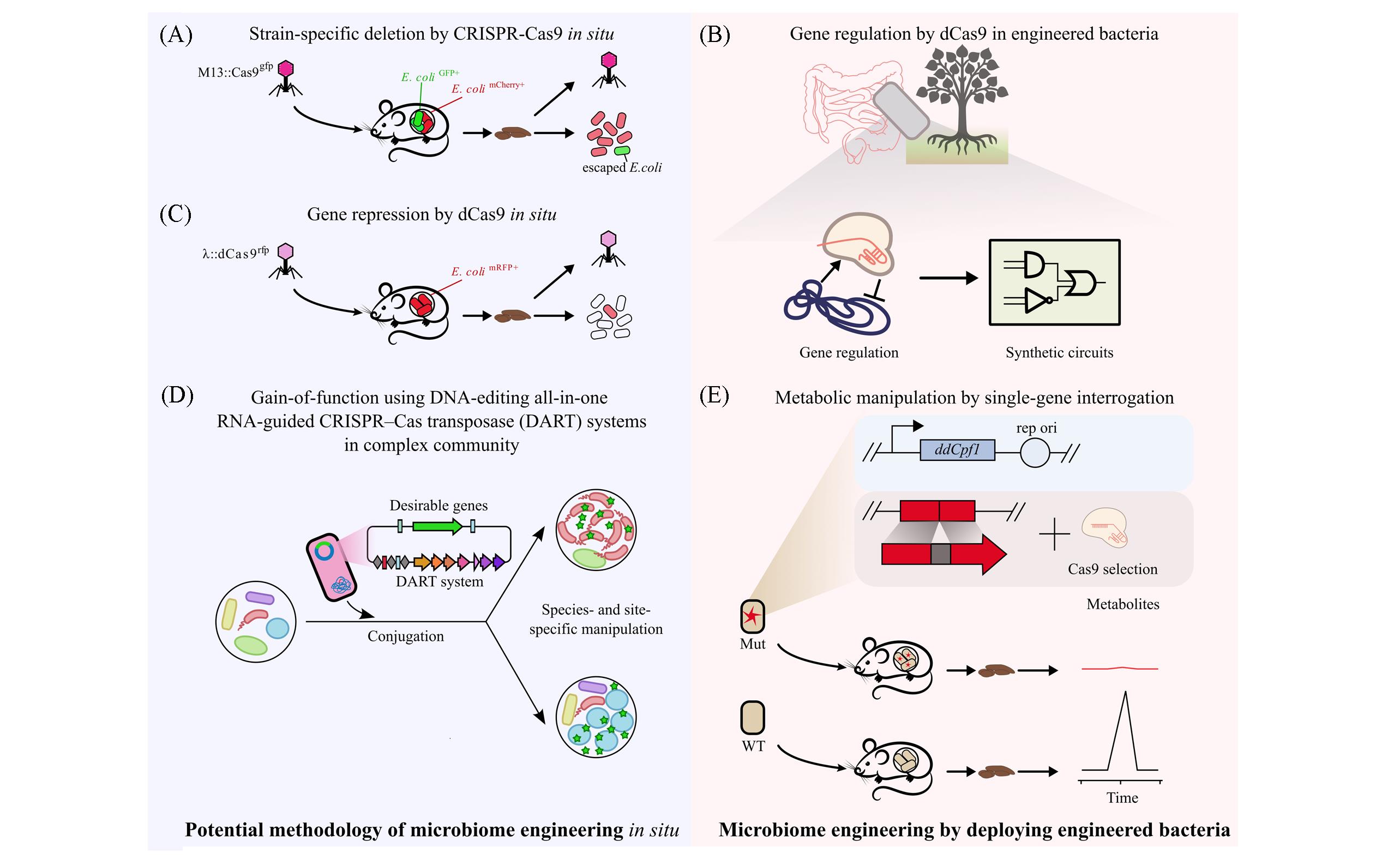
Fig.4 Application of CRISPR⁃Cas system in microbiome engineeringThe potential CRISPR⁃Cas methods of microbiome engineering in situ are summarized in lavender panel, including strain⁃specific deletion by CRISPR⁃Cas9 system(A), gene repression by CRISPR⁃dCas9 system(C) and CRISPR associated transposons mediated specific species⁃/locus⁃integration(D). The strategies for CRISPR⁃Cas based engineered bacteria are summarized in mistyrose panel, including gene regulation by CRISPR⁃dCas9 system in the gut resident species B. thetaiotaomicron(B) and CRISPR⁃Cas system mediated metabolic manipulation in untractable organisms(E).
| 1 | Berg G., Rybakova D., Fischer D., Cernava T., Verges M. C., Charles T., Chen X., Cocolin L., Eversole K., Corral G. H., Kazou M., Kinkel L., Lange L., Lima N., Loy A., Macklin J. A., Maguin E., Mauchline T., McClure R., Mitter B., Ryan M., Sarand I., Smidt H., Schelkle B., Roume H., Kiran G. S., Selvin J., Souza R. S. C., van Overbeek L., Singh B. K., Wagner M., Walsh A., Sessitsch A., Schloter M., Microbiome, 2020, 8(1), 103 |
| 2 | Hill J. H., Round J. L., Cell, 2021, 184(10), 2796—2796.e1 |
| 3 | Bulgarelli D., Schlaeppi K., Spaepen S., ver Loren van Themaat E., Schulze⁃Lefert P., Annu. Rev. Plant. Biol., 2013, 64, 807—838 |
| 4 | Consortium E. B. R., EBRC, 2020, [2020⁃10]. https://roadmap.ebrc.org/2020⁃roadmap⁃microbiomes/ |
| 5 | Lawson C. E., Harcombe W. R., Hatzenpichler R., Lindemann S. R., Loffler F. E., O'Malley M. A., Garcia M. H., Pfleger B. F., Raskin L., Venturelli O. S., Weissbrodt D. G., Noguera D. R., McMahon K. D., Nat. Rev. Microbiol., 2019, 17(12), 725—741 |
| 6 | Eng A., Borenstein E., Curr. Opin. Biotechnol., 2019, 58, 117—128 |
| 7 | van Schooneveld T. C., Gross A., Kalil A. C., N. Engl. J. Med., 2013, 368(22), 2143 |
| 8 | Chen M. X., Wei Z., Tian L., Tan Y., Huang J. D., Dai L., Chinese Science Bulletin, 2021, 66(3), 273—283 |
| 陈沫先, 韦中, 田亮, 谭扬, 黄建东, 戴磊. 科学通报, 2021, 66(3), 273—283 | |
| 9 | Chiba T., Seno H., Gastroenterology, 2011, 141(3), 1114—1116 |
| 10 | Tanoue T., Morita S., Plichta D. R., Skelly A. N., Suda W., Sugiura Y., Narushima S., Vlamakis H., Motoo I., Sugita K., Shiota A., Takeshita K., Yasuma⁃Mitobe K., Riethmacher D., Kaisho T., Norman J. M., Mucida D., Suematsu M., Yaguchi T., Bucci V., Inoue T., Kawakami Y., Olle B., Roberts B., Hattori M., Xavier R. J., Atarashi K., Honda K., Nature, 2019, 565(7741), 600—605 |
| 11 | Atarashi K., Tanoue T., Shima T., Imaoka A., Kuwahara T., Momose Y., Cheng G., Yamasaki S., Saito T., Ohba Y., Taniguchi T., Takeda K., Hori S., Ivanov I. I., Umesaki Y., Itoh K., Honda K., Science, 2011, 331(6015), 337—341 |
| 12 | O'Toole P. W., Cooney J. C., Interdiscip. Perspect. Infect. Dis., 2008, 2008, 175285 |
| 13 | Buffie C. G., Bucci V., Stein R. R., McKenney P. T., Ling L., Gobourne A., No D., Liu H., Kinnebrew M., Viale A., Littmann E., van den Brink M. R., Jenq R. R., Taur Y., Sander C., Cross J. R., Toussaint N. C., Xavier J. B., Pamer E. G., Nature, 2015, 517(7533), 205—208 |
| 14 | Summers W. C., Annu. Rev. Microbiol., 2001, 55(1), 437—451 |
| 15 | Wang X., Wei Z., Yang K., Wang J., Jousset A., Xu Y., Shen Q., Friman V. P., Nat. Biotechnol., 2019, 37(12), 1513—1520 |
| 16 | Perera M. N., Abuladze T., Li M., Woolston J., Sulakvelidze A., Food Microbiology, 2015, 52, 42—48 |
| 17 | Silva Y. J., Costa L., Pereira C., Cunha A., Calado R., Gomes N. C., Almeida A., Microb. Biotechnol., 2014, 7(5), 401—413 |
| 18 | Chen Z., Guo L., Zhang Y., Walzem R. L., Pendergast J. S., Printz R. L., Morris L. C., Matafonova E., Stien X., Kang L., J. Clin. Invest., 2014, 124(8), 3391—3406 |
| 19 | Thompson J. A., Oliveira R. A., Djukovic A., Ubeda C., Xavier K. B., Cell Rep., 2015, 10(11), 1861—1871 |
| 20 | Sheth R. U., Cabral V., Chen S. P., Wang H. H., Trends Genet., 2016, 32(4), 189—200 |
| 21 | Ronda C., Chen S. P., Cabral V., Yaung S. J., Wang H. H., Nat. Methods, 2019, 16(2), 167—170 |
| 22 | Rubin B. E., Diamond S., Cress B. F., Crits⁃Christoph A., Lou Y. C., Borges A. L., Shivram H., He C., Xu M., Zhou Z., Smith S. J., Rovinsky R., Smock D. C. J., Tang K., Owens T. K., Krishnappa N., Sachdeva R., Barrangou R., Deutschbauer A. M., Banfield J. F., Doudna J. A., Nat. Microbiol., 2022, 7(1), 34—47 |
| 23 | Lagier J. C., Dubourg G., Million M., Cadoret F., Bilen M., Fenollar F., Levasseur A., Rolain J. M., Fournier P. E., Raoult D., Nat. Rev. Microbiol., 2018, 16, 540—550 |
| 24 | Vollaard E. J., Clasener H. A., Antimicrob. Agents Chemother., 1994, 38(3), 409—414 |
| 25 | Burstein D., Sun C. L., Brown C. T., Sharon I., Anantharaman K., Probst A. J., Thomas B. C., Banfield J. F., Nat. Commun., 2016, 7, 10613 |
| 26 | Shivram H., Cress B. F., Knott G. J., Doudna J. A., Nat. Chem. Biol., 2021, 17(1), 10—19 |
| 27 | Makarova K. S., Wolf Y. I., Iranzo J., Shmakov S. A., Alkhnbashi O. S., Brouns S. J. J., Charpentier E., Cheng D., Haft D. H., Horvath P., Moineau S., Mojica F. J. M., Scott D., Shah S. A., Siksnys V., Terns M. P., Venclovas C., White M. F., Yakunin A. F., Yan W., Zhang F., Garrett R. A., Backofen R., van der Oost J., Barrangou R., Koonin E. V., Nat. Rev. Microbiol., 2020, 18(2), 67—83 |
| 28 | Jinek M., Chylinski K., Fonfara I., Hauer M., Doudna J. A., Charpentier E., Science, 2012, 337(6096), 816—821 |
| 29 | Jiang F., Doudna J. A., Annu. Rev. Biophys., 2017, 46, 505—529 |
| 30 | Ran F. A., Hsu P. D., Wright J., Agarwala V., Scott D. A., Zhang F., Nat. Protoc., 2013, 8(11), 2281—2308 |
| 31 | Qi L. S., Larson M. H., Gilbert L. A., Doudna J. A., Weissman J. S., Arkin A. P., Lim W. A., Cell, 2013, 152(5), 1173—1183 |
| 32 | Pickar⁃Oliver A., Gersbach C. A., Nat. Rev. Mol. Cell Biol., 2019, 20(8), 490—507 |
| 33 | Barrangou R., Doudna J. A., Nat. Biotechnol., 2016, 34(9), 933—941 |
| 34 | Mir A., Edraki A., Lee J., Sontheimer E. J., ACS Chem. Biol., 2018, 13(2), 357—365 |
| 35 | Janik E., Niemcewicz M., Ceremuga M., Krzowski L., Saluk⁃Bijak J., Bijak M., Int. J. Mol. Sci., 2020, 21(24), 9604 |
| 36 | Paul B., Montoya G., Biomed. J., 2020, 43(1), 8—17 |
| 37 | Chen J. S., Ma E., Harrington L. B., Da Costa M., Tian X., Palefsky J. M., Doudna J. A., Science, 2018, 360(6387), 436—439 |
| 38 | Strohkendl I., Saifuddin F. A., Rybarski J. R., Finkelstein I. J., Russell R., Mol. Cell, 2018, 71(5), 816—824.e3 |
| 39 | Yamano T., Nishimasu H., Zetsche B., Hirano H., Slaymaker I. M., Li Y., Fedorova I., Nakane T., Makarova K. S., Koonin E. V., Ishitani R., Zhang F., Nureki O., Cell, 2016, 165(4), 949—962 |
| 40 | Zhang X., Wang J., Cheng Q., Zheng X., Zhao G., Wang J., Cell Discov., 2017, 3, 17018 |
| 41 | Swarts D. C., Jinek M., Wiley Interdiscip Rev. RNA, 2018, 9(5), e1481 |
| 42 | Meliawati M., Schilling C., Schmid J., Appl. Microbiol. Biotechnol., 2021, 105(8), 2981—2990 |
| 43 | Dronina J., Samukaite⁃Bubniene U., Ramanavicius A., J. Nanobiotechnology, 2022, 20(1), 41 |
| 44 | Abudayyeh O. O., Gootenberg J. S., Konermann S., Joung J., Slaymaker I. M., Cox D. B. T., Shmakov S., Makarova K. S., Semenova E., Minakhin L., Severinov K., Regev A., Lander E. S., Koonin E. V., Zhang F., Science, 2016, 353(6299), aaf5573 |
| 45 | Liu L., Li X., Ma J., Li Z., You L., Wang J., Wang M., Zhang X., Wang Y., Cell, 2017, 170(4), 714—726.e10 |
| 46 | Meeske A. J., Nakandakari⁃Higa S., Marraffini L. A., Nature, 2019, 570(7760), 241—245 |
| 47 | Granados⁃Riveron J. T., Aquino⁃Jarquin G., Cancer Res., 2018, 78(15), 4107—4113 |
| 48 | Mahas A., Neal Stewart C. Jr., Mahfouz M. M., Biotechnol. Adv., 2018, 36(1), 295—310 |
| 49 | Peters J. E., Makarova K. S., Shmakov S., Koonin E. V., Proc. Natl. Acad. Sci. USA, 2017, 114(35), E7358—E7366 |
| 50 | Strecker J., Ladha A., Gardner Z., Schmid⁃Burgk J. L., Makarova K. S., Koonin E. V., Zhang F., Science, 2019, 365(6448), 48—53 |
| 51 | Klompe S. E., Vo P. L. H., Halpin⁃Healy T. S., Sternberg S. H., Nature, 2019, 571(7764), 219—225 |
| 52 | Vo P. L. H., Ronda C., Klompe S. E., Chen E. E., Acree C., Wang H. H., Sternberg S. H., Nat. Biotechnol., 2021, 39(4), 480—489 |
| 53 | Halpin⁃Healy T. S., Klompe S. E., Sternberg S. H., Fernandez I. S., Nature, 2020, 577(7789), 271—274 |
| 54 | Zhang Y., Sun X., Wang Q., Xu J., Dong F., Yang S., Yang J., Zhang Z., Qian Y., Chen J., Zhang J., Liu Y., Tao R., Jiang Y., Yang J., Yang S., ACS Synth. Biol., 2020, 9(8), 1998—2008 |
| 55 | Yang S., Zhang Y., Xu J., Zhang J., Zhang J., Yang J., Jiang Y., Yang S., Nucleic Acids Res., 2021, 49(17), 10192—10202 |
| 56 | Rodríguez L. T., Ellington A. J., Reisch C. R., bioRxiv., 2022, doi:2022.2001.2019.475551 |
| 57 | Chen W., Ren Z. H., Tang N., Chai G., Zhang H., Zhang Y., Ma J., Wu Z., Shen X., Huang X., Luo G.Z., Ji Q., Cell Rep., 2021, 36(9), 109635 |
| 58 | Sharda M., Badrinarayanan A., Seshasayee A. S. N., Genome Biol. Evol., 2020, 12(12), 2450—2466 |
| 59 | Bikard D., Euler C. W., Jiang W., Nussenzweig P. M., Goldberg G. W., Duportet X., Fischetti V. A., Marraffini L. A., Nat. Biotechnol., 2014, 32(11), 1146—1150 |
| 60 | Citorik R. J., Mimee M., Lu T. K., Nat. Biotechnol., 2014, 32(11), 1141—1145 |
| 61 | Gomaa A. A., Klumpe H. E., Luo M. L., Selle K., Barrangou R., Beisel C. L., mBio., 2014, 5(1), e00928⁃13 |
| 62 | Lam K. N., Spanogiannopoulos P., Soto⁃Perez P., Alexander M., Nalley M. J., Bisanz J. E., Nayak R. R., Weakley A. M., Yu F. B., Turnbaugh P. J., Cell Rep., 2021, 37(5), 109930 |
| 63 | Neil K., Allard N., Roy P., Grenier F., Menendez A., Burrus V., Rodrigue S., Mol. Syst. Biol., 2021, 17(10), e10335 |
| 64 | Czepiel J., Drozdz M., Pituch H., Kuijper E.J., Perucki W., Mielimonka A., Goldman S., Wultanska D., Garlicki A., Biesiada G., Eur. J. Clin. Microbiol. Infect. Dis., 2019, 38(7), 1211—1221 |
| 65 | Selle K., Fletcher J. R., Tuson H., Schmitt D. S., McMillan L., Vridhambal G. S., Rivera A. J., Montgomery S. A., Fortier L. C., Barrangou R., Theriot C. M., Ousterout D. G., mBio., 2020, 11(2), e00019—20 |
| 66 | Kiga K., Tan X.E., Ibarra⁃Chavez R., Watanabe S., Aiba Y., Sato’o Y., Li F.Y., Sasahara T., Cui B., Kawauchi M., Boonsiri T., Thitiananpakorn K., Taki Y., Azam A. H., Suzuki M., Penades J. R., Cui L., Nat. Commun., 2020, 11(1), 2934 |
| 67 | Wang T., Guan C., Guo J., Liu B., Wu Y., Xie Z., Zhang C., Xing X. H., Nat. Commun., 2018, 9(1), 2475 |
| 68 | Peters J. M., Koo B. M., Patino R., Heussler G. E., Hearne C. C., Qu J., Inclan Y. F., Hawkins J. S., Lu C. H. S., Silvis M. R., Harden M. M., Osadnik H., Peters J. E., Engel J. N., Dutton R. J., Grossman A. D., Gross C. A., Rosenberg O. S., Nat. Microbiol., 2019, 4(2), 244—250 |
| 69 | Mimee M., Tucker A. C., Voigt C. A., Lu T. K., Cell Syst., 2015, 1(1), 62—71 |
| 70 | Lim B., Zimmermann M., Barry N. A., Goodman A. L., Cell, 2017, 169(3), 547—558.e15 |
| 71 | Whitaker W. R., Shepherd E. S., Sonnenburg J. L., Cell, 2017, 169(3), 538—546.e12 |
| 72 | Taketani M., Zhang J., Zhang S., Triassi A. J., Huang Y. J., Griffith L. G., Voigt C. A., Nat. Biotechnol., 2020, 38(8), 962—969 |
| 73 | Hsu B. B., Plant I. N., Lyon L., Anastassacos F. M., Way J. C., Silver P. A., Nat. Commun., 2020, 11(1), 5030 |
| 74 | Guo C. J., Allen B. M., Hiam K. J., Dodd D., van Treuren W., Higginbottom S., Nagashima K., Fischer C. R., Sonnenburg J. L., Spitzer M. H., Fischbach M. A., Science, 2019, 366(6471), eaav1282 |
| 75 | Jin W. B., Li T. T., Huo D., Qu S., Li X. V., Arifuzzaman M., Lima S. F., Shi H. Q., Wang A., Putzel G. G., Longman R. S., Artis D., Guo C. J., Cell, 2022, 185(3), 547—562.e22 |
| 76 | Sorensen S. J., Bailey M., Hansen L. H., Kroer N., Wuertz S., Nat. Rev. Microbiol., 2005, 3(9), 700—710 |
| 77 | Brito I. L., Nat. Rev. Microbiol., 2021, 19(7), 442—453 |
| 78 | Lu T. K., Collins J. J., Proc. Natl. Acad. Sci. USA, 2009, 106(12), 4629—4634 |
| 79 | Cobb L. H., Park J., Swanson E. A., Beard M. C., McCabe E. M., Rourke A. S., Seo K. S., Olivier A. K., Priddy L. B., PLoS One, 2019, 14(11), e0220421 |
| 80 | Alvarez⁃Martinez C. E., Christie P. J., Microbiol. Mol. Biol. Rev., 2009, 73(4), 775—808 |
| 81 | Brophy J. A. N., Triassi A. J., Adams B. L., Renberg R. L., Stratis⁃Cullum D. N., Grossman A. D., Voigt C. A., Nat. Microbiol., 2018, 3(9), 1043—1053 |
| 82 | Xu Z., Li Y., Cao H., Si M., Zhang G., Woo P. C. Y., Yan A., Nucleic. Acids Res., 2021, 49(16), e94 |
| 83 | Zheng L., Tan Y., Hu Y., Shen J., Qu Z., Chen X., Ho C. L., Leung E. L., Zhao W., Dai L., ACS Synth. Biol., 2022, 11(1), 464—472 |
| 84 | Hamilton T. A., Pellegrino G. M., Therrien J. A., Ham D. T., Bartlett P. C., Karas B. J., Gloor G. B., Edgell D. R., Nat. Commun., 2019, 10(1), 4544 |
| 85 | Neil K., Allard N., Grenier F., Burrus V., Rodrigue S., Commun. Biol., 2020, 3(1), 523 |
| 86 | Gomes A. L. C., Johns N. I., Yang A., Velez⁃Cortes F., Smillie C. S., Smith M. B., Alm E. J., Wang H. H., ISME J., 2020, 14(9), 2347—2357 |
| 87 | Salis H. M., Methods Enzymol., 2011, 498, 19—42 |
| 88 | Reis A. C., Salis H. M., ACS Synth. Biol., 2020, 9(11), 3145—3156 |
| 89 | Solovyev V. V.;Ed. Li R. W., Metagenomics and Its Applications in Agriculture, Biomedicine and Environmental Studies, Nova Science Publishers, New York, 2011, 61—78 |
| 90 | Shahmuradov I. A., Mohamad R. R., Bougouffa S., Radovanovic A., Bajic V. B., Bioinformatics, 2017, 33(3), 334—340 |
| 91 | Umarov R. K., Solovyev V. V., PLoS One, 2017, 12(2), e0171410 |
| 92 | Rahman M. S., Aktar U., Jani M. R., Shatabda S., Mol. Genet. Genomics, 2019, 294(1), 69—84 |
| 93 | Patel J. R., Oh J., Wang S., Crawford J. M., Isaacs F. J., Cell, 2022, 185(9), 1487—1505.e14 |
| 94 | Kotopka B. J., Smolke C. D., Nat. Commun., 2020, 11(1), 2113 |
| 95 | Johns N. I., Gomes A. L. C., Yim S. S., Yang A., Blazejewski T., Smillie C. S., Smith M. B., Alm E. J., Kosuri S., Wang H. H., Nat. Methods, 2018, 15(5), 323—329 |
| 96 | Zrimec J., Borlin C. S., Buric F., Muhammad A. S., Chen R., Siewers V., Verendel V., Nielsen J., Topel M., Zelezniak A., Nat. Commun., 2020, 11(1), 6141 |
| 97 | Wang Y., Wang H., Wei L., Li S., Liu L., Wang X., Nucleic. Acids Res., 2020, 48(12), 6403—6412 |
| 98 | Omotajo D., Tate T., Cho H., Choudhary M., BMC Genomics, 2015, 16, 604 |
| 99 | Sastalla I., Chim K., Cheung G. Y., Pomerantsev A. P., Leppla S. H., Appl. Environ. Microbiol., 2009, 75(7), 2099—2110 |
| 100 | Nye T. M., Jacob K. M., Holley E. K., Nevarez J. M., Dawid S., Simmons L. A., Watson M. E. Jr., PLoS Pathog., 2019, 15(6), e1007841 |
| 101 | Charles E. J., Kim S. E., Knott G. J., Smock D., Doudna J., Savage D. F., bioRxiv., 2021, doi:2021.2005.2026.445687 |
| 102 | Nakamura M., Gao Y., Dominguez A. A., Qi L. S., Nat. Cell Biol., 2021, 23(1), 11—22 |
| 103 | Cao X., Hamilton J. J., Venturelli O. S., Biochemistry, 2019, 58(2), 94—107 |
| 104 | Karkaria B. D., Treloar N. J., Barnes C. P., Fedorec A. J. H., Front. Bioeng. Biotechnol., 2020, 8, 834 |
| 105 | Matsushita M., Fujita K., Hayashi T., Kayama H., Motooka D., Hase H., Jingushi K., Yamamichi G., Yumiba S., Tomiyama E., Koh Y., Hayashi Y., Nakano K., Wang C., Ishizuya Y., Kato T., Hatano K., Kawashima A., Ujike T., Uemura M., Imamura R., Rodriguez Pena M. D. C., Gordetsky J. B., Netto G. J., Tsujikawa K., Nakamura S., Takeda K., Nonomura N., Cancer Res., 2021, 81(15), 4014—4026 |
| 106 | Han K., Nam J., Xu J., Sun X., Huang X., Animasahun O., Achreja A., Jeon J. H., Pursley B., Kamada N., Chen G. Y., Nagrath D., Moon J. J., Nat. Biomed. Eng., 2021, 5(11), 1377—1388 |
| 107 | Fischbach M. A., Cell, 2018, 174(4), 785—790 |
| 108 | Ridaura V. K., Faith J. J., Rey F. E., Cheng J., Duncan A. E., Kau A. L., Griffin N. W., Lombard V., Henrissat B., Bain J. R., Muehlbauer M. J., Ilkayeva O., Semenkovich C. F., Funai K., Hayashi D. K., Lyle B. J., Martini M. C., Ursell L. K., Clemente J. C., van Treuren W., Walters W. A., Knight R., Newgard C. B., Heath A. C., Gordon J. I., Science, 2013, 341(6150), 1241214 |
| [1] | 徐永斌, 冯帅霞, 陈洁, 龚欢, 施松善, 王辉俊, 王顺春. 红花均一多糖的结构表征及抑制HepG2增殖活性[J]. 高等学校化学学报, 2023, 44(4): 20220600. |
| [2] | 黄鼎旻 孙浩田 王振炜 刘豪 苏贤斌. 室温下3-喹啉硼酸催化羧酸酰胺化反应[J]. 高等学校化学学报, 0, (): 20230004. |
| [3] | 曹舒杰, 李泓君, 管文丽, 任梦田, 周传政. 硫代磷酸酯寡聚核苷酸的立体控制合成研究进展[J]. 高等学校化学学报, 2023, 44(3): 20220304. |
| [4] | 郇歆宇, 赖淦强, 黄悦, 杨财广. 化学干预N6-甲基腺嘌呤修饰的研究进展[J]. 高等学校化学学报, 2023, 44(3): 20220340. |
| [5] | 张凯嵩, 王少儒, 张雨桐, 田沺. 基于超分子化学的核酸表观遗传修饰研究[J]. 高等学校化学学报, 2023, 44(3): 20220335. |
| [6] | 常丽颖, 凌鑫宇, 陈和祺, 王雪, 刘涛. 基因编辑在线粒体疾病中的应用[J]. 高等学校化学学报, 2023, 44(3): 20220363. |
| [7] | 方鑫, 赵瑞奇, 莫婧, 王雅芬, 翁小成. 检测核酸表观遗传修饰的测序方法[J]. 高等学校化学学报, 2023, 44(3): 20220342. |
| [8] | 刘文婷, 刘柳宜, 朱博琛, 毛宗万. 核酸G-四链体的识别、 复合物结构与细胞内探测的研究进展[J]. 高等学校化学学报, 2023, 44(3): 20220419. |
| [9] | 唐玉静, 胡敏, 王霞, 王启刚. 载酶纳米催化体系用于疾病诊疗的研究进展[J]. 高等学校化学学报, 2022, 43(12): 20220640. |
| [10] | 仵宇帅, 尚颖旭, 蒋乔, 丁宝全. 可控自组装DNA折纸结构作为药物载体的研究进展[J]. 高等学校化学学报, 2022, 43(8): 20220179. |
| [11] | 朱凯, 利婕, 武潇逸, 胡薇薇, 吴冬梅, 虞诚潇, 葛志伟, 叶兴乾, 陈士国. 基于多孔石墨化碳柱-四极杆-飞行时间质谱解析甜菜果胶精细结构[J]. 高等学校化学学报, 2022, 43(6): 20220023. |
| [12] | 付俊, 吴美婵, 王书珍, 邵秀丽, 何峰. 基于标记法的福白菊精油抗真菌机理研究[J]. 高等学校化学学报, 2021, 42(12): 3657. |
| [13] | 赵卓, 王雪强. 核酸适体偶联药物的生物偶联构建技术与应用[J]. 高等学校化学学报, 2021, 42(11): 3367. |
| [14] | 陈旺, 胡代花, 刘格歌. 由醋酸去氢表雄酮合成熊去氧胆酸[J]. 高等学校化学学报, 2021, 42(9): 2782. |
| [15] | 胡皓程, 李文利, 张嘉宁, 刘宇博. 黑木耳寡糖的提取、 结构表征及生物活性[J]. 高等学校化学学报, 2021, 42(8): 2465. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||