

高等学校化学学报 ›› 2020, Vol. 41 ›› Issue (12): 2658.doi: 10.7503/cjcu20200371
• 庆祝《高等学校化学学报》复刊40周年专栏 • 上一篇 下一篇
收稿日期:2020-06-19
出版日期:2020-12-10
发布日期:2020-12-09
通讯作者:
陈鹏
E-mail:pengchen@pku.edu.cn
MA Weiyi1, LIU Shibo2, CHEN Peng2( )
)
Received:2020-06-19
Online:2020-12-10
Published:2020-12-09
Contact:
CHEN Peng
E-mail:pengchen@pku.edu.cn
摘要:
细胞-细胞相互作用在多种生理过程中有重要意义, 针对这些相互作用的研究是化学与生命科学交叉领域的前沿热点. 基于对酶的功能改造、 定向进化和精准的时空调控, 酶介导的邻近标记方法在分析细胞-细胞相互作用方面具有广泛的应用前景. 本文重点描述了现有邻近标记方法的原理、 效果、 优缺点及潜在应用.
中图分类号:
TrendMD:
马维绎, 刘士博, 陈鹏. 邻近标记方法表征细胞-细胞相互作用. 高等学校化学学报, 2020, 41(12): 2658.
MA Weiyi, LIU Shibo, CHEN Peng. Proximity Labeling in Cell-cell Interaction Detection. Chem. J. Chinese Universities, 2020, 41(12): 2658.
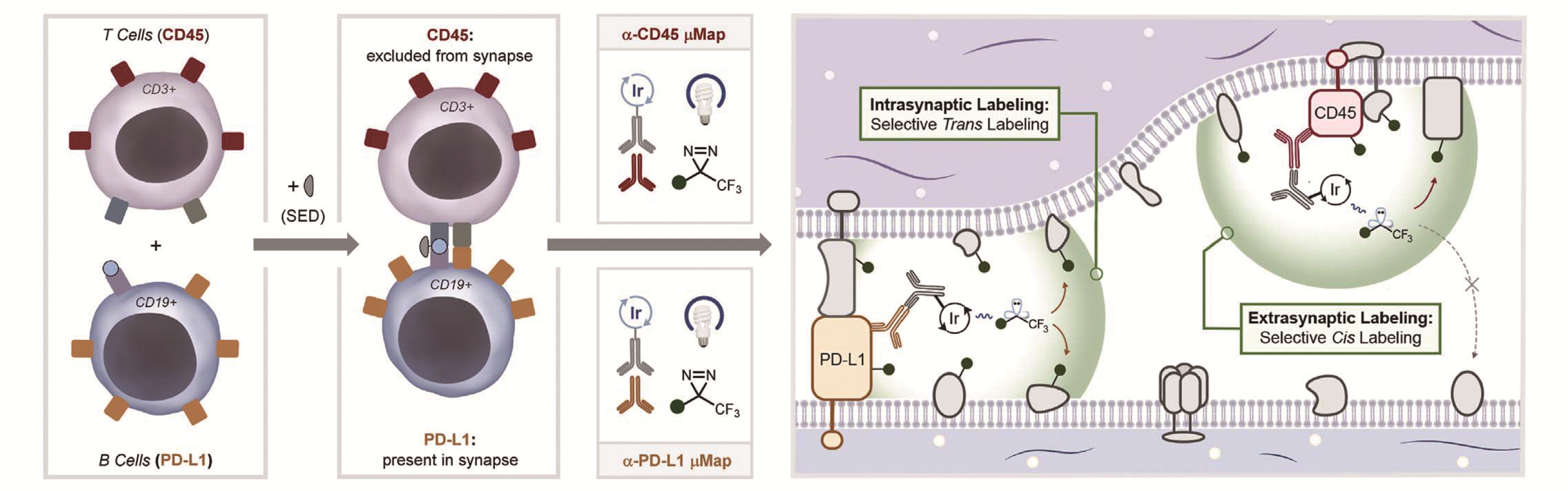
Fig.1 Non?enzymatic proximity labeling via Dexter energy transferSchematic depiction of intrasynaptic μ?mapping within a two?cell system[27]. T cells(CD45RO+/PD?1+) and B cells(PD?L1+) form stable interactions in the presence of staphylococcal enterotoxin D(SED). Antibody?photocatalyst complex targeted to PD?L1 or CD45 shows selective trans or cis labeling.Copyright 2020, American Association for the Advancement of Science.
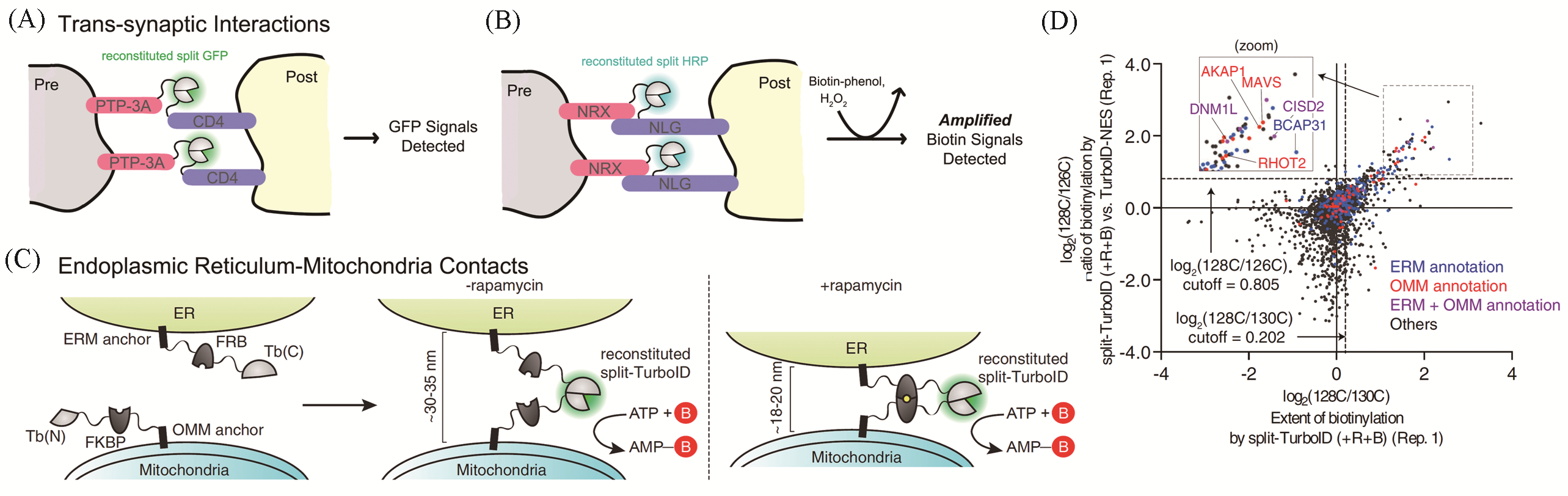
Fig.2 Sensitive visualization of cell?cell interactions with split proteinsSchematic diagram of GRASP(A) and intercellular split HRP reconstitution(B); (C) schematic of split?TurboID reconstitution across ER?mitochondria contacts[19]; (D) MS?based proteomic mapping[19], ERM: ER membrane, OMM: outer mitochondrial membrane. (C, D) Copyright 2020, National Academy of Sciences.
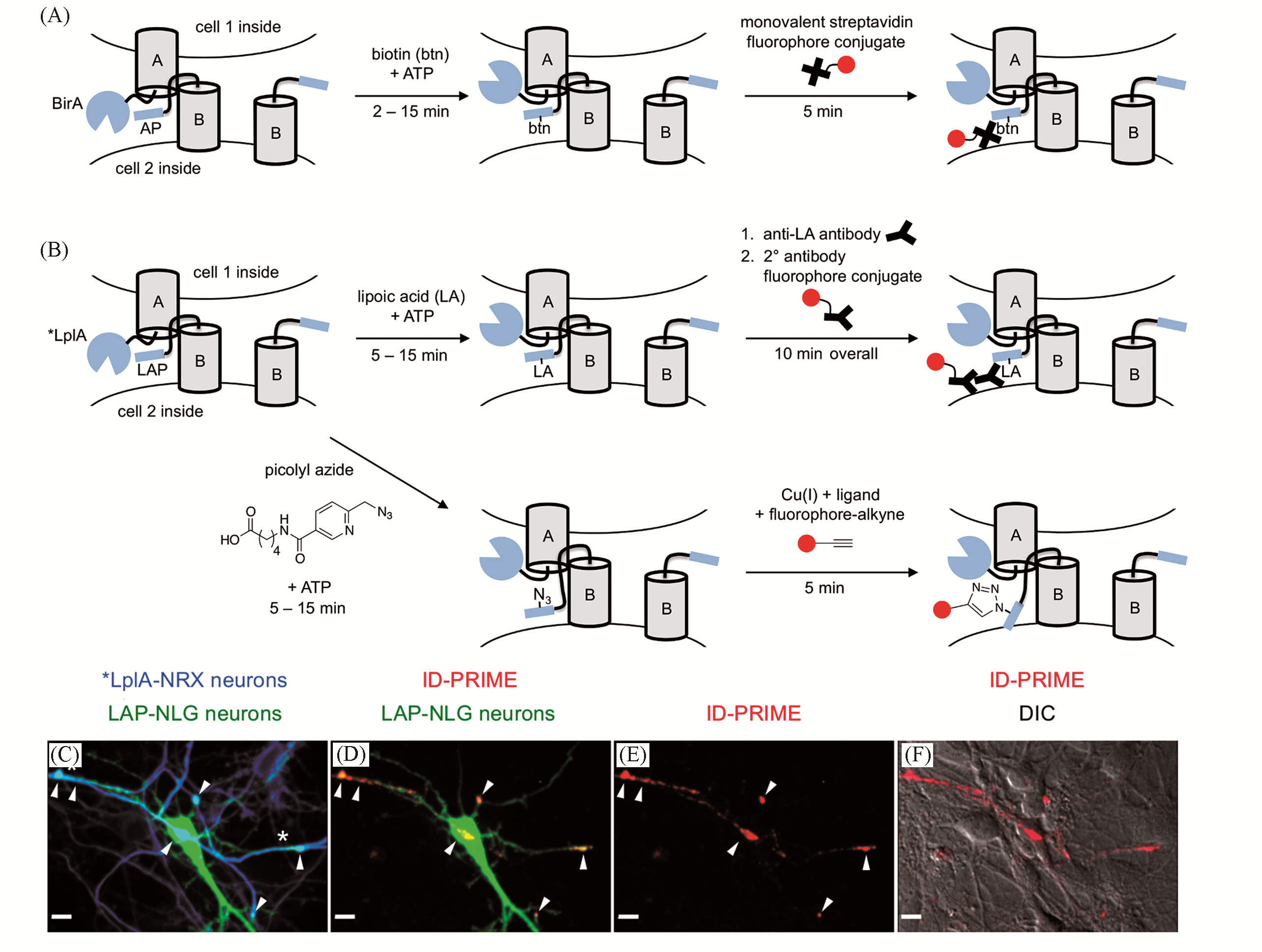
Fig.3 Trans?cellular labeling with BirA and LplA[20](A) Schematic diagram of BLINC, AP: acceptor peptide; (B) schematic diagrams of ID?PRIME, LAP: ligase acceptor peptide; (C—F) ID?PRIME for imaging neurexin?neuroligin interactions in neuron cultures, dissociated neurons were separately nucleofected with *LplA?NRX or LAP?NLG with fluorescent markers(C) and ID?PRIME signal was detected at contact sites[arrow heads(D—F)], bars: 10 μm.Copyright 2013, Public Library of Science.
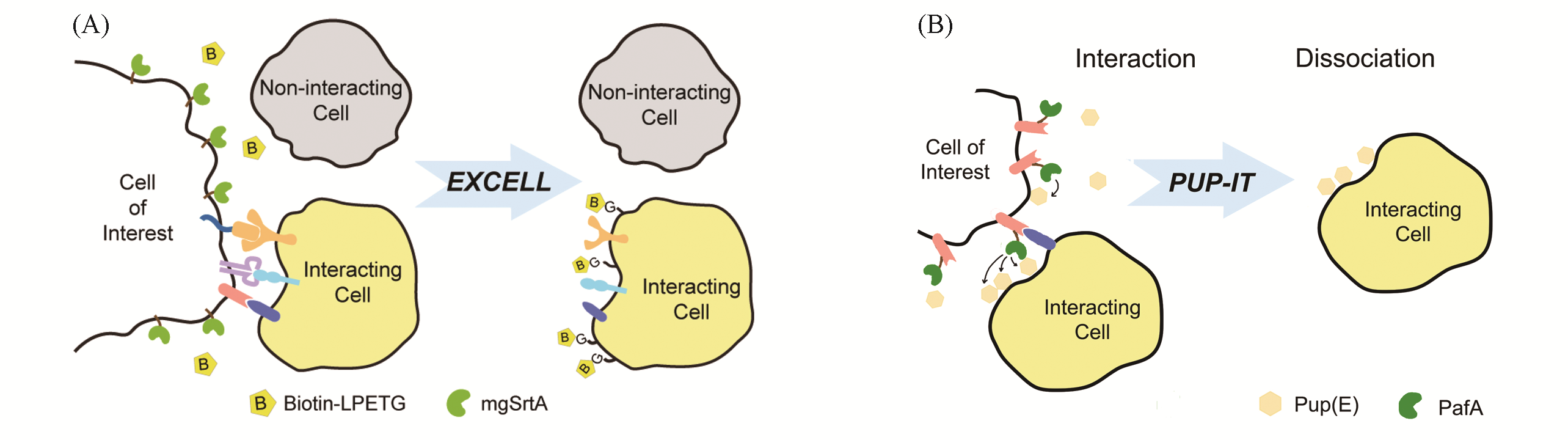
Fig.4 Trans?cellular labeling with sortase and PafA(A) Schematic diagram of EXCELL[23]; (B) schematic diagram of the PUP?IT design. (A) Copyright 2019, American Chemical Society.
| 1 | Cahalan M. D., Parker I., Annu. Rev. Immunol.,2008, 26(1), 585—626 |
| 2 | Konry T., Sarkar S., Sabhachandani P., Cohen N., Annu. Rev. Biomed. Eng.,2016, 18(1), 259—284 |
| 3 | Feng M., Jiang W., Kim B. Y. S., Zhang C. C., Fu Y. X., Weissman I. L., Nat. Rev. Cancer,2019, 19(10), 568—586 |
| 4 | Patel S. A., Minn A. J., Immunity,2018, 48(3), 417—433 |
| 5 | Weissleder R., Pittet M. J., Nat. Biomed. Eng.,2020, 4(5), 489—498 |
| 6 | Joglekar A. V., Leonard M. T., Jeppson J. D., Swift M., Li G., Wong S., Peng S., Zaretsky J. M., Heath J. R., Ribas A., Bethune M. T., Baltimore D., Nat. Methods,2019, 16(2), 191—198 |
| 7 | Li G., Bethune M. T., Wong S., Joglekar A. V., Leonard M. T., Wang J. K., Kim J. T., Cheng D., Peng S., Zaretsky J. M., Su Y., Luo Y., Heath J. R., Ribas A., Witte O. N., Baltimore D., Nat. Methods,2019, 16(2), 183—190 |
| 8 | Klichinsky M., Ruella M., Shestova O., Lu X. M., Best A., Zeeman M., Schmierer M., Gabrusiewicz K., Anderson N. R., Petty N. E., Cummins K. D., Shen F., Shan X., Veliz K., Blouch K., Yashiro⁃Ohtani Y., Kenderian S. S., Kim M. Y., O'Connor R. S., Wallace S. R., Kozlowski M. S., Marchione D. M., Shestov M., Garcia B. A., June C. H., Gill S., Nat. Biotechnol.,2020, 38, 947—953 |
| 9 | Hung C. F., Xu X., Li L., Ma Y., Jin Q., Viley A., Allen C., Natarajan P., Shivakumar R., Peshwa M. V., Emens L. A., Hum. Gene Ther.,2018, 29(5), 614—625 |
| 10 | Popescu D. M., Botting R. A., Stephenson E., Green K., Webb S., Jardine L., Calderbank E. F., Polanski K., Goh I., Efremova M., Acres M., Maunder D., Vegh P., Gitton Y., Park J. E., Vento⁃Tormo R., Miao Z., Dixon D., Rowell R., McDonald D., Fletcher J., Poyner E., Reynolds G., Mather M., Moldovan C., Mamanova L., Greig F., Young M. D., Meyer K. B., Lisgo S., Bacardit J., Fuller A., Millar B., Innes B., Lindsay S., Stubbington M. J. T., Kowalczyk M. S., Li B., Ashenberg O., Tabaka M., Dionne D., Tickle T. L., Slyper M., Rozenblatt⁃Rosen O., Filby A., Carey P., Villani A. C., Roy A., Regev A., Chedotal A., Roberts I., Gottgens B., Behjati S., Laurenti E., Teichmann S. A., Haniffa M., Nature,2019, 574(7778), 365—371 |
| 11 | Satija R., Farrell J. A., Gennert D., Schier A. F., Regev A., Nat. Biotechnol.,2015, 33(5), 495—502 |
| 12 | Efremova M., Vento⁃Tormo M., Teichmann S. A., Vento⁃Tormo R., Nat. Protoc.,2020, 15(4), 1484—1506 |
| 13 | Gerner M. Y., Kastenmuller W., Ifrim I., Kabat J., Germain R. N., Immunity,2012, 37(2), 364—376 |
| 14 | Pittet M. J., Weissleder R., Cell,2011, 147(5), 983—991 |
| 15 | Chung K., Wallace J., Kim S. Y., Kalyanasundaram S., Andalman A. S., Davidson T. J., Mirzabekov J. J., Zalocusky K. A., Mattis J., Denisin A. K., Pak S., Bernstein H., Ramakrishnan C., Grosenick L., Gradinaru V., Deisseroth K., Nature,2013, 497(7449), 332—337 |
| 16 | Yun D. H., Park Y. G., Cho J. H., Kamentsky L., Evans N. B., Albanese A., Xie K., Swaney J., Sohn C. H., Tian Y., Zhang Q., Drummond G., Guan W., DiNapoli N., Choi H., Jung H. Y., Ruelas L., Feng G., Chung K., bioRxiv,2019, 660373 |
| 17 | Wang X., Allen W. E., Wright M. A., Sylwestrak E. L., Samusik N., Vesuna S., Evans K., Liu C., Ramakrishnan C., Liu J., Nolan G. P., Bava F. A., Deisseroth K., Science,2018, 361(6400), eaat5691 |
| 18 | Martell J. D., Yamagata M., Deerinck T. J., Phan S., Kwa C. G., Ellisman M. H., Sanes J. R., Ting A. Y., Nat. Biotechnol.,2016, 34(7), 774—780 |
| 19 | Cho K. F., Branon T. C., Rajeev S., Svinkina T., Udeshi N. D., Thoudam T., Kwak C., Rhee H. W., Lee I. K., Carr S. A., Ting A. Y., Proc. Natl. Acad. Sci. USA,2020, 117(22), 12143—12154 |
| 20 | Liu D. S., Loh K. H., Lam S. S., White K. A., Ting A. Y., PLoS One,2013, 8(2), e52823 |
| 21 | Thyagarajan A., Ting A. Y., Cell,2010, 143(3), 456—469 |
| 22 | Pasqual G., Chudnovskiy A., Tas J. M. J., Agudelo M., Schweitzer L. D., Cui A., Hacohen N., Victora G. D., Nature,2018, 553(7689), 496—500 |
| 23 | Ge Y., Chen L., Liu S., Zhao J., Zhang H., Chen P. R., J. Am. Chem. Soc.,2019, 141(5), 1833—1837 |
| 24 | Liu Q., Zheng J., Sun W., Huo Y., Zhang L., Hao P., Wang H., Zhuang M., Nat. Methods,2018, 15(9), 715—722 |
| 25 | Cassetta L., Pollard J. W., Nat. Rev. Drug Discov.,2018, 17(12), 887—904 |
| 26 | Joly E., Hudrisier D., Nat. Immunol.,2003, 4(9), 815 |
| 27 | Geri J. B., Oakley J. V., Reyes⁃Robles T., Wang T., McCarver S. J., White C. H., Rodriguez⁃Rivera F. P., Parker D. L. Jr., Hett E. C., Fadeyi O. O., Oslund R. C., MacMillan D. W. C., Science,2020, 367(6482), 1091—1097 |
| 28 | Han S., Li J., Ting A. Y., Curr. Opin. Neurobiol.,2018, 50, 17—23 |
| 29 | Branon T. C., Bosch J. A., Sanchez A. D., Udeshi N. D., Svinkina T., Carr S. A., Feldman J. L., Perrimon N., Ting A. Y., Nat. Biotechnol.,2018, 36(9), 880—887 |
| 30 | Slavoff S. A., Liu D. S., Cohen J. D., Ting A. Y., J. Am. Chem. Soc.,2011, 133(49), 19769—19776 |
| 31 | Lam S. S., Martell J. D., Kamer K. J., Deerinck T. J., Ellisman M. H., Mootha V. K., Ting A. Y., Nat. Methods,2015, 12(1), 51—54 |
| 32 | Li J., Han S., Li H., Udeshi N. D., Svinkina T., Mani D. R., Xu C., Guajardo R., Xie Q., Li T., Luginbuhl D. J., Wu B., McLaughlin C. N., Xie A., Kaewsapsak P., Quake S. R., Carr S. A., Ting A. Y., Luo L., Cell,2020, 180(2), 373—386 |
| 33 | Roux K. J., Kim D. I., Raida M., Burke B., J. Cell Biol.,2012, 196(6), 801—810 |
| 34 | Beckett D., Kovaleva E., Schatz P. J., Protein Sci.,1999, 8(4), 921—929 |
| 35 | Puthenveetil S., Liu D. S., White K. A., Thompson S., Ting A. Y., J. Am. Chem. Soc.,2009, 131(45), 16430—16438 |
| 36 | Popp M. W., Ploegh H. L., Angew. Chem. Int. Ed.,2011, 50(22), 5024—5032 |
| 37 | Weeks A. M., Wells J. A., Chem. Rev.,2020, 120(6), 3127—3160 |
| 38 | Bi X., Yin J., Nguyen G. K. T., Rao C., Halim N. B. A., Hemu X., Tam J. P., Liu C. F., Angew. Chem. Int. Ed.,2017, 56(27), 7822—7825 |
| 39 | Feinberg E. H., Vanhoven M. K., Bendesky A., Wang G., Fetter R. D., Shen K., Bargmann C. I., Neuron,2008, 57(3), 353—363 |
| 40 | Yamagata M., Sanes J. R., Front. Mol. Neurosci.,2012, 5(18), 1—9 |
| 41 | Swee L. K., Lourido S., Bell G. W., Ingram J. R., Ploegh H. L., ACS Chem. Biol.,2015, 10(2), 460—465 |
| 42 | Murray E., Cho J. H., Goodwin D., Ku T., Swaney J., Kim S. Y., Choi H., Park Y. G., Park J. Y., Hubbert A., McCue M., Vassallo S., Bakh N., Frosch M. P., Wedeen V. J., Seung H. S., Chung K., Cell,2015, 163(6), 1500—1514 |
| 43 | Han Y., Branon T. C., Martell J. D., Boassa D., Shechner D., Ellisman M. H., Ting A., ACS Chem. Biol.,2019, 14(4), 619—635 |
| 44 | Tang W., Liu D. R., Science,2018, 360(6385), eaap8992 |
| 45 | Hulton C. H., Costa E. A., Shah N. S., Quintanal⁃Villalonga A., Heller G., de Stanchina E., Rudin C. M., Poirier J. T., Nat. Cancer,2020, 1(3), 359—369 |
| 46 | Polstein L. R., Gersbach C. A., Nat. Chem. Biol.,2015, 11(3), 198—200 |
| 47 | Wang H., Wang R., Cai K., He H., Liu Y., Yen J., Wang Z., Xu M., Sun Y., Zhou X., Yin Q., Tang L., Dobrucki I. T., Dobrucki L. W., Chaney E. J., Boppart S. A., Fan T. M., Lezmi S., Chen X., Yin L., Cheng J., Nat. Chem. Biol.,2017, 13(4), 415—424 |
| 48 | Wang J., Liu Y., Liu Y., Zheng S., Wang X., Zhao J., Yang F., Zhang G., Wang C., Chen P. R., Nature,2019, 569(7757), 509—513 |
| 49 | Wang H., Sobral M. C., Zhang D. K. Y., Cartwright A. N., Li A. W., Dellacherie M. O., Tringides C. M., Koshy S. T., Wucherpfennig K. W., Mooney D. J., Nat. Mater.,2020 |
| 50 | Allen C. D., Okada T., Tang H. L., Cyster J. G., Science,2007, 315(5811), 528—531 |
| 51 | Schwickert T. A., Lindquist R. L., Shakhar G., Livshits G., Skokos D., Kosco⁃Vilbois M. H., Dustin M. L., Nussenzweig M. C., Nature,2007, 446(7131), 83—87 |
| 52 | Rothbauer M., Zirath H., Ertl P., Lab Chip,2018, 18(2), 249—270 |
| 53 | Giladi A., Cohen M., Medaglia C., Baran Y., Li B., Zada M., Bost P., Blecher⁃Gonen R., Salame T. M., Mayer J. U., David E., Ronchese F., Tanay A., Amit I., Nat. Biotechnol.,2020, 38(5), 629—637 |
| 54 | Zhang L., Li Z., Skrzypczynska K. M., Fang Q., Zhang W., O'Brien S. A., He Y., Wang L., Zhang Q., Kim A., Gao R., Orf J., Wang T., Sawant D., Kang J., Bhatt D., Lu D., Li C. M., Rapaport A. S., Perez K., Ye Y., Wang S., Hu X., Ren X., Ouyang W., Shen Z., Egen J. G., Zhang Z., Yu X., Cell,2020, 181(2), 442—459 |
| [1] | 陈娜, 秦颂兵, 张兵波, 张旭光, 周菊英, 涂彧. 靶向性纳米金探针对宫颈癌细胞的激光扫描共聚焦散射成像[J]. 高等学校化学学报, 2012, 33(05): 1041. |
| [2] | 刘峰君, 张兵波, 宋歌, 程英升. Gd3+与RGD共修饰量子点用于胰腺癌细胞的荧光及MR双模态成像[J]. 高等学校化学学报, 2012, 33(02): 378. |
| [3] | 杜明,赵镭,李朝睿,赵广华,胡小松 . 富硒灵芝中一种新含硒蛋白的纯化、性质及其自由基清除活性研究[J]. 高等学校化学学报, 2007, 28(1): 75. |
| [4] | 谷宇,,杜志游,郎秋蕾,陈集双,何农跃 . 基于RNA杂交的马铃薯纺锤块茎类病毒检测芯片[J]. 高等学校化学学报, 2006, 27(11): 2106. |
| [5] | 聂松, 陈平, 梁宋平. 表面等离子共振-质谱法对相互作用的生物分子在10-15mol水平的微量鉴定[J]. 高等学校化学学报, 2005, 26(1): 68. |
| [6] | 徐力, 李相鲁, 吴晓霞, 王华, 侯瑞珍, 黄宜兵, 张学忠. 一种新的玉米抗氧化肽的制备与结构表征[J]. 高等学校化学学报, 2004, 25(3): 466. |
| [7] | 刘正春, 贺全国, 肖鹏峰, 梁波, 何农跃, 陆祖宏. 聚氨酯分子印章的制备和表征[J]. 高等学校化学学报, 2002, 23(9): 1823. |
| [8] | 杨波, 泉多惠子, 张书圣. 脂肪酶催化作用下酰胺化反应的立体规则性研究[J]. 高等学校化学学报, 2001, 22(8): 1332. |
| 阅读次数 | ||||||
|
全文 |
|
|||||
|
摘要 |
|
|||||